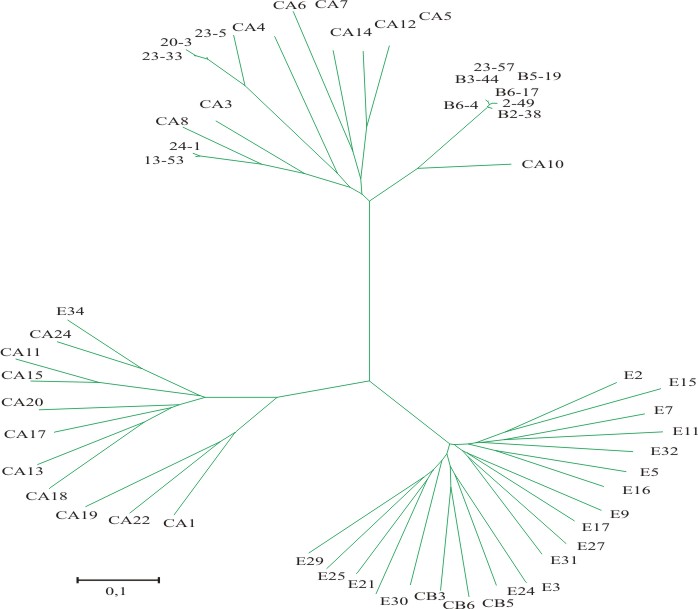
Fig. Árbol filogenético de la región VP1.
Instituto de Medicina Tropical "Pedro Kourí"
Dr. Julio Antonio Barrios Olivera,1 Lic. Luis Sarmiento Pérez,2 Lic. Odalys Valdés,3 Dr. Pedro Mas Lago4 y Téc. Rosa Palomera Puentes5
Se describió la introducción de un método molecular para la identificación de los Enterovirus basado en la amplificación, secuenciación y análisis filogenético de la proteína VP1. Se demostró que este método reduce grandemente el tiempo requerido para la identificación de los Enterovirus aislados y resulta de gran utilidad en la caracterización de aislamientos difíciles de tipificar, con el empleo de los reactivos inmunológicos de rutina. Por la rapidez de ejecución de la técnica reviste vital importancia su uso durante epidemias, dada la rápida determinación del agente causal.
DeCS: INFECCIONES POR ENTEROVIRUS; MODELOS MOLECULARES.
Los Enterovirus constituyen un gran género dentro de la familia Picornaviridae, se describen 64 serotipos antigénicos basados en los ensayos de neutralización. Al nivel mundial, más de 500 000 000 de personas se infectan cada año, resultando en cientos de miles los casos de enfermedad febril indiferenciada, rash, enfermedades gastrointestinales, meningitis aséptica, parálisis y enfermedad neonatal severa. Más recientemente, los Enterovirus han sido implicados en algunas enfermedades crónicas como la diabetes mellitus tipo 1 y la miocardiopatía dilatada.1
]]>
Muestra: se seleccionaron un total de 12 cepas de Enterovirus aisladas en el año 1998 en el Laboratorio Nacional de Referencia de Enterovirus, Instituto de Medicina Tropical "Pedro Kourí" (IPK), Cuba. Estas cepas procedían de niños sanos, ninguna de las cuales pudo ser identificada por la prueba de neutralización con el empleo de la mezcla de Lim-Benyesh-Melnick (LBM).
Extracción de ácido ribonucleico (ARN): para la obtención del ARN viral de la muestra se utilizó el método del TRIZOL LS Reagent comercial (BRL Life Technologies) según las instrucciones del fabricante.
Síntesis del ácido dexosirribonucleico complementario (ADNc): la síntesis del ADNc se realizó con cebadores al azar, con la utilización del estuche comercial de preamplificación ThermoScript (Gibco BRL, Life Technologies). ]]>
Tabla 1. Secuencia nucleotídica y posición en el genoma de los cebadores empleados para la amplificación y secuenciación de VP1
| Primer | Secuencia | Gen | Posición nucleotídica a |
| 011 | GCICCIGAYTGITGICCRAA | ]]> 2A | 3408-3389 |
| 012 | ATGTAYGTICCICCIGGIGG | VP1 | 2951-2970 |
| 040 | ATGTAYRTICCIMCIGGIGC | VP1 | 2951-2970 |
Para la detección del producto amplificado se analizaron 10 µL de cada tubo de reacción en una electroforesis en gel de agarosa 2 % en tampón TBE (Tris-Borato 0,09M, EDTA 2 mM, pH 8). En cada corrida se incluyó el patrón de peso molecular FX174 RF DNA/Hae III Fragments (Gibco BRL, Life Technologies). La coloración de los geles se realizó con una solución de bromuro de etidio a una concentración final de 0,1-0,2 µg/mL, y se visualizaron las bandas de amplificación en un transiluminador de luz ultravioleta (LKB).
Purificación del producto de la RCP: el producto de la RCP se purificó para su posterior secuenciación mediante la utilización del estuche comercial QIAquick (QIAGEN, Santa Clarita, CA).
Secuenciación: se realizó secuenciación manual mediante el método de terminación de la cadena empleando el estuche comercial Thermo Sequenase Radiolabeled Terminator Cycle Sequencing (USB).
Determinación del serotipo: se determinó por comparación de la secuencia amplificada de VP1 con las secuencias de todos los Enterovirus humanos y otros Picornavirus, publicadas en la base de datos GenBank. Se consideró que más de 75 % de homología en la secuencia nucleotídica (88 % en la secuencia aminoacídica) era indicativo de cepas de un mismo serotipo, según lo descrito por Oberste y otros.5
]]>
Amplificación de ácidos nucleicos
La secuencia nucleotídica de la proteína VP1 de los Enterovirus parece estar correlacionada con los serotipos enterovirales. Esta proteína presenta una gran variabilidad, por lo que resulta imposible la amplificación de esta parte del genoma en todos los Enterovirus, con el uso de un solo juego de cebadores. En este trabajo, cuando se emplearon los cebadores 011-012, no se obtuvo la amplificación en ninguna de las cepas del estudio. Con el empleo de los primer 011-040 se obtuvo un producto de 457 pb en las 12 cepas estudiadas.
Tipificación molecular basada en el análisis de la región VP1
Las secuencias de la región VP1 de las cepas estudiadas se compararon con todas las secuencias de Enterovirus publicadas en Genbank, encontrándose en todas entre 78 a 86 % de homología nucleotídica y más de 95 % de homología aminoacídica con algún serotipo de Enterovirus (tabla 2). Esto permitió identificar 3 cepas de Coxsackie A4, 2 Coxsackie A8 (CA8) y 7 Coxsackie A10 (CA10). En la figura se muestra el análisis filogenético de las cepas estudiadas. Como puede observarse, todas se agrupan en correspondencia con el serotipo al cual pertenecen.
Tabla 2. Porcentaje de identidad nucleotídica y aminoacídica de las cepas estudiadas
| ]]> Cepas | Serotipo identificado | Identidad nucleotídica (%) | Identidad aminoacídica (%) |
| 2-49 | CA10 | 78 | 96 |
| 13-53 | CA8 | ]]> 82 | 96 |
| 20-3 | CA4 | 86 | 95 |
| 23-5 | CA4 | 85 | 97 |
| ]]> 23-33 | CA4 | 86 | 97 |
| 23-57 | CA10 | 79 | 96 |
| 24-1 | CA8 | ]]> 81 | 96 |
| B2-38 | CA10 | 78 | 96 |
| B3-44 | CA10 | 79 | 96 |
| ]]> B5-19 | CA10 | 78 | 96 |
| B6-4 | CA10 | 78 | 96 |
| B6-17 | CA10 | ]]> 79 | 96 |

Fig. Árbol filogenético de la región VP1.
]]> Remicroneutralización
Después de conocer el serotipo viral mediante el análisis filogenético de la región VP1, se procedió a su confirmación empleando las mezclas de J-P de LBM. Hubo una correspondencia entre los serotipos identificados por ambas técnicas.
El estudio de la región 5' no codificante (5'NTR) de los Enterovirus mediante métodos moleculares, permite la rápida y específica detección de todos los miembros de este género viral.9 Sin embargo, por la gran variabilidad que presenta esta región dentro de un mismo serotipo no resulta útil para la identificación de los diferentes serotipos.10-12
Otros estudios filogenéticos sugirieron que el empleo de la región de unión entre las proteínas VP4-VP2 para la identificación de los distintos serotipos podía ser de más utilidad que la región 5'NTR, sin embargo, no obtuvieron resultados favorables para todos los serotipos virales.13-15
La región de unión entre VP1 y 2A ha sido ampliamente usada en los estudios de patrones de transmisión de los Poliovirus y se ha podido comprobar que las secuencias de VP1 de estos virus se agrupan en correspondencia con los serotipos homólogos.16
Los serotipos de los Enterovirus están bien definidos sobre la base de la neutralización. En la proteína VP1 se encuentran ubicados los epítopes neutralizantes de mayor importancia.17,18 Recientemente Oberste y otros describieron que la secuencia de la proteína VP1 contiene la información específica de serotipo de todos los Enterovirus. Esto ha permitido el desarrollo de métodos moleculares para la identificación, tanto de los serotipos tradicionales de los Enterovirus como el descubrimiento de otros nuevos.19 ]]>
The introduction of a mollecular method to identify the Entoviruses based on the amplification, sequencing and phylogenetic analysis of protein VP1 was described. It was proved that this method reduces significantly the time required for the identification of the isolated Entoviruses and that it is very useful in the characterization of isolates which are difficult to typify by the routine immunoloigical reagents. As it is a very fast technqiue, its use is very important during epidemics to determine the causal agent rapidly.
]]>
Recibido: 2 de junio de 2003. Aprobado: 9 de julio de 2003.
Dr. Julio Antonio Barrios Olivera. Instituto de Medicina Tropical "Pedro Kourí". Apartado 601, Marianao 13, Ciudad de La Habana, Cuba. Correo electrónico: ciipk@ipk.sld.cu
1 Máster en Virología. Especialista de I Grado en Microbiología.
2 Máster en Virología. Licenciado en Microbiología. Aspirante a Investigador.
3 Máster en Virología. Licenciada en Microbiología. Investigadora Agregada. ]]>
4 Doctor en Ciencias Médicas. Especialista de II Grado en Microbiología. Investigador de Mérito.
5 Técnico en Microbiología.