Instituto de Medicina Tropical Pedro Kourí
Instituto de Salud Carlos III, España
Lic. Odalys Valdés Ramírez,1 Lic. Clara Savón,2 Dr. Ángel Goyenechea,3 Dr. Ángel Valdivia,4 Lic. Grehete González,5 Lic. Lídice Palerm6 y Lic. José A. Melero7
Se realizó la secuenciación nucleotídica de la región del tercio C-terminal de la proteína G de 37 muestras de exudados nasofaríngeos, de niños menores de 1 año provenientes de algunas provincias de Cuba durante 5 períodos epidémicos (1995-2000), para conocer los patrones de circulación de cepas del virus sincitial respiratorio humano; el cual se clasifica en 2 subgrupos antigénicos A y B, y cada uno contiene múltiples variantes. El subgrupo A circuló durante todos los años, el subgrupo B se detectó solamente durante el año 2000. Dentro del subgrupo A se observó la presencia de cepas con 2 tamaños diferentes de la proteína G (297 aa y 298 aa), mientras que para el subgrupo B fue observado un único tamaño (295 aa). El análisis filogenético permitió identificar 5 y 2 genotipos dentro de los subgrupos A y B, respectivamente. Los virus de Cuba se relacionaron filogenéticamente con cepas de otras partes del mundo. Dentro del subgrupo A se encontraron 2 cepas, las cuales fueron muy similares a la cepa prototipo Long. Casi todas las cepas del año 2000 de ambos subgrupos, se agruparon filogenéticamente con cepas que circularon en Sudáfrica durante ese mismo período.
Palabras clave: Virus sincitial respiratorio humano (VSRH), secuenciación nucleotídica de la región del tercio C-terminal de la proteína G, subgrupos antigénicos A y B.
El virus sincitial respiratorio humano (VSRH) es la causa principal de infección del tracto respiratorio bajo en lactantes y niños pequeños.1-4 Este virus también ha sido reconocido como un agente etiológico importante que produce neumonía en pacientes inmunodeprimidos y en ancianos.5-7 Los aislamientos de VSRH se clasifican en 2 subgrupos antigénicos A y B sobre la base de su reactividad frente a un panel de anticuerpos monoclonales. Por análisis de secuencia se demostró que constituyen grupos genéticamente diferentes.8-11 La existencia de distintos linajes dentro de cada subgrupo ha sido demostrada al nivel antigénico y genético.9-11 La proteína G resultó ser la más divergente entre y dentro de cada subgrupo.12 La acumulación de cambios aminoacídicos en el tiempo sugiere que la evolución de esta proteína está bajo presión selectiva.9 El conocimiento sobre la epidemiología molecular del VSRH se ha basado fundamentalmente en estudios realizados en países desarrollados con climas templados.13 Muy pocos estudios han sido realizados en países subdesarrollados y tropicales, donde la infección con VSRH podría seguir un patrón diferente.14 En este reporte se examinaron diferentes patrones de circulación de los subgrupos A y B del VSRH en diferentes provincias de Cuba durante 5 períodos epidémicos.
Muestras clínicas: las muestras seleccionadas para el estudio fueron exudados nasofaríngeos de niños menores de 2 años con infección respiratoria aguda baja, provenientes de diferentes hospitales de Cuba desde 1995 hasta el año 2000. Todos los exudados nasofaríngeos fueron colectados en tubos con tapa de rosca que contenían 4 mL de medio de transporte (Hanks-lactoalbumin con penicilina G 200 U/mL, estreptomicina 200 g/mL y anfotericina B 5µg/mL), transportados a 4 ºC y conservados a - 70 ºC. Las muestras examinadas se muestran en la tabla 1. La nomenclatura empleada indica: el lugar de procedencia, el número asignado al virus y el año en que fue tomada la muestra.
]]> Tabla 1. Nomenclatura y procedencia de los aislamientos usados en este estudio| Nombre | Año de aislamiento | Origen | Nombre | Año de aislamiento | Origen |
| ]]> Hol/167/95 | 1995 | Holguín | CHab/236/98 | 1998 | C. Habana |
| Hol/168/95 | 1995 | Holguín | CHab/237/98 | ]]> 1998 | C. Habana |
| CHab/91/97 | 1997 | C. Habana | CHab/239/98 | 1998 | C. Habana |
| Tun/135/97 | 1997 | ]]> Las Tunas | CHab/240/98 | 1998 | C. Habana |
| Tun/141/97 | 1997 | Las Tunas | Tun/244/98 | 1998 | Las Tunas |
| ]]> Tun/145/97 | 1997 | Las Tunas | Tun/245/98 | 1998 | Las Tunas |
| CHab/102/97 | 1997 | C. Habana | SC/93/99 | ]]> 1999 | Santiago de Cuba |
| CHab/123/97 | 1997 | C. Habana | SC/94/99 | 1999 | Santiago de Cuba |
| CHab/114/98 | 1998 | ]]> C. Habana | CHab/33/00 | 2000 | C. Habana |
| CHab125/98 | 1998 | C. Habana | CHab/34/00 | 2000 | C. Habana |
| ]]> CHab/181/98 | 1998 | C. Habana | CHab/37/00 | 2000 | C. Habana |
| CHab/185/98 | 1998 | C. Habana | CHab/42/00 | ]]> 2000 | C. Habana |
| CHab/197/98 | 1998 | C. Habana | CHab/43/00 | 2000 | C. Habana |
| CHab/198/98 | 1998 | ]]> C. Habana | Tun/50/00 | 2000 | Las Tunas |
| CHab/223/98 | 1998 | C. Habana | Tun/53/00 | 2000 | Las Tunas |
| ]]> Cfgos/226/98 | 1998 | Cienfuegos | Tun/57/00 | 2000 | Las Tunas |
| Cfgos/227/98 | 1998 | Cienfuegos | SS/64/00 | ]]> 2000 | Sancti Spíritus |
| Cfgos/228/98 | 1998 | Cienfuegos | SS/65/00 | 2000 | Sancti Spíritus |
| Cfgos/232/98 | 1998 | ]]> Cienfuegos |
Extracción de ARN: se realizó la extracción de ARN viral directamente de la muestra clínica. Se tomó un volumen inicial de 500 mL. Las muestras se centrifugaron a 12 000 rpm durante 15 min a 4 °C y el sobrenadante de cada una fue eliminado, el precipitado fue resuspendido en 500 mL de trizol (Gibco); seguido de una incubación durante 5 min a temperatura ambiente (TA). Posteriormente se añadieron 100 mL de cloroformo (mezclar por vortex), se incubó 3 min a TA, se centrifugó en igualdad de condiciones y se transfirió la fase superior a otro tubo eppendorf. Posteriormente se añadieron 400 mL de isopropanol, se mezcló mediante agitación manual y se incubó durante 10 min a TA; la mezcla se centrifugó durante 15 min bajo las mismas condiciones mencionadas anteriormente. El ARN se lavó con 500 mL de etanol 75 % (SIGMA), la centrifugación se realizó durante 15 min en igualdad de condiciones, el sobrenadante fue eliminado, el ARN se secó en el flujo y fue resuspendido en 30 mL de agua estéril libre de RNasa.
Transcripción reversa y reacción en cadena de la polemizara (RT-RCP, siglas en inglés): para la RT-PCR se utilizó el kit RT-PCR Access System (Promega). Para esto se añadieron a la mezcla de reacción 10 mL del ARN extraído. En la mezcla se emplearon 10 mL de AMV/Tfl 5X, 1 mL AMV RT (5 U/mL), 1 mL de Tfl DNA polimerasa (5 U/mL), 6 mL de MgSO4 (25 mM), 1 mL de dNTP (10 mM), 1 mL de cada oligonucleótido (100 ng) y se completó con agua bidestilada estéril para un volumen final de 50 mL. La mezcla de reacción para la RT-PCR se colocó en un termociclador (MJ Research, PTC 150) utilizando el programa siguiente: 30 min a 42 ºC, seguido de 5 min a 94 ºC, y 30 ciclos de desnaturalización a 94 ºC durante 30 s, de hibridación a 55 ºC durante 30 s y de extensión a 72 ºC durante 30 s, con una extensión final de 72 ºC por 5 min. Para la RT-PCR se utilizaron los oligonucleótidos G(+) 5GGGGCAAATGCAAACATGTC (posición nucleotídica 1-20), y G(-) 5TTTGCTAACTGCACTGCATGT (posición nucleotídica 1097-1117).
PCR semi-anidada: para la segunda amplificación se añadieron 2 mL de la primera PCR a la mezcla de reacción constituida por 0,25 mL de AmpliTaq Polimerasa (5 U/mL) (Perkin Elmer), 5 mL de buffer PCR (10X) (Perkin Elmer), 6 mL MgCl2 (2 mM) (Perkin Elmer), 0,8 mL de dNTP (25 mM) (Perkin Elmer), 1 mL de cada oligonucleótido (100 ng) y agua bidestilada estéril para un volumen final de 50 mL. La mezcla de la PCR anidada se colocó en el mismo termociclador mencionado anteriormente y el programa utilizado fue el siguiente: 3 min a 94 °C seguido de 30 ciclos de desnaturalización a 94 °C durante 30 s, de hibridación a 55 °C durante 30 s y de extensión a 72 °C durante 30 s, con una extensión final de 72 °C por 5 min. Para la PCR semi-anidada se utilizó uno de los oligonucleótidos utilizados en la RT-PCR, el G(-) 5TTTGCTAACTGCACTGCATGT (posición nucleotídica 1097-1117) y 2 oligonucleótidos internos para el subgrupo A y B, el GA (+) 5GCAGCATATGCAGCAACA (posición nucleotídica 533-551) y el GB (-) 5GATGATTACCATTTTGAAGTGTTCA (posición nucleotídica 496-521). Todos los oligonucleótidos fueron donados gentilmente por el doctor José A. Melero y la doctora Pilar Pérez Breña del Instituto de Salud Carlos III, Madrid, España.
Secuenciación nucleotídica: los productos de la PCR fueron purificados utilizando el kit QIAquick de purificación de PCR (Qiagen). Ambas cadenas fueron secuenciadas automáticamente usando el kit fluorescente dye-labeled terminators en ABI 373 a7 Sequencer models (Perkin-Elmer Applied Biosystems).
Análisis de los datos: los datos de cada una de las secuencias fueron primeramente analizados con el software Chromas (versión 1.3; C. McCarthy, 1996, Griffith University, Brisbape, Queensland, Australia). Los datos de secuencia de la cadena positiva y negativa de cada una de las muestras secuenciadas fueron empalmados usando el programa MegAlign (DNASTAR, software, Madison, Wis) para obtener las secuencias consenso finales. Las secuencias nucleotídicas y aminoacídicas del subgrupo A y B del VSRH fueron alineadas separadamente utilizando el Clustal X 1.64b (Thompson y otros, 1997). El análisis filogenético fue realizado con el MEGA (versión 2.1). Un total de 31 secuencias de VSRH fueron obtenidas de la base de datos del GenBank. Los nombres de las cepas se muestran en la tabla 2.
Tabla 2. Nomenclatura, procedencia y clasificación en subgrupos de las cepas utilizadas en el estudio obtenidas de la base de datos del Gen Bank
| Cepa | ]]> Sub-grupo | Año de aislamiento | País | Cepa | Sub-grupo | Año de aislamiento | País |
| Long | ]]> A | 1956 | EE. UU. | NY103 | A | 1994-95 | EE. UU. |
| A2 | A | 1961 | ]]> Australia | TX68532 | A | 1994-95 | EE. UU. |
| WV2780 | A | 1979 | EE. UU. | AL19376 | ]]> A | 1994-95 | EE. UU. |
| WV19983 | A | 1987 | EE. UU. | MO01 | A | 1994-95 | ]]> EE. UU. |
| Mon/2/88 | A | 1988 | Uruguay | Moz169/99 | A | 1999 | Mozambique |
| Mon/3/88 | ]]> A | 1988 | Uruguay | AgA48-99 | A | 1999 | Sudáfrica |
| RSB89-1734 | A | 1989 | ]]> Reino Unido | SA00J81 | A | 2000 | Sudáfrica |
| RSB89-642 | A | 1989 | Reino Unido | SA0003 | ]]> A | 2000 | Sudáfrica |
| Mon5/90 | A | 1990 | Uruguay | AgK23-00 | A | 2000 | ]]> Sudáfrica |
| Mon1/90 | A | 1990 | Uruguay | AgK28-00 | A | 2000 | Sudáfrica |
| Mad4/90 | ]]> A | 1990 | España | SA97D1289 | A | 1997 | Sudáfrica |
| Mon4/90 | A | 1990 | ]]> Uruguay | Su8/60 | B | 1960 | Suiza |
| Mon5/91 | A | 1991 | Uruguay | CH18537 | ]]> B | 1962 | EE. UU. |
| Mon7/91 | A | 1991 | Uruguay | Ab3064C01 | B | 2001 | ]]> Sudáfrica |
| Mad6/93 | A | 1993 | España | SA0025 | B | 2000 | Sudáfrica |
| CH 57 | ]]> A | 1990-95 | EE. UU. |
En este análisis fueron incluidas secuencias de 7 cepas aisladas en Ciudad de La Habana, no relacionadas con los 5 períodos epidémicos estudiados.15 Los nombres de estas cepas se muestran en la tabla 3.
Tabla 3. Nomenclatura y procedencia de 7 cepas no relacionadas con el estudio
| Nombre | Año de aislamiento | ]]> Origen |
| CHab/52/94 | 1994 | C. Habana |
| CHab/140/94 | 1994 | C. Habana |
| CHab/5/95 | 1995 | C. Habana |
| ]]> CHab/11/95 | 1995 | C. Habana |
| CHab/104/96 | 1996 | C. Habana |
| CHab/195/96 | 1996 | C. Habana |
| CHab/220/96 | ]]> 1996 | C. Habana |
Se realizó la secuenciación nucleotídica del tercio C-terminal del gen de la proteína G (394 nucleótidos, que corresponde al codón en la posición 185 hasta la posición 298 para la cepa prototipo Long y 292 para la cepa prototipo CH18537) de 37 muestras clínicas obtenidas durante 5 períodos epidémicos (1995-2000) de algunas provincias del país. De estas muestras clínicas positivas a VSRH por PCR, 31 pertenecieron al subgrupo antigénico A y 6 al subgrupo B, la identificación de cada subgrupo se realizó por secuenciación nucleotídica. El subgrupo antigénico A se detectó durante todos los años, el subgrupo B se detectó solamente en el año 2000.
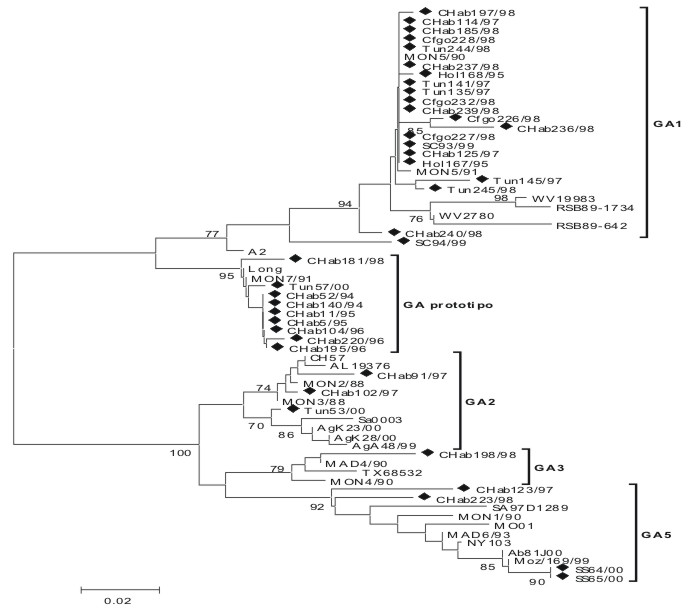
Las secuencias obtenidas fueron comparadas filogenéticamente con secuencias publicadas en el GenBank. Cuando se analizaron las secuencias de los subgrupos A y B en su conjunto, fueron observados 2 subgrupos muy bien definidos. Para facilitar esta comparación, las secuencias de ambos subgrupos se analizaron en forma separada. Los subgrupos A y B fueron genotipados por comparación filogenética con secuencias que habían sido antes asignadas a un genotipo determinado16-18 y por comparación con secuencias de otras regiones geográficas (figs. 1 y 2). Los aislamientos cubanos del subgrupo A se agruparon filogenéticamente en 3 líneas evolutivas principales con un nivel de confianza muy significativo (bootstrap 94-100 %).
Fig. 1. Análisis filogenético de cepas de VSRH del subgrupo A aisladas en Cuba y en diferentes localidades geográficas. Los virus de Cuba son señalizados con un triángulo negro.
Fig. 2. Análisis filogenético de cepas de VSRH del subgrupo B aisladas en Cuba y en diferentes localidades geográficas. Los virus de Cuba son señalizados con un triángulo negro.
]]> La mayoría de los aislamientos de Cuba se agruparon en la rama superior del árbol, donde aparecen cepas de casi todas las provincias estudiadas que circularon durante los años 1995-1999. Dentro de este grupo se observaron secuencias idénticas o casi idénticas. Los aislamientos de esta rama se agruparon filogenéticamente con virus pertenecientes al genotipo GA 1, en este grupo se encontraron cepas que circularon en Uruguay, EE. UU. y Reino Unido, varios años atrás. La cepa SC94/99 se ubicó fuera del genotipo GA 1.Se agruparon 2 aislamientos (CHab181/98 y Tun57/00) en la misma rama de la cepa prototipo Long. Dentro de este grupo se incluyeron 3 cepas representativas de brotes epidémicos ocurridos en Ciudad de La Habana durante los años 1994-1996 y una cepa de Uruguay. En la región secuenciada de la cepa CH181/98 se encontraron solamente 3 nucleótidos diferentes (posición 677, 741 y 818); de estos, solo se observó un cambio aminoacídico, L252V (cambios en las posiciones 677 y 818 fueron silentes). En la cepa Tun57/00 se encontraron 6 nucleótidos diferentes (posiciones 567, 597, 621, 624, 637 802), con un solo cambio al nivel de aminoácido (267 S-L), los cambios en las posiciones restantes también fueron silentes.
La rama inferior se dividió a su vez en 3 ramas secundarias también con un nivel estadístico altamente significativo (bootstrap 67-92 %), los aislamientos cubanos de cada una de las ramas secundarias se agruparon filogenéticamente con cepas pertenecientes a los genotipos GA 2, GA 3 y GA 5. El genotipo GA 2 estaba compuesto por cepas que circularon en diferentes períodos de tiempo en Sudáfrica, Montevideo y Norteamérica. Dentro de este se agruparon 2 cepas de Ciudad de La Habana que circularon durante 1997 y una cepa de Las Tunas del año 2000. Las cepas cubanas de 1997 estaban más estrechamente relacionadas con los aislamientos de Norteamérica y Montevideo que circularon en años diferentes. La cepa del año 2000 se agrupó muy cercanamente con cepas que circularon en Sudáfrica durante el mismo período de tiempo. La cepa CHab198/98 se agrupó dentro del genotipo GA 3 con cepas de Montevideo, Madrid y EE. UU. que circularon en tiempos diferentes.
Dentro del genotipo GA 5 se agruparon 2 cepas de Ciudad de La Habana que circularon durante 1997 y 1998, y 2 cepas de Sancti Spíritus del año 2000. En esta rama se agruparon virus que circularon durante un mismo período de tiempo en áreas geográficas distantes y cepas que circularon en períodos de tiempo y áreas geográficas diferentes. Las cepas de Sancti Spíritus presentaron la misma secuencia nucleotídica y estaban muy relacionadas con cepas de Sudáfrica y de Mozambique que circularon durante el mismo período epidémico.
Los aislamientos cubanos del subgrupo B se agruparon filogenéticamente en 2 ramas diferentes con un valor de bootstrap de 82-100 %. Casi todos los aislamientos cubanos se agruparon dentro del genotipo cluster SAB 1. Dentro de este genotipo 2 aislamientos presentaron la misma secuencia nucleotídica (CHab37/00 y CHab42/00). Las cepas CHab34/00, Tun50/00 y CHab43/00 se diferenciaron de las anteriores en 1 ó 2 nucleótidos. Todas las cepas del subgrupo B se agruparon filogenéticamente con cepas de Sudáfrica que circularon durante ese mismo período de tiempo.
El análisis de la secuencia aminoacídica de los aislamientos cubanos del grupo A mostró la presencia de cepas con 2 tamaños diferentes de la proteína G (297 aa y 298 aa). En todos los casos el codón de parada fue UAG (fig. 3). Para el subgrupo B se observó en todas las cepas un único tamaño para la proteína G (295aa) con 2 codones diferentes de parada UAG y UAA (fig. 4).
Fig. 3. Alineamiento múltiple de las secuencias de aminoácidos de cepas de VSRH del subgrupo A que circularon en Cuba durante 1994-2000. Se indican los cambios de aminoácidos respecto a la secuencia Long.
Fig. 4. Alineamiento múltiple de las secuencias de aminoácidos de cepas de VSRH del subgrupo B que circularon en Cuba durante el año 2000. Se indican los cambios de aminoácidos respecto a la secuencia CH18537.
]]>El análisis filogenético basado en las secuencias nucleotídicas o aminoacídicas mostró que el subgrupo A evolucionó con múltiples linajes. Los aislamientos cubanos pertenecientes al genotipo GA 1 se agruparon filogenéticamente con virus de Uruguay, EE. UU. y Reino Unido aislados varios años atrás. Resultados similares fueron encontrados en otras partes del mundo. Virus aislados en Gambia durante 1993 fueron muy similares a virus aislados en Madrid 10 años antes.19 Estudios realizados en Dinamarca durante varias epidemias consecutivas encontraron virus cuyos patrones de restricción fueron similares a virus aislados hace más de 20 años en Australia y EE. UU.20,21 Estos autores han sugerido, que las fluctuaciones temporales de un genotipo predominante podrían estar dadas más por el estado inmunológico del hospedero que favorece a determinadas cepas dentro de la población circulante, que por la evolución molecular inducida por la presión inmune selectiva. Ellos además plantean que determinados genotipos los cuales no han sido reconocidos durante varios inviernos, podrían mantenerse endémicos en una población durante años y manifestarse ocasionalmente.
El genotipo GA 1 circuló en casi todas las provincias estudiadas y se mantuvo circulando durante 4 años (1995-1999). Cepas con idénticas secuencias fueron vistas en varias comunidades durante un mismo período epidémico y en una misma comunidad durante 3 períodos epidémicos en EE. UU.16,17
Un alto grado de identidad fue observado entre 2 aislamientos cubanos y la cepa prototipo Long. Resultados similares fueron encontrados en años anteriores durante 3 epidemias consecutivas ocurridas en Ciudad de La Habana.15 En Dinamarca durante 2 períodos epidémicos el genotipo predominante mostró un patrón de restricción idéntico a la cepa A2 aislada en 1961.20
Las cepas pertenecientes a la rama inferior se agruparon a su vez en múltiples genotipos GA 2, GA 3 y GA 5. En esta rama se agruparon virus que circularon durante un mismo período de tiempo en áreas geográficas distantes. Por ejemplo 2 cepas de Sancti Spíritus y una de Las Tunas del año 2000 estaban muy estrechamente relacionadas con cepas que circularon durante ese mismo período en Sudáfrica y Mozambique. Diferentes autores han identificado que virus muy similares están presentes simultáneamente en áreas geográficas muy distantes.22 Dentro de esta rama también se agruparon cepas que circularon en tiempos diferentes en otras áreas geográficas. Los diferentes genotipos de VSRH tienen una distribución mundial y se ha visto que virus aislados en lugares distantes y en tiempos diferentes pueden estar más relacionados que virus aislados en un mismo lugar durante una misma epidemia.13
En general, se ha visto que los aislamientos del subgrupo A son más frecuentes que los del subgrupo B. En este estudio se detectó durante el año 2000 la circulación de virus perteneciente al subgrupo B. Las cepas de este subgrupo se agruparon filogenéticamente en 2 genotipos diferentes. A diferencia de lo ocurrido en el subgrupo A, los aislamientos de este grupo se agruparon muy distantes de las cepas prototipos (CH18537 y Su8/60) y del resto de las cepas antiguas. Los aislamientos cubanos pertenecientes a ambos genotipos se agruparon con virus que circularon durante ese mismo período de tiempo en Sudáfrica. Esta elevada similitud con las cepas del continente africano, pudiera estar muy relacionada con el incremento del intercambio de viajeros cubanos a este continente a finales de la década de los años 90. No obstante, durante ese año se detectó una cepa cuya secuencia nucleotídica fue similar a la de la cepa Long, es decir, a pesar de que nuevas variantes se han introducido en Cuba, genotipos antiguos continúan circulando a bajos niveles.
Han sido descritas diferentes longitudes para la proteína G de ambos subgrupos.23,24 En este estudio todas las secuencias cubanas pertenecientes al subgrupo B presentaron una proteína de 295 aa con 2 codones diferentes de parada (UAG y UAA). Sin embargo, dentro de las cepas del grupo A se observaron 2 tamaños de proteína (297 aa y 298 aa) con un solo codón de parada (UAG). Los cambios en el codón de parada han sido asociados con importantes variaciones antigénicas encontradas en mutantes de escape en VSRH, los cuales fueron seleccionados con anticuerpos monoclonales que reconocen epítopes específicos de cepas.13 El análisis filogenético mostró que existe una correlación entre la posición del virus en el árbol y el tamaño de su proteína G. Resultados similares fueron encontrados por otros autores.23-25
Haciendo un análisis del patrón epidemiológico descrito para el VSRH y comparándolo con los resultados en este trabajo, se puede apreciar que los aislamientos cubanos poseen características singulares: Hasta el año 1999 solo se detectó la circulación de cepas pertenecientes al subgrupo A. La mayoría de los aislamientos analizados se agruparon con cepas que circularon varios años atrás, 2 de estos aislamientos fueron muy similares a Long. Cepas con secuencias muy similares circularon durante 4 años en casi todas las provincias. Por tanto, para los aislamientos cubanos pertenecientes al subgrupo A se observó poca variabilidad genética del tercio C-terminal del gen de la proteína G. Durante el año 2000 se detectó la circulación de ambos subgrupos. Casi todas las cepas que circularon durante el año 2000 se agruparon filogenéticamente con cepas de Sudáfrica del mismo período de tiempo. Todas las cepas analizadas del subgrupo B se agruparon muy distantes de las cepas antiguas.
De forma general, las epidemias de VSRH ocurren durante los meses de invierno en las regiones con clima templado13 y durante las estaciones de lluvias en las regiones con clima tropical.26 Hasta la fecha pocos han sido los estudios para conocer la epidemiología de este virus en países en vías de desarrollo y de clima tropical. En Cuba, a pesar de ser un país tropical, se ha visto que la circulación del VSRH ocurre durante los meses de invierno y puede extenderse hasta la primavera, con períodos cortos o largos interepidémicos.27 En este sentido se puede decir, que Cuba tiene condiciones climáticas, geográficas y socioeconómicas únicas, las cuales pudieran estar influyendo en la circulación y evolución del VSRH.
The nucleotide sequencing of the protein G C-terminal region of 37 samples taken from nasopharyngeal washings of under one-year old children from some Cuban provinces was made for 5 epidemic periods (1995-2000) to find out the circulation patterns of strains of human respiratory syncytial virus that is classified in two antigenic subgroups known as A and B; each of them contains multiple variants. Subgroup A has circulated during all these years but subgroup B was detected only in the year 2000. The presence of strains with two different sizes of protein G (297 aa and 298 aa) was observed whereas subgroup B showed only one size (295 aa). Phylogenetic analysis allowed identifying 5 and 2 genotypes within subgroups A and B respectively. Viruses present in Cuba were phylogenetically related to the strains of other parts of the world. Subgroup A comprised two strains very similar to Long prototype strain. Almost all the strains of both subgroups in the year 2000 phylogenetically related with strains that circulated in South Africa during the same period.
]]> Key words: Human respiratory syncytial virus, nucleotide sequencing of the protein G C-terminal, antigenic subgroups A and B.
Recibido: 2 de octubre de 2003. Aprobado: 16 de enero de 2004.
Lic. Odalys Valdés Ramírez. Instituto de Medicina Tropical Pedro Kourí. Apartado 601, Marianao 13, Ciudad de La Habana, Cuba. Teléf: 2020426. Correo electrónico: odalys@ipk.sld.cu
1 Máster en Virología. Licenciada en Bioquímica. Investigadora Agregada. Instituto de Medicina Tropical ¨Pedro Kourí¨ (IPK).
2 Doctora en Ciencias. Licenciada en Biología. Investigadora Titular. IPK.
3 Especialista de II Grado en Microbiología. Investigador y Profesor Titular. IPK.
4 Doctor en Ciencias. Especialista de II Grado en Microbiología. Investigador Auxiliar. IPK.
5 Máster en Virología. Licenciada en Microbiología. Investigadora Agregada. IPK.
6 Licenciada en Microbiología. IPK.
7 Doctor en Ciencias. Licenciado en Biología. Instituto de Salud Carlos III, España.