 ]]>
]]>
ARTÍCULO DE REVISIÓN
Contribución de la genética moderna al desarrollo de la reprogramación celular
Contribution of current genetics to development of cellular reprogramming
]]>
Dra. Kalia Lavaut-Sánchez; DrC. Prof. Porfirio Hernández-RamírezInstituto de Hematología e Inmunología. Ciudad de La Habana, Cuba.
RESUMEN
El avance en el conocimiento de la genética y en especial de la biología molecular, dio paso a una nueva era: la genómica, y a nuevos conceptos como transcriptoma, proteoma, metaboloma, epigenoma, que permiten el estudio de la estructura, organización y función de todos los genes y sus productos, así como de los mecanismos implicados en la regulación de su expresión y el modo en que unos genes interactúan con otros. El uso de nuevas tecnologías en la investigación con células madre favoreció el desarrollo de las células madre pluripotentes inducidas, con el empleo de numerosos métodos para su obtención. Esto demostró que la adición de un reducido número de genes posibilita la reprogramación de células somáticas y la formación de células madre pluripotentes con características embrionarias, sin necesidad de utilizar embriones humanos, lo que tiene sus connotaciones éticas y posibles aplicaciones terapéuticas en medicina regenerativa. ]]>
Palabras clave: genómica, células madre, reprogramación celular, células madre inducidas.ABSTRACT
The advance of the genetics and specially of the molecular biology, gave rise to a new era: the genomic and to new concepts like transcriptome, proteome, metabolome, epigenome allowing us to study the structure, organization and function of all the genes and its products, as well as the mechanisms involved in regulation of its expression and the way in which some genes interacting each other. The use of new technologies in research of stem cells favored the development of induced pluripotent stem cells using the many methods for its detection. It was demonstrated that the addition of a reduced number of genes allows the reprogramming of somatic cells and the formation of pluripotent stem cells with embryonic features, without the use of human embryos, which has its ethical connotations and potential therapeutic applications in regenerative medicine.
Key words: Genomics, stem cells, cellular reprogramming, and induced stem cells.
INTRODUCCIÓN
La genética surgió como una rama de la biología a partir de los primeros experimentos en cruzamientos de plantas realizados por el monje agustino Gregor Mendel, entre los años 1854 y 1868. Años después, Watson y Crick, basándose en los estudios de difracción de rayos X hechos por ellos y otros autores, propusieron una estructura para el ácido desoxirribonucleico (ADN), la que se compone de 2 cadenas de nucleótidos organizadas en una doble hélice.1
La información contenida en el ADN es procesada en 2 etapas consecutivas denominadas transcripción y traducción. La transcripción es el proceso mediante el cual la información almacenada en el código genético se transmite desde el ADN hasta un tipo particular de ácido ribonucleico (ARN), el ARN mensajero (ARNm). La traducción es la transmisión de la información de dicho ARN hasta una secuencia de aminoácidos (proteína). Este último proceso ocurre en los ribosomas, los que contienen 4 tipos diferentes de ARN ribosomal y un gran número de proteínas ribosómicas específicas. La transferencia de información genética desde el ADN hasta el ARN y en último término hasta las proteínas, se ha denominado dogma central de la biología molecular.2
El concepto original de un gen como una secuencia contigua de ADN que codifica una proteína, se modificó con el conocimiento de la existencia de secuencias no codificantes o intrones mediante la separación de las secuencias codificantes o exones; estos últimos son las regiones génicas que llevan la información para la síntesis del ARNm y las proteínas, mientras que los intrones son eliminados del transcripto primario mediante un proceso denominado empalme (splicing). El empalme es un fenómeno normal en células eucariotas y permite incrementar la diversidad de las proteínas. Se conocen, además, sitios de empalme alternativo, proceso mediante el cual los exones del ARNm producto de la primera etapa de la transcripción, se pueden reconectar de diferentes formas. El resultado son diferentes ARNm que son traducidos en diferentes proteínas. En los humanos, el 80 % de los genes tienen empalmes alternativos.3 ]]>
Una importante tarea de múltiples científicos ha sido conocer la secuencia de esas cadenas y diseñar mapas que permitan ubicar los genes en los cromosomas, para así poder aplicar terapias dirigidas a remplazarlos o modificarlos. Paralelamente surgió el concepto de genoma para calificar el conjunto de genes existentes en una célula, lo que determinó el comienzo de un gran trabajo llamado Proyecto Genoma Humano4. Se pensaba que el genoma estaba constituido por 100 000 genes, pero actualmente se conoce que su composición varía aproximadamente entre 20 000 y 25 000 genes distintos. Los genes contienen codificada la información necesaria para la síntesis de una o varias proteínas, aunque se conoce que algunos de ellos no codifican proteínas, sino ARN ribosomales (ARNr) y de transferencia (ARNt) que no se traducen, pero tienen función propia.Este proyecto ha sido sin duda uno de los avances científicos más importantes en la historia de la humanidad, no solo por las implicaciones científicas que se derivan directamente de él sino por sus implicaciones morales y éticas, ya que demostró que todos los seres humanos compartimos el 99,99 % de nuestro ADN, es decir, somos iguales en el 99,99 %. Nos diferenciamos solo en el 0,01 % de la información genética que poseemos y esto es lo que hace que cada ser humano tenga una característica propia e individual.
Hasta hace poco, con las tecnologías disponibles de Biología Molecular, se estudiaban la estructura y función de genes individuales, pero con los avances científicos en esta rama de la ciencia surgió la genómica, cuyos métodos permiten el estudio conjunto de miles de genes, así como las complicadas redes de interacciones que entre ellos se establecen en el interior de las células durante su ciclo vital. La genómica tiene el potencial de revolucionar la práctica médica con lo que se denomina medicina personalizada.4
En las últimas décadas, la tecnología del ADN recombinante ha tenido una gran importancia. La identificación de las endonucleasas de restricción, el desarrollo de los vectores de clonación del ADN, de la reacción en cadena de la polimerasa y los microarreglos, entre otras técnicas, han revolucionado el mundo de la biología molecular y han surgido nuevos conceptos como transcriptoma, proteoma, metaboloma, epigenoma y las respectivas disciplinas que los estudian: transcriptómica, proteómica, metabolómica, epigenómica. Los estudios de transcriptómica, proteómica y metabolómica constituyen la genómica funcional.5
TRANSCRIPTOMA
Es el conjunto de genes que se están expresando en un momento dado en una célula. La expresión de un gen supone que este ha sido transcripto a ARN mensajero. Cada tipo celular tiene un transcriptoma característico.6 Además de los diferentes genes activos en un momento dado, que generan un conjunto particular de ARNs mensajeros, también se transcribe ADN que no es traducido a proteína. Este ARN no codificante tiene un importante papel regulador sobre la expresión de genes.
Actualmente se conoce que la mayoría de los organismos eucariotas tienen un gran número de genes que se transcriben en forma de ARN pequeños, los que están implicados en muchos de los procesos biológicos, incluido el desarrollo, la diferenciación y proliferación celular, la muerte celular, el control metabólico, la hematopoyesis, el silenciamiento transposómico, la defensa antiviral y la diferenciación y mantenimiento de las células madre.7-9 Dentro de este grupo se encuentran los microRNAs (miARN) y pequeños ARNs endógenos de interferencia (endo-siARNs).
Los miARN son las moléculas efectoras naturales del mecanismo de ARN de interferencia (ARNi), de 21 a 25 nucleótidos de longitud se incorporan a un complejo ribonucleoproteico efector, conocido como complejo de silenciamiento inducido por ARNi (RISC, del inglés RNA - induced silencing complex) que señaliza y degrada los ARNm complementarios por ruptura endonucleolítica o inhibición de la traducción. El nivel de complementariedad de las bases nucleotídicas entre los miARN y los ARNm específicos define cuál de los 2 procesos se realizará. La perfecta complementariedad de bases entre ellos induce la degradación de los transcriptos, mientras que la existencia de varias bases no apareadas produce inhibición de la traducción. Esta nueva familia de ARN son diversos en secuencia, se encuentran evolutivamente conservados y están implicados en los mecanismos reguladores postranscripcionales del silenciamiento de la expresión génica.
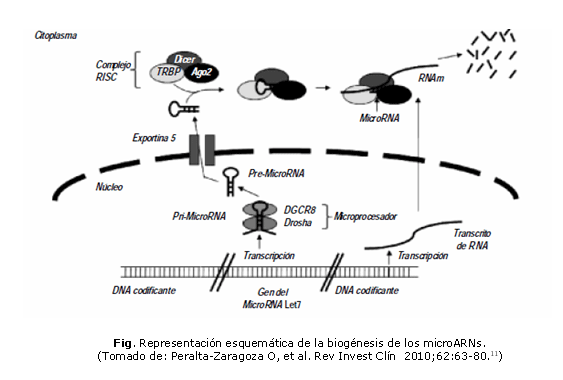
El proceso de biogénesis de los miARN maduros comienza en el interior del núcleo. Cada transcripto primario (pri-miARN) tiene una longitud de 60 a 110 nucleótidos y forman estructuras de plegamiento secundario, donde un pequeño segmento palindrómico se autoaparea por complementariedad de bases que forman una horquilla compuesta por un fragmento apareado y un pequeño bucle en el extremo. Los pri-miARNs son procesados por el microprocesador, el cual está constituido por la proteína de unión al ARN, DGCR8 (del inglés, Di George Síndrome critical region gene 8) y una endonucleasa RNasa tipo II llamada Drosha, que reconoce a esta estructura y la corta por la zona de doble hebra. Esto da lugar a los pre-miARNs que constan de un segmento de doble cadena de 33 nucleótidos con un extremo libre y en el otro un bucle de cadena simple. Luego, los pre-miARN son transportados al citoplasma por el factor de intercambio de nucleótido de guanina Ran (Ran-GTP) y el receptor Exportina 5. Los pre-microARNs se acoplan al complejo RISC, el que está compuesto por la proteína TRBP, proteínas Argonauta 2 (Ago 2) y una segunda RNasa tipo III llamada Dicer que corta el bucle del extremo y libera un fragmento de doble cadena de 22 nucleótidos. Una de las hebras es usada como molde para reconocer a la molécula de ARNm, mientras que la otra cadena es degradada (figura).10,11
Este proceso fue descrito por primera vez en 199312 y referido en el 2001 en varios artículos.13-15 Se han identificado más de 1 000 tipos de miARNs, y por estudios bioinformáticos se predice la existencia de muchos más, aunque solo un determinado subconjunto de ellos es activo en cada tipo celular.Paralelamente a la identificación de los miARNs, también se han descrito ARNs de interferencias pequeños, endógenos llamados endo-siARNs (del inglés small interferent RNA). Se ha demostrado que tienen una longitud de 21 nucleótidos, con orientación sentido y antisentido, extremos 3´modificados, y el extremo 5´ no comienza con uracilo. Son altamente específicos para la secuencia de nucleótidos de ARNm a diferencia de los microARN. Estos siARNs derivan de transposones, de secuencias de heterocromatina, de regiones intergénicas, de transcriptos largos de ARN y de ARNm codificantes.16
Aunque son muchos los métodos para estudiar el transcriptoma, el más utilizado es el de microarreglos o micromatrices, que permite analizar miles de moléculas de ARNm y cuantificar el nivel de expresión de los genes de forma simultánea en un momento del desarrollo o en respuesta a diferentes estímulos ambientales. Los nuevos procedimientos basados en análisis sobre micromatrices de ADN permitirán analizar de forma simultánea prácticamente la totalidad de los genes, mediante la utilización de un soporte (chip) con una superficie aproximada de un centímetro cuadrado.17 Esta nueva capacidad de identificación simultánea y rápida de los genes permitirá conocer el grado de interrelación entre genes o grupos de genes y su influencia en relación con la actividad funcional normal de la célula y, por lo tanto, también de sus alteraciones e implicaciones en la patología.
PROTEOMA
Describe el conjunto total de proteínas expresadas por un genoma completo de una célula durante su tiempo de vida, incluidas las modificadas después de la traducción.
El método más utilizado para estudiar la expresión de las proteínas codificadas por los transcriptos es la electroforesis bidimensional en geles de poliacrilamida. Esta técnica permite separar con gran resolución la mayoría de los polipéptidos celulares combinando de forma secuencial diferencias en carga y en masa molecular.18
METABOLOMA
Los metabolitos son todos los compuestos intermediarios de las reacciones bioquímicas. Es el conjunto dinámico de moléculas y elementos químicos presentes en un organismo vivo, sean sintetizados de novo por el propio organismo o incorporados desde el exterior.
En el año 2007 se completó el análisis del metaboloma humano, individualizando y caracterizando cerca de 2 500 metabolitos, 1 200 principios activos y 3 500 componentes de origen alimentario.19
EPIGENOMA ]]>
El término epigenética se define como cambios heredables en la expresión génica que no son debidos a alteraciones en la secuencia del ADN, sino a modificaciones químicas que controlan la utilización selectiva de los genes.Los seres vivos están formados por células que muestran características morfológicas y funcionales diferentes; aunque todas presentan una información genética idéntica, esta no se expresa de forma simultánea en una misma célula, sino que a lo largo del desarrollo celular se seleccionan grupos de genes que determinan el futuro estructural y funcional de determinados tipos celulares.
Todas las células proceden por divisiones sucesivas de una célula precursora común y las características morfo-funcionales propias de cada tipo celular dependen básicamente del particular grupo de genes que han sido seleccionados para manifestarse. También existe especificidad temporal, lo que quiere decir que los diferentes genes en una célula se activan o desactivan en diferentes momentos de la vida de un organismo.
La regulación de la expresión génica constituye un proceso esencial en el mantenimiento de las diferencias estructurales y funcionales de las células. Las investigaciones sugieren que a medida que las células se desarrollan hacia destinos específicos, ciertas regiones de sus genomas se cierran debido a varias modificaciones epigenéticas. Entonces este acceso limitado para determinados genes se manifiesta en una limitación de su potencial de diferenciación.20
Los mecanismos epigenéticos incluyen las modificaciones de las histonas, el remodelado de la cromatina y la metilación del ADN. Esta última es la principal modificación epigenética del genoma, que regula aspectos fundamentales de su función.
La extensión de la metilación está inversamente relacionada con la actividad génica. Los genes que son inactivos transcripcionalmente están frecuentemente hipermetilados. Comprende diferentes proteínas reguladoras como las ADN metiltransferasas, desmetilasas, proteínas de unión a CpG metilados, enzimas modificadoras de histonas y complejos remodeladores de la cromatina. La región del promotor metilada puede bloquear la transcripción lo que evita la unión de los factores de transcripción; o bien los grupos metilos pueden unirse con otras proteínas que cambian la conformación del cromosoma y hacen la región del promotor inaccesible para la transcripición.
La investigación epigenética ha adquirido una importancia fundamental para el desarrollo de la tecnología de las células madre teniendo en cuenta los mecanismos epigenéticas que pueden intervenir en la regulación de la expresión génica.21
CÉLULAS MADRE EMBRIONARIAS Y ADULTAS
Las células madre, según su estado evolutivo, pueden clasificarse en embrionarias y adultas. Las células madre embrionarias (CMEs) derivan de la masa celular interna del embrión en estadio de blastocisto (7-14 días) y son capaces de generar los diferentes tipos celulares del cuerpo, por ello se llaman pluripotenciales; por otra parte, están las células madre adultas presentes en tejidos de fetos, recién nacidos y adultos.22 Recientemente se han descrito células con características embrionarias obtenidas mediante la reprogramación de células adultas y se denominan células madre pluripotentes inducidas (CMPi).23-25
Métodos de obtención de células madre pluripotentes inducidas (CMPi) ]]>
Varios grupos han mostrado que las células somáticas del humano y el ratón pueden ser reprogramadas por sobreexpresión de algunos factores de transcripción y obtener células con características embrionarias. Estos trabajos han revolucionado la biología de las células madre y han proporcionado nuevas posibilidades para sus aplicaciones terapéuticas en medicina regenerativa.23-27En los experimentos pioneros de los investigadores japoneses Takahashi y YamanaKa23 se hizo el análisis de un grupo inicial de 24 genes, cuya expresión se había asociado de forma específica con células embrionarias y mediante experimentos de transfección en fibroblastos embrionarios de ratón (MEF), fueron eliminando uno a uno los genes. Al final, se redujo la lista a solo 4 genes (Oct4, Soc2, Kfl4, c-Myc). Estos factores de transcripción conforman una intrincada red de interacciones a través de la formación de heterodímeros que actúan sobre los promotores de los genes diana, inducen la expresión de genes que promueven la pluripotencia e inhiben genes que median la diferenciación, además de regular su propia expresión.
El Oct4 pertenece a la familia de factores de transcripción Oct (octámero) y tiene una función clave en el mantenimiento de la pluripotencia. El Sox2 coopera activamente con Oct4 en la regulación de genes implicados en el mantenimiento de la pluripotencia, como Nanog, Fgf4, osteopontina y Lefty, pero, a diferencia de Oct4, no se expresa solamente en células pluripotentes, sino que también lo hace en etapas tardías del desarrollo, especialmente en células madre neuronales. Kfl4 es un miembro de la familia de factores de transcripción Kruppel-like que se expresa en CMEs y parece desempeñar una doble función como oncogén y antioncogén. En la reprogramación parece estar relacionado con la inhibición de p53, que evita la salida de las células del ciclo celular y contrarresta la acción de c-Myc en la inducción de la apoptosis y la diferenciación; se expresa en células de piel, estómago, intestino y músculo esquelético. El c-Myc es un factor de transcripción con múltiples dominios y un potente oncogén implicado en la proliferación celular, la replicación del ADN, la inhibición de la diferenciación celular y la metástasis. Aunque se ha demostrado que el c-Myc no es indispensable para la reprogramación celular, su presencia sí influye de manera significativa en la cinética y la eficiencia del proceso.28 La inclusión de este último en el grupo de 4 genes resultaba problemático, pues es un protooncogen implicado en muchas funciones celulares, como el control del ciclo celular. Su activación fuera de control puede causar tumores. Ante esta situación, el grupo de Yamanaka decidió obtener células inducidas a partir del uso de Kfl4, Oct3/4, Sox2, pero sin añadir c-Myc. Los ratones generados a partir de esas células no desarrollaron tumores. 29
Otros investigadores han minimizado el número de genes que es necesario transferir, combinándolos con drogas que inhiban o bloqueen determinadas rutas metabólicas o de señalización celular. Se demostró que era posible obtener CMPi a partir de fibroblastos humanos mediante la introducción de Oct3/4 y Sox2 y la exposición de las células a un inhibidor de histonas desacetilasas.30
Recientemente, un grupo de científicos utilizó una nueva combinación de genes para la reprogramación de células adultas, se agregó un nuevo factor de transformación, el Tcl- 1A, a los ya conocidos Sox2 y c-Myc.31
Se han utilizado diferentes técnicas para inducir la expresión de los factores de pluripotencia en varios tipos de células adultas. Esta misma combinación de factores funciona también con fibroblastos humanos. El método más común es la transducción génica utilizando retrovirus y más recientemente, lentivirus. Sin embargo, presenta el problema de generar un alto riesgo de inducir mutaciones en los sitios de inserción del retrovirus y de modificar de manera permanente el genoma de las CMPi e inducir la formación de tumores. Varios métodos alternativos se han propuesto tratando de resolver este problema: la utilización de adenovirus no integrativos,32 la transfección transitoria con plásmidos,33 el uso de transposones (piggyBac transposition system)34 y el uso de virus que pueden retirarse de la célula una vez que han cumplido su objetivo de inducir la expresión de los genes de pluripotencia, mediante el sistema Cre (Cre-excisable virus).35 En teoría, estos procederes minimizan el riesgo de modificación del genoma de la célula diana, aunque este riesgo no puede ser descartado de manera absoluta, lo que limita, por ahora, la utilización de las CMPi en ensayos clínicos.
Específicamente el denominado sistema piggyBac, ha sido descrito por varios equipos de investigadores.36,37 Consiste en utilizar en la reprogramación un único vector que es un plásmido que funciona como soporte físico de los 4 genes usados habitualmente, asociado con un transposón (piggyBac), que es una secuencia de ADN con la capacidad de moverse a lo largo del genoma de una célula. Este método, aunque también utiliza plásmidos, añade la herramienta del transposón para eliminar los 4 genes introducidos en las líneas celulares ya establecidas, lo que se minimiza el riesgo de daño al genoma, por lo que es más segura que las anteriores que presentaban problema para eliminar dichos vectores.
La nomenclatura de este sistema surge a partir de los transposones de Drosophila que estaban insertados en genomas de Baculovirus y eran cargados alrededor de estos genomas virales. Así, después de darle diferentes nombres a este transposón, se buscó uno más llamativo y por afinidad se pensó en la palabra piggyback que significa "montar a horcajadas sobre los hombros". Para indicar la relación con los Baculovirus se sustituyó la k y se puso B en mayúscula y así surgió piggyBac.
En el 2009 se publicó un trabajo que cambió la tecnología de las CMPi para inducir la pluripotencia en células somáticas sin la utilización de ADN ni el empleo de virus. El material genético que se venía empleando hasta ese momento se sustituyó por proteínas recombinantes (Oct4, Sox2, c-Myc y Klf4) producidas en el laboratorio a partir de la bacteria Escherichia coli. Las 4 proteínas estaban combinadas por su extremo carboxílico con el péptido poliarginina de 11 residuos, lo cual facilita atravesar la membrana celular y nuclear (técnica conocida como CCP del inglés cell penetrating peptide). Las proteínas se añadieron al medio de cultivo donde se encontraban células adultas de la piel de ratones, que se transformaron en otras más primitivas y pluripotenciales. Se demostró que estas células eran capaces de convertirse en cualquier otro tejido. Las ventajas de este nuevo método incluyen: menos costo, más simple y rápido que los utilizados hasta entonces y fundamentalmente poder lograr células madre con características embrionarias sin la inserción de genes que alteren el código genético de las siguientes generaciones celulares.38
En este contexto de avances científicos con algunos aspectos aún muy controvertidos, ha surgido recientemente lo que puede ser un nuevo hito en la biología celular moderna: las células sintéticas. La información de una secuencia genómica de Micoplasma mycoides obtenida por síntesis biotecnológica, fue introducida dentro de una célula de Micoplasma capricolum para crear nuevas células de Micoplasma mycoides, pero controladas por el cromosoma sintético. El ADN sintético incluía secuencias marcadoras, polimorfismos y mutaciones adquiridas durante el proceso. Las nuevas células tienen el fenotipo esperado y son capaces de continuar su autorreplicación.39 ]]>
Muy recientemente se ha comunicado otro avance en este campo con la introducción de un nuevo método, que aunque relativamente complejo, se plantea que resulta más eficiente que los otros procederes establecidos con anterioridad para hacer la reprogramación de células humanas diferenciadas y llevarlas al estado de pluripotencialidad.Con este nuevo método, las células adultas diferenciadas se convirtieron en células pluripotentes reprogramándolas con ARNm, por lo que las células así reprogramadas se nominaron RiPS (del inglés RNA induced pluripotent stem cells). El ARNm que se empleó en el desarrollo de las RiPS fue un ARNm sintético modificado para que no desencadenara reacciones adversas en las células. Una ventaja adicional de este procedimiento es que también puede usarse para transformar las CMPi en células diferenciadas de linajes predeterminados, lo que permite controlar la diferenciación de las células madre pluripotenciales. Se ha señalado que esta tecnología de ARN elimina el riesgo de integración genómica y mutagénesis insercional que se atribuye a todas las metodologías basadas en ADN.40
Las células madre pluripotentes inducidas (CMPi) ¿son similares o no a las células madre embrionarias (CMEs)?
Se podría afirmar que no existe una diferencia esencial entre las CMEs y las CMPi. Sin embargo, el grado de similitud molecular entre ellas no ha sido completamente dilucidado.
Diferentes estudios sugieren que las CMPi son casi idénticas a las CMEs, pero hay un pequeño porcentaje de sus genes que son expresados diferencialmente. Lo que no está claro es si estas diferencias están dadas por el protocolo de cada experimento o si todas las células reprogramadas expresan una individualidad que las distingue a ellas. Varios grupos han utilizado técnicas para identificar un número de genes que únicamente se expresan en las células embrionarias, pero no en las células maduras, y se definen como genes representantes del linaje de célula madre (stemness), los cuales son responsables de la pluripotencia; dicha función se mantiene por un breve tiempo durante el desarrollo embrionario de los mamíferos, en las células de la masa celular interna del blastocisto. La pérdida de la pluripotencia y la diferenciación a tejidos celulares específicos conduce a cambios en los patrones de expresión génica que incluyen el silenciamiento de genes que codifican para factores de transcripción que son claves para el mantenimiento de la pluripotencia y la expresión de genes inductores de la diferenciación.41
Chin y otros, aplicaron métodos para comparar CMEs y CMPi de humanos y ratones mediante técnicas de hibridización genómica comparativa, con el fin de detectar alteraciones subcariotípicas en ambos grupos de células; además, hicieron estudios del perfil de ARN y de miARN, así como de modificación de las histonas para determinar si existían diferencias en su expresión génica.42
Se pudo apreciar que el 79 % de los genes son expresados a un nivel más bajo en las CMPi que en las CMEs. Esta observación sugiere que las CMPi humanas no tienen eficientemente silenciado el patrón de expresión de las células somáticas de las que se originaron.
Para determinar si los miARNs son expresados al mismo nivel en las CME que en las CMPi, se hizo un análisis de su perfil de expresión y se apreció que el patrón de este tipo de ARN es altamente reproducible entre diferentes experimentos de reprogramación y que las CMPis tienen una individualidad en su miARN que las define como únicas dentro de las CMEs.42
Se pudiera pensar que la causa de la expresión diferencial de los genes entre las células embrionarias e inducidas pudiera estar dada por el protocolo de reprogramación en sí mismo o por alteraciones genómicas. Sin embargo, en estudios de hibridización genómica comparativa se detectaron pocas alteraciones subcariotípicas, lo que sugiere que el genoma de las células reprogramadas se mantiene muy estable después de múltiples pasos.
Por otra parte, las células madre embrionarias e inducidas son similares en morfología, tasa de proliferación y en la expresión de algunos marcadores genéticos como la telomerasa, enzima que mantiene la longitud de los telómeros cromosómicos, elementos importantes para mantener la capacidad de replicación. ]]>
En estudios recientes se pudo apreciar que las CMPi mantienen su memoria, huella del patrón de metilación de las células somáticas de las que proceden. Como ejemplo de esto se ha evidenciado que las CMPi obtenidas a partir de la sangre son más fáciles de retornar a células sanguíneas que las producidas a partir de células de piel o del cerebro.43Al parecer, las diferencias entre ambos tipos celulares radican en su origen y expresión génica. Un aspecto que es necesario definir en las CMPi es su capacidad de inducir tumores, puesto que este es un riesgo en común con las CMEs y limitarían su potencialidad terapéutica.
Aplicaciones clínicas de las células madre
Actualmente, la terapia celular ha surgido como una opción de gran relevancia clínica para la regeneración tisular. Los nuevos conocimientos adquiridos sobre las células madre y su capacidad de convertirse en células de diferentes tejidos está relacionada con la medicina regenerativa y su aplicación clínica en enfermedades cardiovasculares, neurológicas, diabetes, alteraciones ortopédicas, enfermedades malignas, entre otras.
La reprogramación de una célula somática diferenciada a una célula pluripotente con características similares a las embrionarias, es un impacto en el campo de la biología celular que evita el problema ético de la utilización de embriones o de ovocitos humanos y permite desarrollar una fuente de células pluripotentes viable técnicamente y socialmente aceptable. Además, ofrece una herramienta para el estudio de las bases moleculares y celulares de las enfermedades.44
Se han comunicado estudios en los que se han obtenido CMPi de pacientes con anemia de Fanconi, con la particularidad de que las células somáticas fueron previamente tratadas con terapia génica para corregir su defecto genético, por lo que las células producidas eran normales y por lo tanto, crean una nueva posibilidad terapéutica para pacientes con esa enfermedad.45 También se han reprogramado células de pacientes con diabetes mellitus de tipo 1, que se han podido diferenciar en productoras de insulina, por lo que podrían ser útiles para estudiar la patogenia de la enfermedad y crean nuevas expectativas terapéuticas para estos pacientes que pudieran conducir a la terapia celular personalizada.46 Sin embargo, en este campo solo se están dando los primeros pasos y se han hecho algunas investigaciones para tratar de diferenciar in vitro las CMPi hacia linajes celulares específicos.
Por otra parte, como antes comentamos, se han podido obtener CMPis con características autólogas, al proceder de un paciente con determinada enfermedad, lo que abre la posibilidad de su uso en estos casos sin los conflictos que ocasionan las células alogénicas. No obstante estos avances en el área experimental, se considera que aún debe pasar un tiempo antes que se pueda desarrollar su aplicación clínica. Este es un apasionante reto para el futuro. Mientras tanto, la aplicación clínica de las células madre autólogas adultas continúa avanzando y aportando resultados muy alentadores. Solo el futuro podrá contribuir a responder las interrogantes que se mantienen en la actualidad.
REFERENCIAS BIBLIOGRÁFICAS
1. Hernández Fernández R. Panorama de la biología celular y molecular. En: Lantigua A, Hernández R, Quintana J, Morales E, Barrios B, Rojas I, et al. Introducción a la Genética Médica. La Habana: Ciencias Médicas; 2004. pp. 18-24.
2. Mueller RF, Young ID. Fundamentos moleculares y celulares de la herencia. En: Emerys Genética Médica. 10 ed. Madrid: Marban Libros; 2001. p. 16.
3. González CA. Procesamiento de ARNm en la transcripción (splicing).[monografía en internet] Disponible en: http://www.botanica.cnba.uba.ar/Pakete/Dibulgeneral/Splicing/.htm
4. Proyecto Genoma Humano. En: Wikipedia. Disponible en: http://en.wikipedia.org/wiki/proyecto genoma humano
5. Roguev A, Krogan NJ. BAC to the future: Functional genomics in mammals. Nat Methods 2008;5:383-4.
6. Transcriptome. Wikipedia. Disponible en: http://en.wikipedia.orq/wiki/Transcriptome
7. Chu CY, Rana TM. Small RNAs: Regulators and guardians of the genome. J Cell Physiol 2007;213:412-9.
8. Song L, Tuan RS. MicroRNAs and cell differentiation in mammalian development. Birth Defects Res C Embryo Today 2006;78:140-9.
9. Chen XM. MicroRNA signatures in liver diseases. World J Gastroenterol 2009;15:1665-72.
10. Denli AM, Tops BBJ, Plasterrk RHA, Ketting RF, Hannon GJ. Processing of primary microRNAs by the microprocessor complex. Nature 2004;432:231-5.
11. Peralta-Zaragosa O, Bermúdez-Morales VH, Madrid-Marina V. RNA de interferencia: biogénesis, mecanismos moleculares y sus aplicaciones en cáncer cervical. Rev Invest Clín 2010;62:63-80.
12. Lee RC, Feinbaum RL, Ambros V. The C elegans heterochronic gene encodes small RNAs with antisense complementarity to lin-14. Cell 1993;75:843-54.
13. Lagos-Quintana M, Rauhut R, Lendeckel W, Tuschl T. Identification of novel genes coding for small expressed RNAs. Science 2001;294:853-8.
14. Lau NC, Lim LP, Weinstein Eg, Bartel DP. An abundant class of tiny RNAs with probable regulatory roles in Caenorhabditis elegans. Science 2001;294:858-62.
15. Lee RC, Ambros V. An extensive class of small RNAs in Caenorhabiditis elegans. Science 2001;294:862-4.
16. Ghildiyal M, Seitz H, Horwich MD, Li C, Du T, Lee S, et al. Endogenous siRNAs derived from transposons and mRNAs in Drsophila somatic cells. Science 2008;320(5879):1077-81.
17. DeRisi JL, Iyer VR, Brown PO. Exploring the metabolic and genetic control of gene expression on a genomic scale. Science 1997;278:680-6.
18. Humphery-Smith I, Blackstock W. Proteome analysis: Genomics via the output rather than the input code. J Protein Chem 1997;16:537-44.
19. Metabolome. En: Wikipedia. Disponible en: http://en.wikipedia.org/wiki/metabolome
20. ¿Epigenética? La epigenética y el futuro de las células madre. [homepage on the internet] Disponible en: http://epigenome.eu/es/
21. Paz MF. Mecanismos epigenéticos de regulación de la expresión génica. (monografía en Internet). Departamento de Inmunología y Oncología. Madrid: CNB-CSIC Disponible en: http://nevada.ual.es/agr
22. Hernández P, Dorticós E. Medicina regenerativa. Células madre embrionarias y adultas. Rev Cubana Hematol Inmunol Hemoter. 2004; 20: Disponible en: http://scielo.sld.cu/scielo.php?script=sci_arttext&pid=S086402892004000300001&lng=es&nrm=iso
23. Takahashi K, Yamanaka S. Induction of pluripotent stem cells from mouse embryonic and adult fibroblast cultures by defined factors. Cell 2006;126:663-76.
24. Takahashi K, Yamanaka S, Tanabe K, Ohnuki M, Narita M, Ichisaka T, et al. Induction of pluripotent stem cells from adult human fibroblasts by defined factors. Cell 2007;131:861-72.
25. Yu J, Vodyanik MA, Smuga-Otto K, Antosiewicz-Bourget J, Frane JL, Tian S, et al. Induced pluripotent stem cell lines derived from human somatic cells. Science 2007;318:1917-20.
26. Okita K, Ichisaka T, Yamanaka S. Generation of germline- competente induced pluripotent ítem cells. Nature 2007;448:313-7.
27. Maherali N, Sridharan R, Xie W, Utical J, Eminli S, Arnold K, et al. Directly reprogrammed fibroblasts show global epigenetic remodeling and widespread tissue contribution. Cell Stem Cell 2007;1:57-70.
28. Chaparro O, Beltrán O. Reprogramación nuclear y células pluripotentes inducidas. Rev Med 2009;17:252-63.
29. Nakagawa M, Koyanagi M, Tanabe K, Takahashi K, Ichisaka T, Aoi T, et al. Generation of induced pluripotent ítem cells without Myc from Mouse and human fibroblasts. Nat Biotechnol 2008;26:101-6.
30. Huangfu D, Osafune K, Maehr R, Guo W, Eijkelenboom A, Chen S, et al. Induction of pluripotenet stem cells from primary human fibroblasts with only Oct 4 and Soc2. Nat Biotechnol 2008;26:1269-75.
31. Picanço-Castro V, Russo-Carbolante EM, Reis LJ, Fraga AM, Magalhães DA, Orellana MD, et al. Pluripotent reprogramming of fibroblasts by lentiviral-mediated insertion of SOX2, C-MYC and TCL-1A. Stem Cells Dev 2010 May 26. [Epub ahead of print]
32. Stadtfeld M, Brennand K, Hochedlinger K. Reprogramming of pancreatic beta cells into induced pluripotent stem cells. Curr Biol 2008;18:890-4.
33. Okita K, Nakagawa M, Hyenjong H, Ichisaka T, Yamanaka S. Generation of mouse induced pluripotent stem cells without viral vectors. Science 2008;322:949-53.
34. Woltjen K, Michael IP, Mohseni P, Desai R, Mileikovsky M, Hamalainen R, et al. piggyBac transposition reprograms fibroblasts to induced pluripotent stem cells. Nature 2009;458:766-70.
35. Soldner F, Hockemeyer D, Beard C, Gao Q, Bell GW, Cook EG, et al. Parkinson's disease patient-derived induced pluripotent stem cells free of viral reprogramming factors. Cell 2009;136:964-77.
36. Kaji K, Norrby K, Paca A, Mileikovsky M, Mohseni P, Woltjen K. Virus-free induction of pluripotency and subsequent excision of reprogramming factors. Nature 2009;458:771-5.
37. Woltjen K, Michael IP, Mohseni P, Desai R, Mileikovsky M, Hämäläinen R, et al. PiggyBac transposition reprograms fibroblast to induced. Nature 2009;458:766-70.
38. Zhou H, Wu S, Joo JY, Zhu S, Han D W, Lin T, et al. Generation of induced pluripotent stem cells using recombinant proteins. Cell Stem Cell 2009;4:381-4.
39. Craig Venter, Gibson DG, Glass J, Lartigue C, Noskov V, Chuang RY, et al. Creation of a bacterial cell controlled by a chemically synthesized genome. Science 2010;329(5987):52-56. DOI: 10.1126/science.1190719. Disponible en:
http://www.sciencexpress.org / 20 May 2010 / Page 1 / 10.1126/science.1190719 8
]]>
40. Warren L, Manos PD, Ahfeld T, Loh YH, Li H, Lau F, et al. Highly efficient reprogramming to pluripotency and directed differentiation of human cells with synthetic modified m RNA. Cell stem cell. Disponible en: http://www.cell.com/all-stem-cell/fulltext/S1934.5909(10)00434-0 (Visitado 25-10-2010)
41. Bhattacharya B, Puri S, Puri RK. A review of gene expression profiling of human embryonic stem cell lines and their differentiated progeny. Curr Stem Cell Res Ther 2009;4:98-106.
42. Chin MH, Mason MJ, Xie W, Volinia S, Singer M, Peterson C, et al. Induced pluripotent stem cells and embryonic stem cells are distinguished by gene expression signatures. Cell Stem Cell 2009;5:111-23.
43. Kim K, Doi A, Wen B, Ng K, Zhao R, Cahan P, et al. Epigenetic memory induced pluripotent ítem cells. Disponible en: http://www.nature.com/nature/journal/unfv/ncurrent/full/nature09342.html
44. Cruz L. Reprogramación nuclear y celular. Gac Méd Caracas 2010;118:68-69 Disponible en: http://www.scielo.org.ve/pdf/gmc/v118n1/art10.pdf
45. Raya A, Rodríguez-Pizá I, Guenechea G, Vassena R, Navarro S, Barrero MJ, et al. Disease-corrected haematopoietic progenitors from Fanconi anaemia induced pluripotent stem cells. Nature 2009;460:53-9.
46. Burt RK, Loh Y, Pearce W, Beohre N, Barr WG, Craig R, et al. Clinical applications of blood derived and marrow derived stem cells for non-malignant diseases. JAMA 2008;299:925-36.
]]>
Recibido: 2 de noviembre del 2010.
Aprobado: 15 de noviembre del 2010.
]]>
Dra. Kalia Lavaut-Sánchez. Instituto de Hematología e Inmunología. Apartado 8070, CP 10800. Ciudad de La Habana, Cuba. Tel (537) 643 8695, 8268. Fax (537) 644 2334. E-mail: ihidir@hemato.sld.cu
]]>