Hibridación in situ fluorescente: herramienta en el diagnóstico de las hemopatías malignas
Fluorescence in situ hybridization: diagnostic tool for hematological malignancies
Dra. Kalia Lavaut Sánchez, Lic. Norbelys Hernández Aguilar, Lic. Vera Ruiz Moleón
Instituto de Hematología e Inmunología. La Habana, Cuba.
]]>
RESUMEN
Introducción: las neoplasias hematológicas tienen origen clonal y se caracterizan por presentar gran heterogeneidad genética. El desarrollo de la citogenética molecular a través de la hibridación in situ por fluorescencia (FISH, por su sigla en inglés) se convirtió en un avance importante en el diagnóstico citogenético de estas neoplasias.
Objetivo: describir las alteraciones cromosómicas detectadas en pacientes con neoplasias hematológicas a partir de la introducción de esta técnica.
Métodos: se realizó un estudio descriptivo de tipo transversal de pacientes con neoplasias hematológicas en el Laboratorio de Citogenética del Instituto de Hematología e Inmunología (IHI), en el período comprendido entre julio de 2014 y abril de 2015. Se utilizó la técnica de FISH con las sondas fluorescentes específicas.
Resultados: se estudiaron 87 muestras correspondientes a diferentes tipos de neoplasias hematológicas. Con la sonda LSI BCR/ABL se observaron 18 casos positivos de leucemia mieloide crónica y los ocho pacientes con leucemia linfoide aguda fueron negativos. Se marcaron con sonda PML/RARα 17 muestras con diagnóstico de leucemia promielocítica: 10 fueron positivas. Se procesaron 8 muestras con la sonda LSI RUNX1/RUNX1T1, una resultó positiva. Dos muestras marcadas con sonda LSI RB1 (13q14) y una con LSI TP53 (17p13.1), resultaron negativas. se observó un caso positivo de deleción 7q31.
Conclusiones: a pesar de que la muestra estudiada es pequeña, resulta importante reportar los primeros resultados como evidencia de la incorporación de la técnica de FISH en el IHI, lo que constituye una nueva herramienta para el diagnóstico, pronóstico y seguimiento de las neoplasias hematológicas.
Palabras clave: hibridación in situ fluorescente, neoplasia hematológica, leucemia.
ABSTRACT
Introduction: hematological neoplasias have clonal origin and are characterized by great genetic heterogeneity. The development of molecular cytogenetic through fluorescence in situ hybridization (FISH) became a major advance in the cytogenetic diagnosis of these neoplasias.
Aim: to describe chromosomal abnormalities detected in patients with hematological malignancies after the introduction of this technique.
Methods: a descriptive cross-sectional study of patients with hematological malignancies was performed. Their bone marrow samples were processed at the Laboratory of Cytogenetics of the Institute of Hematology and Immunology, between July 2014 and April 2015. FISH technique was used along with various fluorescent probes.
Results: 87 samples were studied. With LSI BCR / ABL probe, 18 samples were positive of chronic myeloid leukemia and 8 patients with diagnostic of acute lymphoblastic leukemia were negative. With PML/RARα probe 17 samples of patients with promyelocytic leukemia were labeled, 10 were positive. Eight samples were labeled with probe RUNX1 / RUNX1T1, one was positive. Two samples for LSI probes labeled RB1 (13q14) and one with LSI TP53 (17p13.1) were negative. One positive case 7q31 deletion was observed.
Conclusions: despite the sample is small, we consider it important to report our first results as evidence of the incorporation of the FISH technique at the IHI, which constitutes a new tool for the diagnosis, prognosis and monitoring of hematological malignances.
Keywords: fluorescence in situ hybridization, hematologic malignancy, leukemia.
INTRODUCCIÓN
]]> Las neoplasias hematológicas tienen origen clonal y se caracterizan por presentar gran heterogeneidad genética. Varios mecanismos genéticos se relacionan con el origen de estas dolencias, entre ellos las alteraciones cromosómicas numéricas y estructurales, principalmente deleciones, inversiones y translocaciones. Estas alteraciones conducen a la activación de protooncogenes o a la inactivación de genes supresores de tumores, los cuales promueven la inestabilidad genómica. El análisis citogenético en estas enfermedades es una importante herramienta para definir el diagnóstico, predecir el pronóstico, evaluar la respuesta al tratamiento y profundizar en el conocimiento de las bases genéticas de su patogénesis.1El desarrollo de la citogenética molecular a través de la hibridación in situ por fluorescencia (FISH, por su sigla en inglés), se convirtió en un avance importante en el diagnóstico citogenético de las neoplasias hematológicas. Esta técnica presenta alta sensibilidad y especificidad y posibilita el análisis de células, tanto en metafase como en interfase. Esta última ventaja supera una limitación importante de la citogenética convencional, la necesidad de obtener las células en metafase. Además, permite el análisis de un gran número de células de forma rápida y la identificación de cambios estructurales más sutiles por debajo de la resolución de la citogenética convencional.2
La técnica de FISH utiliza fragmentos de secuencias de ADN, sonda marcada con fluorescencia, con el fin de localizar una secuencia complementaria en el ADN de la muestra. Existen varios tipos de sondas, cada una con una función específica según lo que se desea detectar. Se describen las sondas centroméricas (que marcan toda la región del centrómero), las sondas de pintado cromosómico (constituidas por una librería de sondas que abarcan todo el cromosoma) y las sondas de secuencia única (locus específico) que marcan regiones cromosómicas muy concretas.
Para la detección del cromosoma Filadelfia en las leucemias mieloide crónica (LMC) y linfoide aguda (LLA), se utilizan sondas de locus específicos y diferentes colores para marcar las regiones involucradas, en la búsqueda de señales híbridas para caracterizar la reorganización, tanto en metafase como en núcleos en interfase.
Una metodología similar se utiliza para la detección de la translocación (15;17) presente en la leucemia promielocítica (LPM), así como la translocación (8;21) y otras alteraciones citogenéticas específicas descritas en la clasificación de la OMS del 2008 para la leucemia mieloide aguda (LMA), como la inversión del cromosoma 16 (inv16) y los reordenamientos en 11q23.3
En la leucemia linfocítica crónica (LLC) existe un bajo índice mitótico, por lo que es difícil obtener metafases a través de la citogenética convencional. La técnica de FISH permite detectar alteraciones cromosómicas y estratificar grupos pronósticos con implicación clínica y terapéutica; ejemplo de ello son las deleciones 13q, 17p, los rearreglos en 11q, entre otras.4
En los síndromes mielodisplásicos (SMD) las anomalías cromosómicas detectadas por FISH pueden aportar información pronóstica y ser útiles para respaldar decisiones terapéuticas en algunos casos, como las deleciones 5q, 7q y la monosomía 7. 5
En este trabajo se presentan los primeros resultados de la detección de alteraciones cromosómicas a través de la introducción de la técnica de FISH en el Instituto de Hematología e Inmunología (IHI), como una herramienta más en el diagnóstico de las neoplasias hematológicas.
MÉTODOS
]]> Se realizó un estudio prospectivo, descriptivo de tipo transversal, para identificar las alteraciones cromosómicas por técnica de FISH en muestras de sangre medular (MO) de 84 pacientes con neoplasias hematológicas, recibidas en el Laboratorio de Citogenética del IHI en el período comprendido entre julio de 2014 y abril de 2015.La técnica de FISH se realizó con sondas comerciales marcadas directamente con diversos fluorocromos; se utilizó cada una de las sondas teniendo en cuenta la impresión diagnóstica del paciente en el momento de recepción de la muestra en el laboratorio. En tres de ellos, dada la enfermedad presentada, se realizaron dos estudios con sondas diferentes para un total de 87 estudios, distribuidos como se muestra en el cuadro:
| Sondas | Alteración cromosómica | Estudios |
| LSI BCR/ABL Dual color | t (9;22) | 44 |
| LSI PML/RARA Dual color | t (15;17) | ]]> 17 |
| RUNX1/RUNX1T1 Dual Color | t (8;21) | 9 |
| CBFB Break | rearreglos en el locus CBFB (16q22) | 5 |
| LSI MLL Dual Color | rearreglos en el gen MLL (11q23) | 1 |
| ]]> LSI RB1(13q14) señal naranja | deleción del gen RB1 | 2 |
| LSI TP53(17p13.1) señal naranja | deleción del gen TP53 | 1 |
| LSID7S486 Spectrum Orange/CEP 7 Spectrum Green | deleción 7q31 | 6 |
| LSICSF1R Spectrum Orange/D5S23,D5S721 Spectrum Green | ]]> deleción 5q33-34 | 2 |
Preparación de la muestra
Todas las muestras fueron cultivadas por técnica de citogenética convencional6. La extensión se realizó en láminas portaobjetos y la calidad de la preparación fue verificada en microscopio de contraste de fase.
Pretratamiento de las láminas
Las láminas (debidamente identificadas) fueron sometidas a pretratamiento en solución 2XSSC (NaCl/citrato de sodio) a 37°C, durante 30 min. Posteriormente fueron deshidratadas mediante lavados sucesivos en diluciones etanólicas, al 70 %(v/v), 85 % (v/v) y un tercer lavado en 100 %. Se mantuvieron 2 min en cada lavado.
Hibridación y detección
En cada lámina se aplicaron 10 μL de sonda, se colocó un cubreobjeto y se selló con cemento de goma. Las láminas fueron ubicadas en un sistema de desnaturalización e hibridación de ADN (S-96 Quanta Biotech, qCycler). Se realizó la codesnaturalización a 72°C durante 2 min, seguido de la hibridación en cámara húmeda a 37°C durante toda la noche, por 18 horas. Al día siguiente se retiró el cubreobjeto y se realizaron dos lavados para eliminar la hibridación excedente, en 70 mL de 0,4XSSC/ 0,3 % NP40 a 72°C durante 3 min y posteriormente en 70 mL de 2XSSC/ 0,1 % NP40 a temperatura ambiente (25°C) durante 30 s.
En todos los casos se utilizó la tinción de contraste DAPI (diamidinofenilindol) para la identificación de los núcleos celulares en interfase.
Análisis
]]> Las señales de hibridación se analizaron en un microscopio de fluorescencia OLYMPUSBX51. Los núcleos donde el marcaje era evidente fueron seleccionados para el conteo de las señales. Fueron descartados los núcleos sobrelapados o con un marcaje débil. Fue considerada señal si el marcaje estaba dividido en dos, pero la distancia entre las señales era menor que su ancho.En cada muestra fueron analizados de100 a 200 núcleos. Se consideró positivo el resultado cuando la alteración cromosómica estuvo presente en más del 10 % de los núcleos observados, según bibliografía consultada.7,8
Para las sondas dual color, las células negativas mostraron dos señales rojas (2R) y dos verdes (2V) separadas e independientes (correspondientes a cada par cromosómico). Las células positivas mostraron una señal roja y una verde independiente, y dos señales de fusión roja-verde o amarillas (2F) al estar los dos fluorocromos unidos.
Para las sondas LSI RB1 (13q14), LSI TP53 (17p13.1) las células negativas muestran dos señales rojas y las células con la alteración cromosómica muestran una señal roja.
Para detectar la deleción 7q31 y 5q33-34, las células negativas mostraron dos señales verdes (control) y dos rojas (región de la deleción); mientras que las células positivas mostraron dos señales verdes y una roja.
Captura y procesamiento de imágenes
Se utilizó el Programa Olympus MicroDP-BSW para la captura, procesamiento y análisis de las imágenes. De cada imagen tomada se guardó una versión, como evidencia del marcaje real en los núcleos. Los resultados fueron expresados de acuerdo con la nomenclatura ISCN (del inglés: International Standing Committee on Human Cytogenetic Nomenclature 2013).9
RESULTADOS
Del total de 87 estudios realizados, en cinco no se obtuvo hibridación o resultó muy débil la señal, por lo que estos casos no resultaron útiles para el diagnóstico.
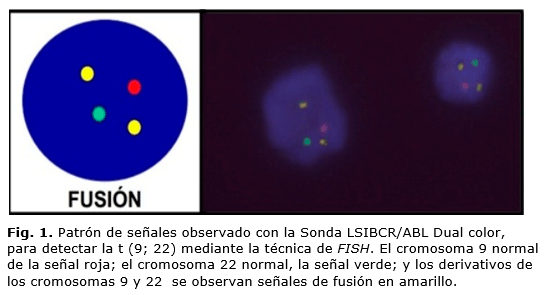
]]> De 42 muestras marcadas con sonda LSI BCR/ABL, 34 correspondían a un posible diagnóstico de LMC y de ellas, sólo 18 resultaron positivas (figura 1); en 17 muestras se observó un patrón típico de hibridación y en una, un patrón atípico. Las ocho muestras restantes marcadas con esta sonda, eran pacientes con LLA al inicio de la enfermedad, todas fueron negativas.Se aplicó una sonda LSI MLL a una muestra de un paciente con LLA de debut para detectar translocaciones que involucren la región 11q23; no se detectó ningún rearreglo en ese locus.
Se marcaron con sonda LSI PML/RARA para la detección de la t(15;17), un total de 17 muestras con diagnóstico de LPM. De ellas, 10 eran estudios al debut y todas resultaron positivas con patrón típico de hibridación. Siete muestras, que eran casos de revaluación, resultaron negativas (figura 2).
Ocho muestras fueron marcadas con sonda LSI RUNX1/RUNX1T1 para detectar la t(8;21); de ellas, solo una resultó positiva, la que mostró un patrón típico de señales. Para identificar la inversión del cromosoma 16 se marcaron tres muestras con la sonda LSI CBFB break; todas resultaron negativas.
En las dos muestras marcadas con sonda LSI RB1 (13q14) y en la marcada con LSI TP53 (17p13.1), no se observó la deleción.
Se observó un caso positivo con la deleción 7q31 (figura 3), de un total de seis muestras estudiadas. Las dos muestras estudiadas para detectar la deleción 5q resultaron negativas.
]]> DISCUSIÓN
La leucemia es un trastorno clonal de las células progenitoras hematopoyéticas, caracterizada por aberraciones genéticas adquiridas. La formación de proteínas de fusión a partir de reordenamientos cromosómicos, ha contribuido significativamente a la comprensión del mecanismo molecular de la patogénesis de la leucemia. La técnica de FISH es considerada de gran utilidad para la detección de alteraciones cromosómicas y por tanto, desempeña una función crucial en la selección de una terapia dirigida a los diferentes tipos de leucemias.10
La translocación recíproca t(9;22)(q34;q11.2) provoca la formación del denominado cromosoma Filadelfia (Ph), el cual se encuentra presente aproximadamente en el 90 % de los pacientes con LMC. En el 10 % restante se pueden presentar translocaciones variantes o atípicas, como la deleción de secuencias en el cromosoma 9 derivativo, que pueden pasar desapercibidas mediante el estudio de citogenética convencional, por lo que el uso del FISH ayuda a confirmar el diagnóstico.11
En el presente estudio se obtuvo un menor porcentaje de muestras positivas con la t (9;22), que en otros estudios reportados por diferentes autores.12-14 A pesar de estos resultados, la aplicación del FISH pudo definir la presencia o ausencia de esta translocación, lo que facilitó el diagnóstico diferencial entre la LMC y otras neoplasias mieloproliferativas Ph negativas, pues muchos de los pacientes presentaron trombocitosis y leucocitosis al debut y los estudios de citogenética convencional fueron no útiles. Esta alteración cromosómica se presenta también en alrededor del 5 % de los pacientes pediátricos con LLA y se asocia a un pronóstico desfavorable, lo cual cambió desde el surgimiento de los inhibidores tirosinquinasa como el imatinib, nilotinib, entre otros. Cuando estos medicamentos se administran a pacientes con LLA Ph+ se plantea que el rango de remisión completa es mayor del 90 % y la supervivencia libre de eventos es superior que la de los controles históricos.15
La LPM se caracteriza por la presencia de la translocación recíproca t(15;17) en alrededor del 90 % de los pacientes. Esta translocación da lugar a la formación del gen de fusión PML/RAR? en el cromosoma 15 derivativo y tiene implicación pronóstica, ya que estos pacientes muestran mejor respuesta al tratamiento con ácido todo trans-retinoico.16 Todas las muestras de los pacientes al debut de la enfermedad resultaron positivas, lo cual coincide con otros estudios internacionales.17, 18 En el 10 % de los pacientes están descritas inserciones crípticas que no son visibles con la citogenética convencional, por lo que el FISH constituye una herramienta útil en el diagnóstico de la LPM.
En el 2 % de los casos existen translocaciones que incluyen rearreglos del gen RAR? con otros genes, como las t(11;17),t(5;17).18 En las muestras negativas a la t(15;17) pudieran estar presentes algunas de estas translocaciones lo cual no pudo precisarse por disponer de esas sondas fluorescentes. ]]>
La t(8;21) fue la primera alteración citogenética descrita en la LMA. Representa un subtipo particular en la clasificación de la OMS del 2008 con características clínicas y biológicas específicas, asociada a un pronóstico favorable. En este estudio se presentó en el 10 % de la muestra, lo cual coincide con la literatura que reporta una frecuencia entre el 5 y el 10 % en este tipo de leucemia,3, 19 La detección de esta translocación es esencial para el manejo óptimo de estos pacientes y su implicación en el diagnóstico, pronóstico y tratamiento.20
En la LLC existe un bajo índice mitótico in vitro de las células leucémicas, aun con la utilización de mitógenos. La técnica de FISH es capaz de superar esta dificultad, por lo que se convierte en una herramienta muy factible para la detección de alteraciones cromosómicas. Esto permite el establecimiento de grupos de riesgo citogenético, entre los que se destacan las deleciones: 13q14.3 asociada a buen pronóstico y 17p13 de pronóstico desfavorable.21, 22 En la literatura se reporta como alteración citogenética más frecuente la deleción 13q, en alrededor del 55 % de los pacientes y en el 7 % la deleción17p.23 Sin embargo, en el presente estudio no se encontró ninguna alteración citogenética en los pacientes con diagnóstico de LLC, lo que puede deberse al limitado número de la muestra.
La evaluación citogenética en los SMD reviste importancia por su implicación pronóstica, basado en el IPSS (del inglés: International Prognostic Scoring System) descrito en 199724 y su revisión en el 2012 (IPSS- R). 25
La deleción heterocigótica intersticial del cromosoma 5q (del5q) es una de las alteraciones citogenéticas más comunes, reconocida como un subtipo en la clasificación de la OMS. Esta deleción se asocia con un fenotipo clínico característico y una sensibilidad terapéutica a la lenalidomida. Con el uso del FISH se pudieron localizar dos regiones críticas que intervienen en la hematopoyesis, la 5q31 y 5q 32-33.26
La segunda alteración más frecuente en los SMD es la monosomía del cromosoma 7, en alrededor del 25 %, se puede presentar como una monosomía total con peor pronóstico o como una deleción del brazo largo (del 7q) con pronóstico intermedio. Se reportan tres regiones la 7q 22 y dos más teloméricas la 7q 31-32 y 7q 36, en las cuales están mapeados genes supresores de tumores.27 ]]>
Varios estudios multicéntricos reportan la presencia de alteraciones citogenéticas y su implicación pronóstica,28-30 lo cual concuerda con los resultados de este estudio en el que se observó una del 7q, a pesar de lo pequeño de la muestra.
La aplicación del análisis citogenético en el estudio de los SMD aporta datos de valor pronóstico con importantes implicaciones clínicas y terapéuticas, por lo que se sugiere la necesidad de realizar el cariotipo en el momento del diagnóstico y durante la evolución de la enfermedad.
A pesar de que la muestra estudiada es pequeña, resulta de gran importancia la incorporación de la técnica de FISH como una herramienta más en el diagnóstico de las neoplasias hematológicas. Lo anterior viene dado por las ventajas que presenta respecto a la citogenética convencional como: la mayor rapidez y sensibilidad, su especificidad y la posibilidad de analizar un mayor número de células. Hasta donde se conoce, estos son los primeros resultados obtenidos de la aplicación de esta técnica en el estudio de las leucemias en Cuba.
REFERENCIAS BIBLIOGRÁFICAS
1. Herrera JC, Ramírez GC, Muñetón CM. Estudio de las aneuploidías del cromosoma 17 y la deleción del gen TP53 en neoplasias hematológicas, por la técnica del FISH-bicolor. Iatrea. 2008 dic;21(4):364-74.
]]>
2. Foppa CE. Aplicações da metodologia fish em citogenética de neoplasias 2009. [citado: marzo 15, 2015].Disponible en: https://repositorio.ufsc.br/bitstream/handle/123456789/132329/20092-CarolinaEFoppa.pdf?sequence=1&isAllowed=y
3. Dohner H, Estey EH, Amadori S, Appelbaum FR, Buchner T, Burnett AK, et al. Diagnosis and management of acute myeloid leukemia in adults: recommendations from an international expert panel, on behalf of the European Leukemia. Blood. 2010 Jan;115(3):455-73.
4. García JA, Giraldo P, López J, Ríos E, Sastre JL, Terol MJ, et al. Guía de consenso nacionales para el estudio y tratamiento de los pacientes con leucemia linfocítica crónica. Med Clin (Barc) 2013;141(4):175.e1-e8.
5. Codispoti KET, Depalma L. Myelodsplastic syndrome in elderly patients: correlation of CBC with cytogenetic and FISH analysis. Int J Lab Hematol. 2010 Aug;32(4):443-8.
6. Alfaro J, Legues M, Grebe G. Técnicas de Citogenética. En Hematología. Técnicas y procedimientos de laboratorio. Guido Osorio (ed). Santiago de Chile: Publicaciones Técnicas Mediterráneo; 1996. p.159-68.
]]>
7. Espinet B, Salido M, Solé F. Técnicas de citogenética molecular y sus aplicaciones. Utilidad de la citogenética en el estudio de las neoplasias.Laboratori de Citogenètica i Biologia Molecular. Servei de Patologia. Hospital de Mar de Barcelona. [citado: marzo 15, 2015]. Disponible en:http://www.seapcongresos.com/2005/Cursos/Curso_Largo_Patologia_Molecular/Citogenetica_molecular.PDF.
8. Solé F. Bases técnicas del FISH. Servei de Patologia. Laboratori de Citogenètica i Biología Molecular Hospital del Mar. Barcelona. [citado: marzo 15, 2015]. Disponible en: https://www.seap.es/c/document_library/get_file?uuid=065873b3-02a9-452f-9b49-605a3ebcbddd&groupId=10157
9. Simons A, Shaffer LG, Hastings RJ. Cytogenetic Nomenclature: Changes in the ISCN 2013 compared to the 2009 edition. Cytogenet Genome Res. 2013;141(1):1-6.
10. Hu L, Ru K, Zhang L, Huang Y, Zhu X, Liu H, et al. Fluorescence in situ hybridization (FISH): an increasingly demanded tool for biomarker research and personalized medicine. Biomark Res. 2014 Feb 5;2(1):3.
11. Jabbour E, Kantarjian H. Introduction: chronic myelogenous leukemia (CML). Semin Hematol. 2007;44(Suppl 1):S1-S3.
]]>
12. Choi HJ, Kim HR, Shin MG, Kook H, Kim HJ, Shin JH, et al. Spectra of Chromosomal Aberrations in 325 Leukemia Patients and Implications for the Development of New Molecular Detection Systems. Korean Med Sci. 2011 Jul;26(7):886-92.
13. Dávila MI, Cerda RM, Leal CH, Arana RM, Báez E, Cortés EI. Alteraciones cromosómicas secundarias en pacientes con leucemia mieloide crónica, en un hospital de referencia del noreste de México. Gac Méd Méx. 2004 Nov-Dic;140(6):589-92.
14. Seong CM. Monitoring the course of chronic myelogenous leukemia by FISH. Int J Hematol. 2002 Aug;76:53-7.
15. Marzocchi G, Castagnetti F, Luatti S, Baldazzi C, Stacchini M, Gugliotta G, et al. Variant Philadelphia translocations: molecular-cytogenetic characterization and prognostic influence on frontline imatinib therapy, a GIMEMA Working Party on CML analysis. Blood. 2011 Jun;117(25):6793-800.
16. Avvisati G, Lo Coco F, Paoloni FP, Petti MC, Diverio D, Vignetti M, et al. AIDA 0493 protocol for newly diagnosed acute promyelocytic leukemia: very long-term results and role of maintenance. Blood. 2011May;117(18):4716-25.
]]>
17. Campbell LJ, Oei P, Brookwell R, Shortt J, Eaddy N, Ng A, et al. FISH Detection of PML-RARA Fusion in ins(15;17) Acute Promyelocytic Leukaemia Depends on Probe Size. Biomed Res Int. 2013 Mar;2013:1-4 doi: 10.1155/2013/164501
18. Sagrillo MR, Cardoso SH, Silva L, Graça C, Ferreira E, Hamerschlak N, et al. Leucemia promielocítica aguda: caracterização de alterações cromossômicas por citogenética tradicional e molecular (FISH). Rev Bras Hematol Hemoter. 2005;27(2):94-101
19. Reikvam H, HatfieldKJ, KittangAO, Hovland R, BruserudØ. Acute Myeloid Leukemia with the t(8;21) Translocation: Clinical Consequences and Biological Implications. J Biomed Biotechnol. 2011 May; 2011:1-23 doi: 10.1155/2011/104631
20- Harrison CJ, Hills RK, Moorman AV, Grimwade DJ, Hann I, Webb DK, et al. Cytogenetics of childhood acute myeloid leukemia: United Kingdom Medical Research Council Treatment Trials AML 10 and 12. J Clin Oncol. 2010 Jun;28(16):2674-81.
21. Travella A,Bezares R, Rodríguez A, Slavutsky I. Anomalías cromosómicas estructurales nuevas en leucemia linfocítica crónica. Su valor pronóstico. Hematología. 2012 Ene- abril;16(1):8-19.
]]>
22. Greipp PT, Smoley SA, Viswanatha DS, Frederick LS, Rabe KG, Sharma RG, et al. Patients with chronic lymphocytic leukaemia and clonal deletion of both 17p13.1 and 11q22.3 have a very poor prognosis. Br J Haematol. 2013 Nov;163(3):326-33.
23. Cantú ES, McGill JR, Stephenson CF, Hoffmann HM, Tang L, Yan J, et al. Male - to- female Sex ratios of abnormalities detected by fluorescence in situ hybridization in a population of chronic lymphocytic leukemia patients. Hematol Rep. 2013 Jan;5(1):13-7.
24. Greenberg P, Cox C, LeBeau MM, Fenaux P, Morel P, Sanz G, et al. International scoring system for evaluating prognosis in myelodysplastic syndromes. Blood. 1997 March;89(6):2079-88.
25. Greenberg P, Tuechler H, Schanz J, Sanz G, Garcia- Manero G, Solé F, et al. Revised international prognostic scoring system for myelodysplastic syndromes. Blood. 2012 Sep;120(12):2454-65.
26. Komrokji RS, Padron E, Ebert BL, List AF. Deletion 5q MDS: molecular and therapeutic implications. Best Pract Res Clin Haematol. 2013 Dec;26(4):365-75.
]]>
27. Haase D. Cytogenetic features in myelodysplastic syndromes. Ann Hematol. 2008 Jul;87(7):515-526.
28. Schanz J, Steidl C, Fonatsch C, Pfeilstocker M, Nosslinger T, Tuechler H, et al. Coalesced multicentric analysis of 2,351 patients with myelodysplastic syndromes indicates an underestimation of poor-risk cytogenetics of myelodysplastic syndromes in the internation al prognostic scoring system. J Clin Oncol. 2011 May;29(15):1963-70.
29. Pozdnyakova O, Miron PM, Tang G, Walter O, Raza A, et al. Cytogenetic abnormalities in a series of 1,029 patients with primary myelodysplastic syndromes: a report from the US with a focus on some un defined single chromosomal abnormalities. Cancer. 2008 Dec;113(12):3331-40.
30. Schanz J, Tüchler H, Solé F, Mallo M, Luño E, Cervera J, et al. New comprehensive cytogenetic scoring system for primary myelodysplastic syndromes (MDS) and oligoblastic acute myeloid leukemia after MDS derived from an international database merge.J Clin Oncol. 2012 Mar 10;30(8):820-9.
]]> Recibido: mayo 28, 2015.
Dra. Kalia Lavaut Sánchez. Instituto de Hematología e Inmunología. Apartado 8070, La Habana, CP 10800, CUBA. Tel (537) 643 8695, 8268
Email: rchematologia@infomed.sld.cu