Histocompatibilidad de donantes haploindénticos para el trasplante de células progenitoras hematopoyéticas
Histocompatibility of haploindénticos donor for hematopoietic progenitor cells transplantation
Antonio A. Bencomo Hernández, María GuiliaYavi Andia, Arturo Chang Monteagudo, Luz M. Morera Barrios, Catalino R. Ustáriz García
Instituto de Hematología e Inmunología. La Habana, Cuba.
]]>
RESUMEN
Introducción: El trasplante es una alternativa para lograr la curación de los pacientes con hemopatías. La reducción en el número de hijos por pareja a nivel mundial ha acrecentado la necesidad de abordar el trasplante HLA haploidéntico.
Objetivo: Caracterizar la compatibilidad a nivel de antígenos y epítopes HLA a receptores y donantes para el trasplante haploidéntico de progenitores hematopoyéticos.
Métodos: Se estudiaron 215 receptores cubanos, 95 femeninos y 120 masculinos y 313 hermanos. Se estudiaron también las madres en 95 casos y los padres en 73.
Resultados: En el locus B se observó el mayor número de incompatibilidades de clase I. En la clase II, el DRB1 fue significativamente superior al DQ. El menor número de eplets incompatibles se observó entre los receptores con el padre y las incompatibilidades menores de 10 eplets fueron más frecuentes con la madre. Al considerar la compatibilidad de eplets en los loci B y DRB1, más del 45 % de los donantes haploidénticos fueron compatibles en epítopes con el receptor. En 34 receptores de 215 (15,8 %) se identificaron donantes con compatibilidad total de epítopes HLA de clase I, II o ambos.
Conclusiones: Entre los receptores cubanos de trasplante haploidéntico de progenitores hematopoyéticos y sus posibles donantes pueden encontrase parejas con alta compatibilidad a nivel de antígenos y epítopes del sistema HLA, por lo que esta caracterización pudiera incluirse en los algoritmos de selección.
Palabras clave: antígenos HLA-A; antígenos HLA-B; antígenos HLA-DR; antígenos HLA-DQ; sitios genéticos ; trasplante haploidéntico.
ABSTRACT
Introduction: The transplant is an alternative to achieve the healing of patients with haemopathies. The reduction in the number of siblings worldwide has increased the need to address haploidentical HLA transplantation.
Objective : To characterize the compatibility at the level of antigens and HLA epitopes to receptors and donors for the haploidentical transplantation of hematopoietic progenitors. Methods: 215 recipients, 95 female and 120 male and 313 siblings were studied. Mothers were also studied in 95 cases and parents of 73 recipients.
Results: In the B locus the highest number of class I incompatibilities was observed. In class II, DRB1 was significantly superior to DQ. The lowest number of incompatible eplets was observed between the recipients with the father and the incompatibilities less than 10 eplets were more frequent with the mother. When considering the compatibility of eplets in loci B and DRB1, more than 45% of haploidentical donors are epitopes compatible with the receptor. In 34 recipients of 215 (15.8%), donors were identified with total compatibility of HLA class epitopes. I, II or both. These results should be considered for the preparation of an algorithm for the selection of donors in haploidentical transplantation.
Conclusions : Among the Cuban recipients of haploidentical transplantation of hematopoietic progenitors and their possible donors can be found couples with high compatibility at the level of antigens and epitopes of the HLA system, so this characterization could be included in the selection algorithms.
Keywords: HLA-A antigens; HLA-B antigens; HLA-DR antigens; HLA-DQ antigens; genetic loci ; transplantation, haploidentical.
La introducción de las técnicas de biología molecular ha provocado un impacto en el mundo científico y específicamente en el estudio del complejo principal de histocompatibilidad (CPH), creando una revolución en el campo del trasplante de órganos y tejidos, en el diagnóstico de enfermedades y otras aplicaciones básicas. 1 Los genes del CPH se localizan en el brazo corto del cromosoma 6 y codifican en el humano los antígenos del sistema HLA (del inglés, human leukocyte antigens). Estos antígenos se expresan principalmente en las membranas de las células nucleadas. 2-5
La tipificación del sistema HLA desempeña una función muy importante en la medicina contemporánea. Las moléculas HLA son el objetivo principal de las respuestas inmunitarias a los trasplantes alogénicos, son elementos esenciales para las respuestas a estímulos antigénicos y se implican además en la susceptibilidad genética a padecer enfermedades autoinmunes. Una de las características cardinales de las moléculas del sistema HLA es su diversidad en la población humana. La tipificación del HLA detecta y clasifica tal diversidad.1
Las moléculas HLA son proteínas especializadas codificadas por genes presentes en un locus denominado CPH. Los genes del CPH se expresan de forma codominante y en un individuo se expresan las moléculas del CPH heredadas de ambos padres. Este sistema se hereda en bloques por lo que una persona tendrá la mitad de cada progenitor, que es denominada haplotipo, y que constituye el conjunto de moléculas del CPH presente en cada cromosoma.
El que dos hermanos sean o no HLA idénticos depende de las leyes mendelianas de la herencia: hay 25 % de probabilidades de compartir los dos haplotipos y por tanto de ser HLA idénticos, 50 % de compartir un haplotipo y ser HLA haploidénticos y 25 % de no compartir ningún haplotipo.6 Cada molécula del HLA recibe una designación numérica. Por ejemplo, un haplotipo HLA de un sujeto podría ser HLA-A*02, HLA-B *05, HLA-C*01, HLA-DRB1*03, HLA-DQB1*02, HLA-DPB1*06.7
Desde hace unos años se ha producido un progreso espectacular en el estudio del polimorfismo HLA a nivel genético. A partir del año 2012 se introdujeron en el país las técnicas moleculares de tipificación HLA en los estudios familiares, para la identificación de posibles donantes relacionados para el trasplante de progenitores hematopoyéticos (TPH).7 El uso de métodos moleculares, amplía el conocimiento del polimorfismo HLA, de modo que permite saber con precisión el grado de disparidad entre donante y receptor. Una mejor identificación de los diferentes alelos sirve para elegir las parejas donante-receptor con el mayor nivel de compatibilidad posible.
Por otra parte, los estudios moleculares han permitido dilucidar las estructuras de los sitios antigénicos de las moléculas HLA conocidos como eplets y el grado de similitud o disparidad entre los diferentes antígenos. De esta forma y a partir del programa informático HLA Matchmaker puede identificarse el grado de disparidad o no entre antígenos para una mejor selección de los posibles donantes.
El HLA Matchmaker es un programa estructurado de compatibilidad que considera cada antígeno HLA como un epítope representado por una secuencia de aminoácidos o tripletes presentes en los residuos de aminoácidos de la porción inmunogénica reconocida por los anticuerpos. Al considerarse el eplet s como el epítope funcional, las diferencias en eplets entre los donantes y receptores es una medida de la compatibilidad de epítopes HLA.8, 9
Los estudios han demostrado que las diferencias en un gran número de eplets entre donante y receptor se asocian con menores sobrevida en el trasplante renal incluida la producción de anticuerpos que median el rechazo del órgano.10 De acuerdo a estos resultados la compatibilidad de eplets se utiliza en la actualidad en el programa de trasplante renal en Europa y Australia.11,12 La aplicación en la selección de donantes para el TPH es limitada sin resultados concluyentes.8
En este trabajo se caracteriza la compatibilidad a nivel de antígenos y epítopes HLA a receptores y donantes para el trasplante haploidéntico de progenitores hematopoyéticos.
]]>MÉTODOS
Se realizó un estudio ambispectivo de tipo observacional de todos los pacientes de Cuba y familiares, con indicación de estudios de histocompatibilidad para posible TPH en el período comprendido entre enero de 2013 y agosto de 2017. Se incluyeron 215 receptores con un rango de edad de 2 a 60 años, 95 femeninos y 120 masculinos; 313 hermanos, 95 madres, 73 padres y 5 otros familiares.
La colección de la muestra se realizó de sangre periférica en tubos con EDTA. Las muestras se procesaron en centrífugas refrigeradas a 1150 g por 10 min a 22oC, para obtener la capa de leucocitos (buffy coat) a partir de la cual se realizó el aislamiento de ADN en equipo QIAcube (QIAGEN, GmbH). La concentración de ADN se determinó por el método espectrofotométrico en equipo Epoch (Biotek Instruments Inc) que fue ajustada a 30 ng/mL.
La tipificación molecular HLA de los loci A, B, DR y DQ se realizó con el estuche de baja resolución Olerup SSP HLA A B DR DQ SSP Combi tray y los correspondientes estuches de alta resolución Olerup SSP para los casos en que no fuera posible la correcta identificación de los haplotipos en el estudio familiar.
La amplificación se realizó en termocicladores Q-CYcler II ( Quanta Biotech LTd), mediante el programa recomendado por el fabricante. La lectura de la amplificación se realizó por electroforesis capilar en equipo QIAxcel Advance (QIAGEN, GmbH), con el uso del cartucho Qiaxcel DNA FastAnalysis kit (QIAGEN, GmbH). La interpretación de los resultados se realizó a través de la presencia de la amplificación de la banda específica y con el uso del software Helmberg-Score (Olerup).
Los resultados de la tipificación HLA molecular de los loci A, B, DR y DQ se expresaron según la nueva nomenclatura aceptada 13 y fueron registrados en una base de datos en formato Microsoft Access, en conjunto con la información obtenida en la planilla de recolección de datos que contenía la información siguiente: nombres y apellidos, edad, sexo, color de la piel, número de identidad personal, dirección, número de trasfusiones, trasplantes anteriores, embarazos y enfermedades asociadas.
El estudio se realizó de acuerdo con la última revisión de la Declaración de Helsinki, que establece los principios éticos para las investigaciones médicas en seres humanos. 14,15
Determinación de incompatibilidades en eplets
La estimación se realizó con el Software-HLA Matchmaker versión 1.4 ( www.HLAMatchmaker.net ) con estimación de 4 dígitos a partir de la tipificación HLA de baja resolución por frecuencia poblacional, de acuerdo a lo sugerido en el mismo programa. Se analizaron las incompatibilidades a partir del HLA del receptor y el de los posibles donantes.
]]> Análisis estadísticoSe utilizó la prueba de chi-cuadrado para la comparación de frecuencias absolutas. Se consideró significativo un valor de p <0,05.
RESULTADOS
Entre los pacientes con indicación de TPH predominaron las hemopatías malignas y dentro de ellas la más frecuente fue la leucemia mieloide aguda (tabla 1).
En el estudio de compatibilidad predominaron los donantes haploidénticos y no idénticos y en menor medida los HLA idénticos. En un caso se encontró total identidad HLA con la madre (tabla 2).
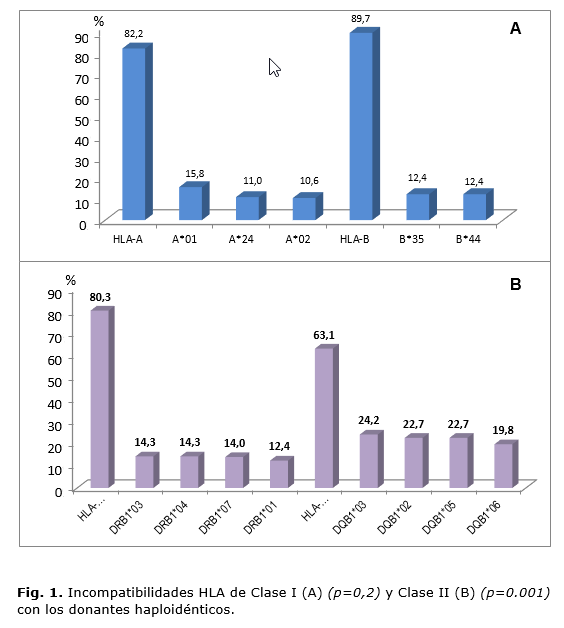
El mayor número de incompatibilidades entre los receptores con los donantes haploidénticos se observaron en los loci de clase I y dentro de estos en el locus B, aunque las diferencias no fueron significativas con respecto al locus A. Los antígenos donde se observaron el mayor número de incompatibilidades fueron el A*01, *24, B*35, y B*44 (Fig. 1A).
Para los loci de clase II, en el DRB1(DRB1*03,*04,*07), se encontraron las diferencias más importantes que fueron significativamente más frecuentes con respecto al DQ (DQB1 *02,*03,*05) (Fig. 1B).
La frecuencia mayor de eplets compatibles (0-5) se observó entre los receptores con el padre. Sin embargo, las incompatibilidades menores de 10 eplets fueron más frecuentes con la madre en relación con el padre o los hermanos haploidénticos (p=0,01)(Fig. 2A).
]]> En la comparación de los eplets únicamente entre los loci B y DRB1 no hubo diferencias entre los hermanos con los padres. Al considerar la compatibilidad de eplets en estos loci, más del 45 % de los donantes haploidénticos son epítopes compatibles con el receptor (Fig. 2B).En 34 receptores de 215 (15,8 %) se identificaron donantes con compatibilidad total de epítopes HLA de clase I, II, o ambos, o sea sin diferencias de eplets. Predominaron los compatibles de clase II en 15 receptores y en menor proporción los de clase I, o ambos. La identidad de epítopes fue más frecuente con los hermanos que con los parentales. El 67 % de estos receptores presentaban alelos HLA homocigóticos (tabla 3).
DISCUSIÓN
El TPH es un tratamiento potencialmente curativo para muchos pacientes afectados por trastornos hematológicos. Sus principales indicaciones son las leucemias, los linfomas y las insuficiencias de la médula ósea.16 Dentro de estas, la leucemia mieloide aguda es una de las más frecuentes debido al pronóstico desfavorable con los tratamientos convencionales.17 Estos hallazgos coinciden con los encontrados en el grupo de pacientes analizados con estudios de compatibilidad para TPH.
La frecuencia de compatibilidad HLA entre receptores y donantes se corresponde con lo comunicado en la literatura con relación a la proporción menor de donantes relacionados HLA idénticos y no idénticos y mayor de haploidentidad.6 No obstante, debido a la inclusión de los parentales y de otros familiares en el estudio, la frecuencia de donantes haploidénticos fue superior a lo esperado si solo se hubieran incluido los hermanos.
La búsqueda de un donante relacionado compatible para el trasplante, comúnmente hermano HLA idéntico, es la variante tradicionalmente más deseada, pero es cada vez más escasa debido a la tendencia internacional y, en Cuba, a la disminución del número de hijos.
El trasplante con donante haploidéntico es la opción más frecuente y la que se está desarrollando en especial después que se demostró la eficacia de la administración de altas dosis de ciclofosfamida postrasplante para el control de la enfermedad de injerto contra huésped (EICH). 18 De esta forma, en este trabajo se profundiza en la en la caracterización de la compatibilidad HLA con este tipo de donantes.19
Las incompatibilidades más frecuentes con los donantes haploidénticos a nivel de antígenos HLA se encontraron en el locus B y DRB1. Este resultado es importante si se tiene en cuenta que son los loci donde se recomienda la mayor compatibilidad para evitar la EICH.3 Otros estudios comunican hallazgos similares. 20 Los antígenos de clase I y II donde se observaron las incompatibilidades más comunes coinciden con los de mayor frecuencia descritos en la población cuabana.21
Teniendo en cuenta estos resultados, se caracterizaron las incompatibilidades a nivel de epítopes (eplets) que esclarece las diferencias o no en las estructuras antigénicas que podrían influenciar la alorreactividad bidireccional entre receptor e injerto y de esta forma considerar HLA eplets compatibles a donantes con incompatibilidad HLA.8
]]> Las incompatibilidades menores de 10 eplets se consideran aceptables para evitar una respuesta inmune HLA específica.22 Los resultados más alentadores se han obtenido en la selección de donantes para el trasplante renal cadavérico y constituye una herramienta cada vez más usada para la selección de donantes renales a receptores hipersensibilizados, donde la búsqueda de la compatibilidad es crucial por la presencia de anticuerpos en el receptor contra antígenos HLA del órgano a trasplantar que median el rechazo agudo.23En este estudio, las menores incompatibilidades en eplets (0-5) se encontraron con el padre, lo que lo señala como una opción a valorar en la población cubana para el trasplante haploidéntico en ausencia de donantes relacionados compatibles. Hasta donde se conoce no se ha realizado estudios que evalúen la compatibilidad paterna en eplets que pudieran confirmar o polemizar estos resultados.
No obstante, las incompatibilidades en eplets menores de 10 se encontraron con la madre y con los hermanos haploidénticos. La madre es una opción preconizada en muchos estudios donde se obtuvieron mayor sobrevida postrasplante y menor incidencia de EICH.24
Estos resultados se atribuyen al efecto NIMA (del inglés, Non Inherited maternal antigens) o antígenos maternos no heredados, para los cuales los hijos presentarían tolerancia por su exposición en la etapa fetal vía cordón umbilical y postnatal a través de la leche materna.25 Los hermanos haploidénticos NIMA compatibles o con presencia de antígenos maternos no heredados por el receptor a trasplantar también pudieran ser una elección ventajosa.
En el análisis de la compatibilidad de eplets únicamente de los loci B y DRB1se encontró que en casi la mitad de los receptores se puede identificar un donante relacionado con compatibilidades menores de 10 que podría ser una primera selección en el algoritmo de estudio de los donantes relacionados haploidénticos.
En términos de identidad antigénica la ausencia de diferencias en eplets o con resultados "0" podría considerarse como HLA compatible aun en presencia de diferentes antígenos. Esto es debido a que a pesar que el sistema HLA es el más polimórfico presenta gran homología y la diversidad está dada por cambios en algunos residuos de la cadena de aminoácidos que en su estructura tridimensional forma los epítopes reconocibles por el sistema inmune. 26
En el 15 % de los receptores se identificaron donantes HLA eplets totalmente compatibles con mayor frecuencia para los antígenos de clase II, resultados esperados por ser los antígenos de clase I los más polimórficos;13 y con una mayor proporción entre los receptores homocigóticos ya que las diferencias estarían solo en base a un antígeno con una mayor probabilidad de encontrar identidad.
Los resultados de este trabajo muestran las complejidades en el estudio de la compatibilidad HLA en el trasplante haploidéntico y aportan herramientas para la selección de los donantes y así garantizar la mejor compatibilidad en aras de disminuir la EICH.
REFERENCIAS BIBLIOGRÁFICAS
]]>1. Mahdi BM. A glow of HLA typing in organ transplantation. ClinTransl Med. 2013;2(1):6.
2. Marsh SG, Albert ED, Bodmer WF, Bontrop RE, Dupont B, Erlich HA, et al. Nomenclature for factors of the HLA system, 2010. Tissue Antigens. 2010 Apr;75(4):291-455.
3. Abbas AK, Lichtman AH, Pillai S. Major Histocompatibility Complex Molecules and Antigen Presentation to T Lymphocytes. Cellular and molecular immunology. 7th ed. Philadelphia: Elsevier/Saunders; 2010. p. 109-38.
4. Erlich H. HLA DNA typing: past, present, and future. Tissue Antigens. 2012 Jul;80(1):1-11.
5. Kelley J, Walter L, Trowsdale J. Comparative genomics of major histocompatibility complexes. Immunogenetics. 2005 Jan;56(10):683-95.
]]>6. Parslow TG, Stites DP, Terr A, Imboden J. Presentación de antígenos y complejo principal de histocompatibilidad. Inmunología básica y clínica. 10 ed. México D.F: El manual moderno; 2007 p. 93-108.
7. Bencomo-Hernández A. A propósito del primer año del Centro de Ingeniería Celular y Trasplante de Órganos y Tejidos (CICEL). Rev Cubana Hematol Inmunol Hemoter.2014; 30(3): 192-5.
8. Duquesnoy RJ. Antibody-reactive epitope determination with HLA Matchmaker and its clinical applications. Tissue Antigens 2011; 77, 525-34.
9. Silva E, Alba A, Castro A, Carrascal M, Buckel E, Aguiló J. Evaluation of HLA Matchmaker Compatibility as Predictor of Graft Survival and Presence of Anti-HLA Antibodies. Transplant Proceed. 2010, 42; 266-9
10. Sapir-Pichhadze R, Tinckam K, Quach K, Logan AG, Laupacis A, John R, et al. HLA-DR and -DQ eplet mismatches and transplant glomerulopathy: a nested case-control study. Am J Transplant. 2015; 15:137-48.
11. Duquesnoy RJ, Witvliet M, Doxiadis II, de Fijter H, Claas FH. HLA Matchmaker-based strategy to identify acceptable HLA class I mismatches for highly sensitized kidney transplant candidates. Transplant Int. 2004; 17:22-30.
12. Sypek MP, Alexander SI, Cantwell L, Ierino FL, Ferrari P, Walker AM, et al. Optimizing Outcomes in Pediatric Renal Transplantation Through the Australian Paired Kidney Exchange Program. Am J Transplant . 2017; 17:534-41.
13. Marsh SG. Nomenclature for factors of the HLA system, update June 2016. Int J Immunogenet. 2016 Oct;43(5):320-9. doi: 10.1111/iji.12284
14. World Medical Association (AMM). Helsinki Declaration. Ethical principles for medical research involving human subjects. Assist Inferm Ric. 2001 Apr-Jun;20(2):104-7.
15. WMA. Declaration of Helsinki. Ethical Principles for Medical Research Involving Human Subjects. 2011 [updated 2011 2008 Oct; cited 2011 Jan 15]; Available from: http://www.wma.net/en/30publications/10policies/b3/17c.pdf .
16. Apperley J, Niederwieser D, Huang XJ, Nagler A, Fuchs E, Szer J, et al. Haploidentical hematopoietic stem cell transplantation: A global overview comparing Asia, the European Union, and the United States. Biol Blood Marrow Transplant. 2016; 22(1):23-6.
]]>17. Wang Y, Liu QF, Xu LP, Liu KY, Zhang XH, Ma X, et al. Haploidentical vs identical-sibling transplant for AML in remission: a multicenter, prospective study. Blood. 2015;125(25):3956-62.
18. McCurdy SR, Kanakry JA, Showel MM, Tsai HL, Bolaños-Meade J, Rosner GL et al. Risk-stratified outcomes of nonmyeloablative HLA-haploidentical BMT with high-dose posttransplantation cyclophosphamide. Blood 2015;125(19):3024-31.
19. Kollman C, Spellman S, Zhang M. The effect of donor characteristics on survival after unrelated donor transplantation for hematologic malignancy. Blood. 2016; 127:260-67.
20. Lazaryan A, Wang T, Spellman SR, Wang HL, Pidala J, Nishihori T, et al. Human leukocyte antigen supertype matching after myeloablative hematopoietic cell transplantation with 7/8 matched unrelated donor allografts: a report from the Center for International Blood and Marrow Transplant Research. Haematologica. 2016;101(10): 1267-74.
21. Morera Barrios LM, Chang Monteagudo A, García García MA, de la Guardia Peña OM, Ustariz García CR, Marcell Rodríguez L, et al. Frecuencia de genes HLA en pacientes con insuficiencia renal crónica, del occidente y centro de Cuba. Rev Cubana HematolInmunolHemoter [Internet]. 2014 [citado 2018 Sep 30];31(1):[aprox. 0 p.]. Disponible en: http://www.revhematologia.sld.cu/index.php/hih/article/view/257 .
]]>22. Wiebe C, Pochinco D, Blydt-Hansen TD, Ho J, Birk PE, Karpinski M, et al. Class II HLA epitope matching-A strategy to minimize de novo donors pecific antibody development and improve outcomes. Am J Transpl. 2013; 13:3114-22.
23. Heidt S, Haasnoot GW, van Rood JJ, Witvliet MD, Claas FHJ. Kidney allocation based on proven acceptable antigens results in superior graft survival in highly sensitized patients. Kidney Int. 2018; 93:491-500.
24. Wang Y, Zhaoa XY, Xu LP, Zhanga XH, HanaW, Chen H, et al. Lower incidence of acute GVHD is associated with the rapid recovery of CD4+CD25+CD45RA+regulatory T cells in patients who received haploidentical allografts from NIMA-mismatched donors: A retrospective (development) and prospective (validation) cohort-based study. Oncoimmunol. 2016; 5(12):e1242546.
25. Molitor ML, Haynes LD, Jankowska-Gan E, Mulder A, Burlingham WJ. HLA class I noninherited maternal antigens in cord blood and breast milk. Hum Immunol. 2004;65(3):231-239.
26. Tambur AR. HLA-epitope matching or eplet risk stratification: the devil is in the details. Front Immunol. 2018; 9:02010.
]]>
Recibido: octubre 15, 2018.
Aceptado: noviembre 1, 2018.
Prof. DrC. Antonio Bencomo Hernández . Instituto de Hematología e Inmunología. Calle 19 # 960 e/ 8 y 10. Plaza de la Revolución. La Habana, CP 10400, CUBA.Tel (537) 832 0485/ 846 1112.
Correo electrónico : rchematologia@infomed.sld.cu