INGENIERÍA BIOMÉDICA
Una introducción a la mecanobiología computacional
An introduction to computation mechanobiology
]]>
Ft. Nancy Landinez Parra,I Ing. Diego A. Garzón-Alvarado Ph. D,II Ing. Carlos Alberto Narváez TovarI
I Departamento de Movimiento Corporal Humano, Fisioterapia. Universidad Nacional de Colombia.
II Departamento de Ingeniería Mecánica y Mecatrónica. Facultad de Ingeniería. Universidad Nacional de Colombia.
La mecanobiología estudia el comportamiento de células, tejidos y órganos bajo los efectos de la bioquímica, la biología celular y los estímulos externos, como las cargas mecánicas. Esta involucra el desarrollo de modelos y la realización de experimentos con el objetivo de entender los procesos complejos que se presentan en la génesis y mantenimiento de órganos y tejidos. Mediante esta disciplina se ha logrado aislar y analizar diversos efectos como lo son la genética, los factores moleculares autocrinos y paracrinos, y las cargas mecánicas sobre tejidos y órganos. En esta vía, el presente trabajo muestra los principales desarrollos y aportes de la mecanobiología computacional en el conocimiento médico.
Palabras clave: Mecanobiología, biología, mecánica, computacional, ingeniería, ciencias biomédicas.
Key words: Mechanobiology, biology, mechanics, computation , engineering, biomedical sciences.
INTRODUCCIÓN
Durante las últimas décadas se ha experimentado un importante avance en el desarrollo de las computadoras, y con ello, se han implementado nuevas metodologías para la simulación computacional. Con el pasar de las décadas, la tarea de simulación encomendada a los computadores ha incrementado su complejidad, a tal punto, que en algunas ocasiones, los fenómenos complejos de la naturaleza se estudian en un ambiente virtual antes de pasar a la experimentación tradicional. Esta nueva ciencia extendió sus redes para ser aplicada en procesos tan disímiles como la ingeniería estructural, en el cálculo y diseño de puentes y edificios,1 hasta la química molecular, donde se diseñan nuevos fármacos bajo combinaciones hechas en computador.2 Es así cómo un gran esfuerzo científico, académico y gubernamental se ha empleado en desarrollar nuevas máquinas con grandes prestaciones de cómputo3 para el estudio climático,4 militar, aeronáutico,5 entre otros.
Así mismo, entre las muchas áreas del conocimiento en las que se ha extendido la simulación computacional, se puede enumerar la medicina.6 El éxito que albergó el uso de los computadores en resolver problemas complejos de ingeniería permitió a los médicos tener la confianza suficiente para probar hipótesis clínicas, que a la luz de la experimentación, podrían resultar bastante complejos, costosos y éticamente imposibles (ver por ejemplo Boyle C).7 Por tanto, a partir de los principios de los métodos numéricos, las matemáticas y la física se crea un ambiente sinérgico que permite a la simulación computacional esclarecer incógnitas médicas, que de otra manera serían difíciles de resolver. Los principios de la nueva ciencia computacional, en términos de la representación virtual de los aspectos médicos, necesita, además, de los principios biológicos, eléctricos y mecánicos para mejorar sus procedimientos clínicos y desarrollar nuevos tratamientos. ]]>
La principal herramienta de la medicina ha sido la biología. Con las ciencias biológicas la medicina ha logrado explicar el comportamiento de células, tejidos y órganos.8 Por ejemplo, los principios fundamentales de biología celular vegetal y animal, se han extrapolado al comportamiento humano. La tangencia de la biología y la medicina ha logrado activar líneas de investigación con objetivos comunes, que a la luz del siglo XXI se denomina ingeniería de tejidos,9 y que pretende explicar el comportamiento de células y tejidos (naturales y artificiales) bajo la acción de efectos físicos externos. En esta nueva rama del conocimiento se involucra además, la biología molecular, la química farmacéutica, las matemáticas, la física y, también, por supuesto, la simulación computacional.10
Alternativamente, desde muchos siglos atrás, la física y la ingeniería han estado en constante contacto con la medicina a través de importantes científicos, como Galileo y Newton, entre otros.11 La búsqueda de científicos y médicos por mejorar tratamientos y entender las patologías con mayor precisión, desarrollaron un mayor grado de conocimiento en la medicina con ayuda particular de diferentes áreas de la física, ingeniería y biología. Es así como aparecen las especialidades en la medicina, que tienen una importante comunicación con las ciencias básicas, como es el caso de la neurología, que hace uso de la teoría de conducción y campo eléctrico, la oftalmología, que hace uso de los principios de la óptica, dentro de una larga lista de especialidades. Cada rama de especialidad de la medicina se encarga de estudiar a profundidad un fenómeno físico que se presenta de manera habitual en un sistema, órgano o tejido.
En particular, la mecánica clásica y la ingeniería mecánica han establecido vínculos indisolubles con la ortopedia y la traumatología.12 Desde el punto de vista del tejido, la ingeniería mecánica estudia el comportamiento de los materiales que conforman el hueso,13 participa en el diseño de nuevos materiales sustitutos, estudia la cinemática del movimiento del esqueleto, entre otras aplicaciones. Además, la mecánica del continuo ha estudiado el comportamiento de cada pieza del esqueleto ante fuerzas externas, restricciones mecánicas y posibles lesiones.14 Por ejemplo, cuando se generan lesiones importantes en los huesos, como por ejemplo la fractura, el diseñador y el ingeniero en conjunto con el cuerpo médico establecen las posibles soluciones, que son denominadas, prótesis (exógenas y endógenas), y que requieren de un estudio formal de ingeniería.15 Por tanto, el objetivo de esta conjugación es elevar la calidad de vida de quien padece lesiones óseas, por lo que se requiere entonces, de un grupo multidisciplinario cuyo objetivo es la búsqueda de mejores tratamientos y desarrollar prótesis funcionales y estéticas. Estos procedimientos, rápidamente se ramificaron en otras tantas especialidades médicas y la odontología.16
Rápidamente, la ingeniería mecánica y la medicina, en especial la ortopedia, desarrollaron la biomecánica.17 Esta nueva rama del conocimiento tiene como función la aplicación de la metodología, filosofía y conocimiento de la ingeniería mecánica en la medicina. Con la biomecánica se iniciaron estudios interdisciplinares sobre el comportamiento de los tejidos y órganos ante cargas externas. En especial, se analizaron los estados de esfuerzo y deformación de los huesos, su relación con la geometría, las restricciones y las cargas.18 Estos estudios, se hicieron, inicialmente, de forma analítica, pero rápidamente, con el advenimiento de los computadores, se lograron hacer modelos más sofisticados con ayuda de la mecánica de medios continuos e ingeniería estructural.19 Sin embargo, hasta este momento, los huesos eran modelados como materiales con un comportamiento característico y único en el transcurso de la simulación. Este tipo de acercamiento es típico de la ingeniería, donde se requiere conocer el estado de tensiones y deformaciones en un instante en el tiempo. Conforme se desarrollaban nuevas tecnologías en los computadores y surgían problemas más complejos en la medicina, aparecieron nuevas preguntas de investigación, especialmente, sobre la respuesta que tiene un tejido ante las cargas mecánicas externas.20 Por tanto, la biomecánica computacional abandonó la idea tradicional de estudiar el comportamiento mecánico, para incluir la respuesta del tejido durante el proceso, por lo cual, requería del conocimiento de la respuesta celular y del tejido ante estímulos externos, es decir, requería de la biología.11 Por consiguiente, aparecen las primeras simulaciones de remodelado óseo.21 Durante el proceso del modelado matemático del remodelado óseo se establecieron reglas de comportamiento y respuesta a nivel celular y tejido. Estas reglas determinaron el comportamiento del hueso ante las solicitaciones mecánicas: aumentando la densidad ósea en aquellos sitios de mayor tensión, y disminuyendo la densidad en sitios donde había desuso del hueso.22 Se había conformado la mecanobiología computacional,23 que rápidamente se extendió a diversas aéreas de la medicina.
La mecanobiologia computacional modela los procesos de respuesta de las células, tejidos y órganos ante cargas y estímulos externos.22 El modelado matemático del comportamiento está basado en reglas, muchas de ellas empíricas, hechas bajo la metodología de prueba y error, hasta ajustarlas al comportamiento real de cada fenómeno medico. En este artículo se lleva a cabo una revisión bibliográfica sobre el rol de esta nueva área del conocimiento en el desarrollo de la teoría biológica y medica. Por tanto, el objetivo es hacer una documentación del estado del arte sobre los recientes avances y desafíos de la mecanobiología. ]]>
DESARROLLO
Un paseo breve por la historia de la biomecánica y la mecanobiología
Uno de los primeros científicos en conceptualizar, mediante modelos matemáticos, los fenómenos fisiológicos fue Galileo Galilei (Pisa, 15 de febrero de 1564-Florencia, 8 de enero de 1642).11 Considerado el "Padre de la ciencia", incursionó en casi todas las áreas de la ciencia y las artes, y la medicina no fue la excepción. A partir de sus observaciones sistemáticas, Galileo midió el ritmo cardíaco por comparación de este con los sucesivos sonidos de un péndulo sincrónico.
Utilizando los principios de medida de Galileo, William Harvey (1 de abril de 1578-3 de junio de 1657)11 describió las propiedades de la sangre al ser distribuida por todo el cuerpo a través del bombeo del corazón. Esto confirmó las ideas de René Descartes que en su libro "Descripción del cuerpo humano" afirmó que las arterias y las venas eran tubos que transportaban nutrientes alrededor del cuerpo.11 Debe apuntarse que el español Miguel Servet describió la circulación pulmonar un cuarto de siglo antes que Harvey naciera, por lo que en el libro de Teología (Christianismi Restitutio, publicado en 1553) fue considerado hereje. En consecuencia, casi todas las copias del mismo fueron quemadas, excepto 3 que fueron descubiertas décadas más tarde.24 ]]>
Otro colega de Galileo, Santorio Santorio estudió el fenómeno denominado perspiratio insensibilis (la pérdida de agua en el cuerpo), para lo cual usó una báscula especial de su invención. En el transcurso de algunos años, Santorio registró escrupulosamente el peso del cuerpo en las diferentes horas del día, para medir el balance hídrico, llegando a conclusiones sorprendentemente cercanas a la realidad, si se considera la simplicidad de los instrumentos de que disponía.11
Descartes (31 de marzo de 1596, La Haye en Touraine-11 de febrero de 1650, Estocolmo) sugirió que los sistemas físicos, incluido el cuerpo humano, eran regidos por las mismas leyes universales.11
Leonhard Euler (15 de abril de 1707-7 de septiembre de 1783) utilizó las leyes de Newton (quien escribió sobre el movimiento, pero no sobre biomecánica) para obtener las ecuaciones diferenciales necesarias para describir la propagación de ondas en arterias, investigación que consignó en un artículo publicado en 1775.25
Thomas Young (13 de junio de 1773-10 de mayo de 1829) estudió la formación de la voz humana, la cual identificó con un modelo de elasticidad de materiales. Young también trabajó en la teoría sobre la luz y el color, lo cual le permitió desarrollar lentes para el astigmatismo.
Hermann Ludwig Ferdinand von Helmholtz (31 de agosto de 1821-8 de septiembre, de 1894) es considerado el padre de la bioingeniería. Helmholtz fue profesor de fisiología y patología en diversas universidades, para dedicar sus últimos años a la enseñanza de la física en la Universidad de Berlín. Sus contribuciones abarcan la óptica, acústica, termodinámica, electrodinámica, fisiología y medicina. A partir de sus múltiples conocimientos en fisiología y física, Helmholtz diseñó lentes, calculó la geometría del ojo humano, estudió el mecanismo de audición, determinó la velocidad de un pulso nervioso y mostró que el latido cardíaco es una importante fuente de calor. ]]>
En el siglo XX ya se encuentran numerosos aportes a la concepción matemática del cuerpo humano, entre los que cabe destacar a Archibald Vivian Hill (26 de septiembre de 1886-3 de junio de 1977), fisiólogo inglés, fundador de la biofísica, ganador en 1922 del premio Nóbel de medicina por sus descubrimientos sobre el funcionamiento del sistema muscular, y a quien se debe la, hoy en día famosa, ecuación de Hill utilizada en múltiples campos del modelado biológico (ver por ejemplo Brouwers JEM y otros).26 Por su parte, la construcción de modelos matemáticos de autoorganización se debe a Alain Turing (23 de junio de 1912-7 de junio de 1954), quien en 1952 propuso la autoformación de patrones espaciales a partir de ecuaciones de reacción-difusión, fenómeno que fue comprobado experimentalmente 40 años después, cuando la reacción conocida como CIMA (reacción entre los iones clorito y yoduro en presencia de ácido malónico), conformó patrones de concentración en pruebas de laboratorio.27
Durante el siglo XX se confirmaron diversas tendencias en el estudio de la medicina. Por ello se desarrolla la bioingeniería y dentro de esta, la simulación gracias al vertiginoso avance de los computadores. La simulación fue la encargada de estudiar las funciones y el comportamiento del cuerpo humano ante agentes biofísicos externos. La biomecánica y la mecanobiología, son dos de estas importantes áreas de investigación actual.22 La biomecánica se ha encargado de responder a las preguntas sobre el comportamiento de las diversas estructuras corporales ante diferentes condiciones de carga. Por su parte, la mecanobiología responde a las preguntas que surgen sobre la diferenciación, mantenimiento y adaptación de las células como una respuesta activa a los estímulos biomecánicos de su entorno.
Primero fue la biomecánica
La biomecánica surge de la necesidad de responder preguntas y hallar soluciones a problemas médicos y biológicos que involucran el conocimiento de la mecánica, la geometría y los materiales.11 La biomecánica ha tenido un vertiginoso avance, desde su origen, con Galileo Galilei, quien estudió el ritmo cardiaco,11 hasta nuestros días, donde se realizan sofisticados estudios de nanotubos de carbono como andamios estructurales para acelerar y mejorar el proceso de recuperación de fracturas.28 Es así como la biomecánica, a su vez, se ha bifurcado en dos grandes ramas, a saber, la biomecánica experimental y la computacional, esta última, área del conocimiento en que se ubica el presente trabajo.
En el año de 1968 se crea el Journal of Biomechanics, revista de alto nivel de impacto (indexado como JCR), en la que se publican los primeros artículos de la biomecánica computacional. Tal vez, el primer artículo que relata el uso del computador se encuentra en Snyder MF y otros,29 el cual modeló el sistema arterial humano en un computador análogo, en el cual se estudió la evolución de la presión arterial y las ondas de flujo ejercidas por los pulsos de presión durante el latido del corazón. Desde de la década de los 60 se han hecho simulaciones de todo tipo, desde el sistema musculoesquelético30-33 hasta problemas de cargas sobre tumores.34 Hoy en día (año 2009) se realizan modelos computacionales tan específicos como en Chen D y otros,35 donde se emplea mecánica computacional de fluidos, técnicas de malla deformable e interacción fluido-estructura para estudiar los movimientos del cilio activo y la respuesta del cilio pasivo ante diferentes tipos de flujos. El objeto de este estudio es entender el método de cuantificación del patrón de flujo en el nodo de un embrión de mamífero que regula la aparición del lado izquierdo del cuerpo en desarrollo (es decir, señala la ubicación de los órganos, específicamente el corazón). ]]>
La biomecánica computacional ha servido en múltiples áreas de la medicina aplicando la mecánica como herramienta de análisis. Sin embargo, la mayor aplicación de esta área ha sido solucionar problemas ortopédicos y entender el sistema musculoesquelético. Las herramientas de la mecánica clásica, como son la mecánica de fluidos, mecánica de sólidos y el análisis de movimiento son utilizados para entender el comportamiento de diferentes tejidos (y órganos) como el tejido blando, duro y la mecánica celular. El análisis de tejido duro ha sido el más estudiado desde el punto de vista computacional.36 Para ello se usa la elasticidad y conceptos de mecánica de sólidos avanzada, como la viscoelasticidad, hiperelasticidad y plasticidad (mecánica de sólidos no lineal). Los métodos de solución de estos modelos de mecánica de sólidos utiliza, en general, el de los elementos finitos y elementos de contorno. La introducción de los métodos computacionales, específicamente los elementos finitos, a la biomecánica ortopédica se inicia en 1972,36 año en el que comienzan las publicaciones sobre evaluación de esfuerzos en huesos humanos. Desde este año la frecuencia de publicaciones sobre estructuras óseas, hueso-prótesis, mecanismos de fijación de fracturas y su relación con otros tejidos aumento exponencialmente.36 Los objetivos de las investigaciones realizadas fueron establecer relaciones entre las cargas y la morfología de huesos, y establecer diseños óptimos para fijaciones, prótesis y mejorar las técnicas de implantes.36
En Liu XS y otros,31 por ejemplo, se evalúan los esfuerzos inducidos sobre el cartílago por la tensión del periostio. El objetivo es entender si la liberación de carga de compresión en el cartílago en fase de crecimiento permite modular el desarrollo de los huesos largos. Otro ejemplo de análisis de tejido duro y prótesis realizado por elementos finitos (EF) se encuentra en Abdul-Kadir M y otros,37 donde se observa el modelo por EF de una prótesis de cadera, se estudian los micromovimientos en la interfaz prótesis-fémur y su asociación con la inestabilidad del implante. El objetivo de ese trabajo fue evaluar las prótesis sin cemento y relacionar el micromovimiento con el dolor, reportado por pacientes cuando se inicia la pérdida de fijación. Los autores encontraron que la interferencia mecánica de 50 ìm es suficiente para alcanzar una buena fijación primaria y evitar fracturas en el fémur.
Sin embargo, el método de los elementos finitos no ha sido el único utilizado en la biomecánica computacional. Sfantos GK y otros38 muestran la aplicación del método de los elementos de contorno para simular el desgaste de la prótesis de cadera. En este artículo se hacen simulaciones para diferentes tamaños de fémur, tipos de copas acetabulares y tipos de material. Bajo estas condiciones se colocan cargas mecánicas de caminata normal y se simula el comportamiento de los materiales durante 20 años de servicio. Este trabajo muestra la utilidad de los elementos de contorno para almacenar grandes cantidades de información en el tiempo de simulación y la gran utilidad para hacer análisis de elasticidad. La conclusión del estudio muestra, después de 20 años de operación normal, que el deterioro de la copa acetabular puede llegar a 1,7 mm de profundidad, lo cual puede ser perjudicial al sistema implante-hueso por la generación de partículas del desgaste, a los cuales, el cuerpo puede generar una reacción inmune que termina con la fijación de la prótesis.
Stephen Cowin, del Departamento del City College de Nueva York en el año 1978 publica,39 un artículo que desarrolla el proceso de remodelamiento óseo utilizando un algoritmo adaptativo (de control) que predice la densidad del tejido a partir de las tensiones que soporta el hueso. La teoría de remodelamiento óseo fue programada bajo elementos finitos, usando un control retroalimentado a partir de la densidad de energía de deformación, el cual lograba determinar la adaptación de forma y densidad del hueso ante diferentes requerimientos de carga mecánica, resultados que confirmaban la teoría de adaptación del hueso expuesta por Wolff y Roux (1881).40 Este trabajo abre un debate importante entre diferentes teorías expuestas por Huiskes,41 Carter,42 Doblaré43 y otros muchos exponentes que intentan predecir el comportamiento adaptativo del hueso a partir de la teoría de control y de plasticidad, entre otros.
En Garzón-Alvarado DA 44 se describe uno de los tantos algoritmos que se han desarrollado para explicar el proceso de remodelación ósea. A partir de la teoría de remodelación, se dio inicio al análisis del comportamiento del tejido a partir de cargas impuestas por endroprótesis,45 por lo cual se abandonó la idea de analizar los esfuerzos sobre el material de la prótesis para volver sobre lo que ocurría al nivel de tejido, este adelanto sirvió para predecir la distribución trabecular durante el uso continuo de los implantes a lo largo del tiempo. Es así como nace la mecanobiología, la cual establece la relación del comportamiento del tejido desde el punto de vista biológico, a partir de las cargas mecánicas. La mecanobiología, fue el término acuñado por Rik Huiskes,46 la cual conformó una nueva rama de la bioingeniería. ]]>
Y luego fue la mecanobiología
La mecanobiología computacional, determina las reglas cuantitativas que gobiernan las acciones celulares para su expresión, diferenciación y mantenimiento ante estímulos biológicos y mecánicos, las cuales pueden simularse mediante métodos numéricos. El procedimiento para hallar dichas reglas es habitualmente mediante el proceso de "prueba-error".22 Los ensayos computacionales se simulan a partir de problemas de valor en el contorno mediante los cuales, las cargas mecánicas sobre el contorno son trasladadas a variables mecánicas locales (deformaciones y tensiones). Del lado biológico, estas variables mecánicas locales o biofísicas estimulan la expresión celular para regular, por ejemplo, la composición de la matriz y la expresión de sustancias moleculares. Tanto la parte biológica como la mecánica se combinan en un modelo computacional, que considera la aplicación de fuerzas, mecanotransducción, expresión celular, genética y la transformación de las características de la matriz extracelular. El método usual de implementación numérica de estos problemas mecanobiológicos es el método de los elementos finitos.47,48
A diferencia de los problemas tradicionales de la ingeniería, donde el cálculo numérico produce una respuesta a un fenómeno conocido, en la mecanobiología se ensayan diferentes relaciones matemáticas, variables de entrada y estímulos biofísicos para simular el comportamiento de un tejido u órgano. De esta forma se establecen hipótesis, y la simulación permite verificar si es plausible en comparación con las evidencias experimentales existentes que muchas veces son incompletas e insuficientes para verificar, sin duda alguna, las hipótesis de partida, abriéndose entonces nuevas vías de experimentación.22,47 Por ello, la simulación numérica ha sido recientemente citada como "El tercer método de la ciencia", después de la lógica (teórica) y la experimentación.49
Uno de los temas más importante en la mecanobiología es la mecanotransducción, concepto que ronda en la comunidad científica desde Roux en 188140 hasta las últimas publicaciones sobre el tema.50 Usando las herramientas científicas ya descritas, en los últimos años, se ha intentado predecir el crecimiento y la diferenciación celular en términos cuantitativos, a partir de estímulos biofísicos y mecánicos.
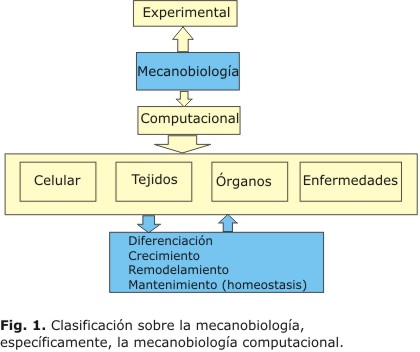
La mecanobiología puede dividir su campo de aplicación en cuatro grandes áreas: mecanobiología celular,51 de tejidos,52 de órganos53 y, mecanobiología de patologías y enfermedades. A su vez, en cada subdivisión establecida, se puede tener temas de interés especial que pueden tener tangencia con otras áreas del conocimiento, a saber: ]]>
1. En el caso de la mecanobiología celular, se puede establecer la mecanobiología intracelular,54 de diferenciación y de expresión génica. Estas dos últimas,55 son comunes, tanto en el estudio de las células como de los tejidos.
2. La mecanobiología de tejidos se encarga de establecer el comportamiento mecánico y extracelular.56 Un punto importante de esta área es el estudio de la homeostasis, la conservación y producción de matriz extracelular.
3. En la mecanobiología de órganos se establece el funcionamiento, patologías, crecimiento y remodelamiento de los tejidos que conforman los órganos. Nuevamente, esta área puede tener temas en común con la de tejidos.57
4. Mecanobiología de patologías y enfermedades, donde se estudia el establecimiento y causas de las patologías, así como sus posibles soluciones y tratamientos.58
En la figura 1, se puede observar una clasificación sobre la mecanobiología, específicamente, la mecanobiología computacional.
A continuación se presentan algunos ejemplos sobre cada una de las aéreas de la mecanobiología.
]]>
a. Mecanobiología celularLas diferentes áreas de la mecanobiología: celular, tejidos, órganos y patologías pueden unirse entre sí en torno a un tema en común como se observará en los siguientes epígrafes. La mecanobiología celular, como se anotó en párrafos anteriores, desarrolla nuevas hipótesis y teorías sobre el efecto que las cargas tienen sobre el comportamiento celular. En especial se estudia la diferenciación y expresión génica. Sin embargo, existe numerosa bibliografía donde se explica el comportamiento mecánico del citoesqueleto y los organelos, es decir, se estudia la célula a nivel intracelular. Por ejemplo, los primeros modelos computacionales en estudiar el ambiente intracelular fueron desarrollados por Sauro y Fell,59 Mendes60 y Mendes61 quienes estudiaron los caminos metabólicos de la célula. Conforme pasaron los años se desarrollaron nuevas simulaciones más complejas que involucraban mayor cantidad de variables y mayor precisión, como en Johnson y otros62 que desarrollaron algoritmos numéricos para predecir el comportamiento de cada organelo en la célula. En este artículo se muestra un programa que desarrolla múltiples procesos lógicos que determinan el comportamiento y mantenimiento celular. Particularmente, sobre el citoesqueleto se han desarrollado simulaciones del tipo multiescala. Por ejemplo, Bertaud y otros63 han desarrollado un trabajo sobre el rol de los filamentos en la mecánica de la deformación celular. Hallaron que la deficiencia en los filamentos de la células pueden alterar el comportamiento mecánico de la célula, por lo que se obtiene una respuesta de mayor elongación ante cargas mecánicas. Estos resultados fueron comparados con estudios experimentales en donde se halló una excelente correlación con la simulación.
Gracias a las nuevas técnicas experimentales64 se pueden obtener una mayor cantidad de datos del interior de la célula para definir su comportamiento en los caminos metabólicos, en el funcionamiento específico de cada organelo y en la proliferación, diferenciación y muerte. Con estos datos se ha llevado a cabo una mayor cantidad de simulaciones computacionales que muestran la evolución de la célula ante diferentes agentes biofísicos externos. Sanz y otros65 desarrollaron un modelo sobre el efecto que tiene la curvatura del sustrato sobre el comportamiento mecánico de la célula. En este artículo se estudia el citoequeleto modelado como un cuerpo continuo que se mueve gracias a la acción de motoroes de proteínas. Con esta hipótesis se desarrolla un modelo constitutivo para simular la adhesión celular, mediante fuerzas contráctiles, sobre los substratos con curvatura.
En la misma via, Kopacz y otros66 han desarrollado un modelo matemático que predice la adhesión endothelial modulada por la acción molecular. En este artículo se muestra la adhesión de las células a las arterias mediado por un factor denominado Src homólogo 2, que contiene fosfatasa tirosina (SHP). Para este modelo, nuevamente se utiliza un enfoque desde la mecánica del medio continuo a nivel celular, mientras se utiliza la tasa de reacción Kramers para modelar la adhesión celular al substrato. En la figura 2 se muestra la separación entre el substrato (en la parte inferior) y la célula (en rojo) gracias a la acción de un flujo pulsátil como se presenta en las arterias y venas.
Otro tipo de simulaciones, de gran interés científico se ha enfocado en la morfogénesis celular. En este sentido, Shinbrot y otros67 desarrollaron modelos de las células con geometría esférica, las cuales pueden migrar e interactuar mediante fuerzas eléctricas para atraer y repelerse entre sí. En este artículo se reporta la morfología y los patrones desarrollados, por lo que se crea un autoensamble para formar estructuras únicas de aglomerados celulares. En la figura 3 se pueden observar algunas de las simulaciones llevadas a cabo por el grupo de Shinbrot. ]]>
b. Mecanobiología de tejidos y órganos
En la mecanobiología de tejidos y órganos también se han hecho numerosos aportes sobre el papel que cumple la mecánica y la biología en la morfogénesis, desarrollo y mantenimiento. Se inicia una con una descripción sobre la morfogénesis y desarrollo, y luego, se muestran ejemplos sobre la homeostasis y mantenimiento de órganos y tejidos.
El crecimiento biológico es el proceso mediante el cual se adiciona masa, se configura la forma y se ajustan las dimensiones finales de los órganos que se encuentran en desarrollo. En el proceso de crecimiento del cuerpo humano se encuentran dos tipos de tejidos: el tejido duro y el tejido blando. El tejido duro puede desarrollarse mediante la aposición de masa sobre la superficie del tejido (desarrollo intramembranoso), o mediante el proceso de formación de un molde de cartílago y posterior reemplazo por tejido óseo, como ocurre en el caso de los huesos largos (desarrollo endocondral). Por el contrario, los tejidos blandos, como los vasos sanguíneos o ligamentos, experimentan un crecimiento volumétrico que genera tensiones residuales internas sobre los órganos. La cinemática del crecimiento fue descrita inicialmente por Skalak y otros,68 y ha sido desarrollada extensamente por muchos otros autores, entre los que se pueden contar Cowin,40 Doblaré y García-Aznar 69 y Humphrey.70 Por ejemplo, Kuhl y Steinmann han presentado un modelo teórico y numérico de crecimiento a partir de un sistema termodinámico abierto que tiene aplicación a tejidos duros71 y para la consolidación de heridas.72 Por su parte, Garikipati y otros73 proponen una formulación completa para el transporte de masa y mecánica multifásica en tejidos, incluyendo crecimiento.
Los modelos antes mencionados40,68-73 se construyeron a partir de la evidencia fenomenológica de que el crecimiento es inducido por estímulos mecánicos. Una línea diferente de trabajo fue abierta a partir de los trabajos de Turing,74 donde se pone de manifiesto que las señales moleculares generan estímulos sobre las células para que estas sinteticen matriz extracelular, se dividan o se diferencien, según reglas biológicas que inducen el crecimiento de tejidos y órganos.75 ]]>
Los modelos de crecimiento, a partir de la información biológica (señales moleculares y respuesta celular) han merecido un especial interés a partir del trabajo de Turing.74 De hecho, este demostró el potencial de las ecuaciones de reacción-difusión para generar patrones espaciales de las sustancias bioquímicas que, bajo reglas particulares de diferenciación, permiten la formación de tejidos y la agrupación de células. La evolución de estos modelos bioquímicos ha traído consigo el desarrollo de disciplinas asociadas tan importantes como los sistemas dinámicos biológicos. A partir de los primeros modelos de Turing se han construido formulaciones matemáticas de muchos procesos biológicos basados en este esquema.75
Las primeras ecuaciones de reacción-difusión tenían en cuenta una única especie química, como en el trabajo de Wolpert76 donde se muestra que la posición molecular de una sustancia permite la diferenciación celular dependiente de un nivel umbral de concentración establecido. A medida que la comprensión de los fenómenos bioquímicos aumentaba, se fueron construyendo modelos complejos con múltiples especies. Cada uno de estos modelos matemáticos genera patrones particulares según los parámetros involucrados en la ecuación. Los sistemas dinámicos han jugado desde entonces un papel importante en biología, intentando predecir las bifurcaciones y la formación de patrones, según tres posibilidades de inestabilidad: Hopf, Inestabilidad de Turing y Turing Oscilante.77
En lo que se refiere en concreto a la formulación bioquímica del crecimiento biológico, también se han construido diversos modelos. Por ejemplo, Dillon y otros78 simularon el desarrollo de extremidades incorporando el crecimiento celular, la mitosis y las interacciones de los morfogenes producidos en la zona de actividad apical. De otro lado, Anotida Madzvamuse79 simuló la distribución de la pigmentación en las alas de mariposas, explicando, mediante modelos de reacción-difusión, los múltiples tipos de distribución dependiendo del tamaño y forma del dominio de análisis.
Posteriormente, a principios de la década de los 80, Oster y Murray80 construyeron un modelo mecanobiológico que constituyó la unión entre el modelo de reacción difusión con las cargas mecánicas. A partir de este modelo se han simulado procesos de condensación mesenquimal que incluyen procesos biológicos y mecánicos. Bajo este marco de trabajo, se han simulado diferentes casos como la formación de tumores,81,82 la formación de extremidades, la tubulogénesis y la angiogénesis. Un ejemplo reciente lo describe Namy y otros83 en donde se determinan las condiciones críticas del espacio de parámetros del modelo para que se produzca la tubulogénesis en un tejido sometido a campos de tracción celular en una caja de Petri.
Paralelamente a la anterior tendencia, y a partir de la evidencia experimental, se crearon modelos donde las cargas mecánicas influenciaban la formación de tejidos, pero que, a diferencia de los modelos antes descritos, no incluían ecuaciones de reacción difusión de sustancias químicas. Los modelos basados en esta línea de la mecanobiología han significado un avance importante en la explicación de fenómenos relacionados con el cuerpo humano, especialmente con el sistema esquelético,22 porque además de explicar los procesos biológicos permiten desarrollar líneas de experimentación mecánica basadas en los ensayos numéricos.22 Ejemplos sobre esta línea de acción han sido publicados en las últimas dos décadas. Por ejemplo, Carter y otros34 citan la aparición de los centros secundarios de osificación en función de una variable auxiliar denominada "índice osteogénico", que está relacionada con los valores de la tensión octaédrica a la que se encuentra sometido el hueso. A partir de ensayos numéricos, y por comparación con las evidencias experimentales, se hallaron intervalos posibles para la variable osteogénica. Por otro lado, y a partir de datos clínicos y de experimentación, se han desarrollado diversos modelos sobre la influencia mecánica y genética en la morfogénesis y la osificación endocondral durante la etapa embrionaria. En especial, se han desarrollado modelos sobre la formación femoral en etapa prenatal, donde aún no se considera la formación del centro secundario de osificación,30 Shefelbine y otros84,85 han descrito las consecuencias mecánicas de la mineralización sobre el comportamiento de la placa de crecimiento. Además, a partir de las condiciones mecánicas del desarrollo, Shefelbine84 propone un modelo sobre la evolución del ángulo bicondilar, mostrando datos importantes sobre la evolución estructural del esqueleto del hombre y las diferencias con los primates. Van Donkelaar y Huiskes85 crearon un modelo que está a mitad de camino entre los de reacción-difusión y los modelos mecánicos. En un marco de trabajo unidimensional, realizaron un modelo de elementos finitos que incorpora el crecimiento de un hueso por señales moleculares presentes en la metáfisis de un fémur humano. El análisis incluye síntesis de factores de crecimiento en zonas relevantes del hueso en formación, así como el transporte y degradación de dichas sustancias. ]]>
Garzón-Alvarado y otros,86,87 han utilizado un modelo de reacción-difusión de morfogenes e incluyendo variables mecánicas, han desarrollado modelos completos de la morfogenesis ósea para explicar la aparición y crecimiento de los canales de cartílago y el posterior desarrollo del centro secundario de osificación. Los ejemplos desarrollados por Garzón-Alvarado y sus colaboradores permiten tener en cuenta el rol de los canales de cartílago en la formación de la epífisis. Nuevamente, este desarrollo fue hecho mediante elementos finitos, pero, adicionalmente, se incluyeron autómatas celulares para simular la aparición de los canales (ver figuras 4 y 5).
Desde la homeostasis y mantenimiento se han hecho excelentes trabajos que amplían el conocimiento experimental con la simulación computacional. Por ejemplo, Klein-Nulend y otros88 desarrollaron un excelente trabajo sobre la mecanobiología del hueso. En este trabajo se presentan los estados de remodelamiento y las rutas metabólicas que le permiten al hueso estar en constante intercambio mineral y renovación de tejido. Un trabajo similar se presenta en Loret B y Simoes,89 los que crean las condiciones necesarias para el crecimiento y mantenimiento de los tejidos en virtud del intercambio de masa en el tejido. Al igual, que en el caso de la mecanobiología celular, se pueden enumerar una gran cantidad trabajos que sería imposible consignar en esta revisión. En el siguiente apartado se muestra la influencia de la mecanobiología en el estudio de patologías, enfermedades y recuperación de tejidos y órganos.
c. Mecanobiología de patologías, enfermedades y recuperación de tejidos y órganos
]]>
Utilizando la misma metodología mecanobiológica, se han simulado patologías, reparación y recuperación de tejidos y órganos. Por ejemplo, en fracturas óseas90 donde se han considerado estados de crecimiento, diferenciación y regeneración tisular regulados a través de factores exclusivamente mecánicos. Doblaré y otros,91 así como Gómez-Benito y otros92 han desarrollado modelos matemáticos y simulaciones computacionales que determinan los eventos que ocurren durante la cicatrización de una fractura. En especial, Gómez-Benito y colaboradores desarrollan simulaciones que tienen en cuenta el espacio que existe entre la fractura y la migración de células y morfogenes en el transcurso del proceso de recuperación. Mediante un enfoque similar, Weis y otros93 proponen un modelo inverso, por elementos finitos, que desarrolla las condiciones necesarias para acelerar la cicatrización en el fémur de roedores. Hanna Isaksson y otros94 propone un modelo geométrico donde tiene en cuenta la regulación mecánica durante la fractura y la cicatrización sin agentes externos. Para este fin, Isaksson y otros desarrollaron modelos de reacción difusión que en conjunto con la mecánica de cuerpos deformables permiten conocer el flujo celular y de nutrientes al callo óseo. Modelos similares a los ya mencionados se pueden encontrar en García-Aznar JM y otros, Meroi EA y otros, Wehner T y otros.90,95,96
También, estudios sobre otros tipos de tejidos se pueden encontrar en la literatura sobre modelos de daño o reparación. En el párrafo anterior se trató la cicatrización que ocurre luego de la fractura ósea. Sin embargo, no es el único tipo de tejido estudiado desde la perspectiva de la mecanobiología. El cartílago ha sido estudiado en varios modelos matemáticos y computacionales. Por ejemplo, Landinez y otros97 desarrollaron un modelo computacional que tiene en cuenta el daño que es ocasionado por cargas mecánicas. En ese modelo se obtiene un parámetro de daño (D) que ubica espacialmente el sitio de mayor probabilidad donde se puede producir fractura en el cartílago articular de la rodilla. Además, se incorporan los efectos del ejercicio, masa de índice corporal (sobrepeso) entre otros efectos realistas. En la figura 6, se observa la abstracción del modelo geométrico y la malla de elementos finitos.
En la figura 7 se pueden observar los resultados donde se muestra la zona de daño del cartílago. De igual forma, Wilson y otros98 han desarrollado un modelo del cartílago articular que tiene en cuenta la red de fibras de colágeno en el tejido. Para este fin, el modelo se ha hecho mediante elementos finitos con un modelo constitutivo poroviscoelástico, lo cual tiene en cuenta el flujo de líquido en la rodilla. Modelos similares a los mencionados se pueden observar en Wilson W y otros, Wilson W y otros, Peña E y otros,99-101 entre otros.
En odontología, la mecanobiología ha desarrollado modelos exitosos en el desarrollo de lesiones, en la recuperación y cicatrización alrededor de implantes dentales y en el manejo de patologías especiales. Por ejemplo, Vanegas y otros102 han desarrollado un modelo de osteointegración dental alrededor de un implante. En dicho artículo se establecen las principales moléculas y células que intervienen en el proceso de migración celular para la conformación del nuevo tejido que se desarrollara alrededor del implante. El modelo se diferencia del de Moreo y otros103 por involucrar con mayor completud las variables de cicatrización desde el momento de la inserción de la prótesis hasta la formación total del tejido circundante. Adicionalmente, una línea de trabajo en odontología se ha abierto gracias a los modelos de remodelación ósea como el propuesto por Lin y otros104 quienes desarrollan modelos computacionales sobre la distribución de densidad ósea debido a cargas masticatorias en la mandíbula.
La lista de artículos y trabajos que utilizan la mecanobiología como herramienta fundamental de análisis es extensa y no cabría en este trabajo una descripción completa de todas y cada una de las áreas en las que ha incursionado. Sin embargo, se ha hecho una revisión de los trabajos actuales y las tendencias en el desarrollo de modelos computacionales que permiten construir hipótesis, teorías y probar in silico modelos que pueden ser complejos de llevar al laboratorio. En el siguiente apartado se mostraran los desafíos existentes en la mecanobiología.
]]>
Desafíos y nuevas tendencias en la mecanobiología
La pregunta central del problema de la mecanobiologia es: ¿se pueden llevar a cabo ensayos computacionales de fenómenos a nivel de tejido y órgano sin conocer exactamente los parámetros y variables implicadas? La respuesta a esta pregunta es tal vez el problema central de la mecanobiología computacional. Muchos de los fenómenos biológicos que involucran cargas tienen variables aún no muy bien entendidas, por tanto, la mecanobiología está jalonando nuevas líneas de experimentación, que en un futuro pueden dar respuestas sobre valores y modelos que son supuestos en el computador. Sin embargo, aún bajo las contradicciones enunciadas, hay fenómenos mecanobiológicos que son simulados y corresponden, cualitativamente, a lo observado clínica y experimentalmente. Es allí donde la mecanobiología ha realizado importantes avances. Por ejemplo, en la estimación de variables y parámetros desconocidos (en las relaciones existentes entre diferentes modelos a nivel molecular y celular) se cuenta hoy en día con nuevos y valiosos datos para alimentar modelos que pueden predecir fenómenos como el crecimiento del cáncer, el crecimiento de huesos largos y fenómenos de reparación ósea.
Es de notar que los procesos biológicos presentan una gran variabilidad estadística, por lo que los modelos mecanobiológicos pueden ser, simplemente, estimaciones gruesas de fenómenos que involucran procesos multiacoplados. Este acoplamiento de fenómenos trae consigo el manejo de diferentes escalas de tiempo y espacio, lo cual ha desarrollado nuevas ramas que utilizan modelos «multiescala», que tal vez, especulando, puede ser el siguiente paso en la comprensión de la física, biología y los materiales. Adicionalmente, en los nuevos modelos computacionales se deben incluir efectos eléctricos, que en conjunto con la mecánica pueden dar cuenta del comportamiento de células y tejidos. Estos ingredientes, más los efectos químicos desarrollarían modelos altamente complejos que requieren de mayor estudio en futuros trabajos.
CONCLUSIONES
Se ha realizado un breve recorrido sobre la historia de la biomecánica y su trascurrir hacia la mecanobiología como herramientas necesarias para el análisis médico. En el artículo se puede evidenciar que el advenimiento de la computación permitió desarrollar teorías más sofisticadas y claras sobre los fenómenos biológicos que ocurren a nivel de tejido y órgano. Es así, como aplicando las leyes fundamentales de conservación: de masa, momentum, energía y sobre la base del principio de entropía se establecen relaciones biológicamente plausibles para formular modelos computacionales que describen procesos biológicos. ]]>
En este artículo se hizo una breve revisión del estado del arte de la mecanobiología, se citan algunas fuentes y se describen los modelos más importantes y relevantes a juicio del autor. Sin embargo, por ser una línea de investigación activa, los artículos que se publican al respecto pueden ascender a los cientos de miles, por lo que la visión entregada aquí es minúscula con respecto al gran universo de producción científica sobre el área.
REFERENCIAS BIBLIOGRÁFICAS
1. Malekly H, Mousavi SM, Hashemi H. A fuzzy integrated methodology for evaluating conceptual bridge design. Expert Systems with Applications.2010;37(7):4910-20. ]]>
2. Saven JG. Computational protein design: Advances in the design and redesign of biomolecular nanostructures, Colloid & Interface Science. 2010;15(1-2):13-7.
3. Komatitsch D, Erlebacher G, Göddeke D, Michéa D. High-order finite-element seismic wave propagation modeling with MPI on a large GPU cluster. Journal of Computational Physics. 2010;229(20):7692-7714.
4. Krasnopolsky VM, Fox-Rabinovitz MS. Complex hybrid models combining deterministic and machine learning components for numerical climate modeling and weather prediction. Neural Networks. 2006;19(2):122-34.
]]>
5. Strawn RC, Biswas R. Numerical simulations of helicopter aerodynamics and acoustics. Journal of Computational and Applied Mathematics.1996;66(1-2):471-83.
6. Valentini G, Tagliaferri R, Masulli F. Computational intelligence and machine learning in bioinformatics. Artificial Intelligence in Medicine. 2003;45(2-3):91-6.
7. Boyle C, Kim IY. Comparison of different hip prosthesis shapes considering micro-level bone remodeling and stress-shielding criteria using three-dimensional design space topology optimization. Journal of Biomechanics. In Press 2011.
8. Hanley NA. Commonalities in the endocrinology of stem cell biology and organ regeneration. Molecular and Cellular Endocrinology 2008;288(1-2):1-5.
9. Cortesini R. Stem cells, tissue engineering and organogenesis in transplantation. Transplant Immunology. 2005;15(2):81-9.
10. Hollister SJ, Lin CY. Computational design of tissue engineering scaffolds. Computer Methods in Applied Mechanics and Engineering. 2007;196(31-32):2991-8.
11. Fung YC. Biomechanics: Mechanical properties of living tissues. Springer Verlag; 1990. ]]>
12. Sutherland CJ, Bresina SJ, Gayou DE. Use of general purpose mechanical computer assisted engineering software in orthopaedic surgical planning: advantages and limitations. Computerized Medical Imaging and Graphics. 1994;18(6):435-42.
13. Yaszemski MJ, Yasko A.W. Musculoskeletal Tissue Engineering for Orthopedic Surgical Applications. Frontiers in Tissue Engineering;1998. p. 197-212.
14. Prendergast PJ. Finite element models in tissue mechanics and orthopaedic implant design. Clinical Biomechanics.1997;12(6):343-66.
]]>
15. Webster TJ. Nanophase ceramics: The future orthopedic and dental implant material. Advances in Chemical Engineerins. 2001;27:125-66.
16. Quaas S, Rudolph H, Luthardt RG. Direct mechanical data acquisition of dental impressions for the manufacturing of CAD/CAM restorations. Journal of Dentistry.2007; 35(12):903-8.
17. Ateshian GA, Friedman MH. Integrative biomechanics: A paradigm for clinical applications of fundamental mechanics. Journal of Biomechanics. 2009;42(10): 1444-51.
18. Woo SL-Y, Thomas M, Saw SSC. Contribution of biomechanics, orthopaedics and rehabilitation: The past, present and future. The Surgeon. 2004;2(3):125-36.
19. Miles AW, Gheduzzi S. Basic biomechanics and biomaterials. Surgery (Oxford). 2009;27(2):90-5.
20. Carter DR, Beaupr´e GS. Skeletal Function and Form - Mechanobiology of skeletal Development, Aging, and Regeneration. Cambridge University Press; 2001.
21. Weinans H, Huiskes R, Grootenboer HJ. The behavior of adaptive bone-remodeling simulation models. Journal of Biomechanics. 1992;25(12):1425-41. ]]>
22. Huiskes R. The law of adaptive bone remodeling: a case for crying newton? London, Singapore River Edge; 1995.
23.Van der Meulen MCH, Huiskes R. Why mecanobiology?Journal of Biomechanics. 2002;35(4).
24. Debus AG. El hombre y la naturaleza en el renacimiento. México. FCE-CONACYT. 1985;(384).
]]>
25. Varadarajan VS. Euler Through Time: A new look at old themes.AMS;1983.
26. Brouwers JEM, van Donkelaar C, Sengers BG, Huiskes R. Can the growth factors PTHrP, Ihh and VEGF, together regulate the development of a long bone? Journal of Biomechanics. 2006;39:277482.
27. Lengyel I, Epstein IR. Modeling of Turing structures in the chloriteiodide- malonic acid-starch reaction system. Science, 1991;251:6502.
]]>
28. Edwards SL, Church JS, Werkmeister JA, Ramshaw JAM. Tubular micro-scale multiwalled carbon nanotube-based scaffolds for tissue engineering. Biomaterials. 2009;30(9):1725-31.
29. Snyder MF, Rideout VC, Hillestad RJ. Computer modeling of the human systemic arterial tree. Journal of Biomechanics. 1968;1(1):341-53.
30. Fox MD, Reinbolt JA, Õunpuu S, Delp S. Mechanisms of improved knee flexion after rectus femoris transfer surgery. Journal of Biomechanics 2009;42(5):614-619.
31. Liu XS, Bevill G, Keaveny TM, Sajda P, Guo XE. Micromechanical analyses of vertebral trabecular bone based on individual trabeculae segmentation of plates and rods. Journal of Biomechanics. 2009;42(3):249-56.
32. Eswaran SK, Bevill G, Nagarathnam P, Allen MR, Burr D, Keaveny T. Effects of suppression of bone turnover on cortical and trabecular load sharing in the canine vertebral body. Journal of Biomechanics. 2009;42(4):517-23.
33. Huthmann S, Staszyk C, Jacob HG, Rohn K, Gasse H. Biomechanical evaluation of the equine masticatory action: Calculation of the masticatory forces occurring on the cheek tooth battery. Journal of Biomechanics. 2009;42(1):67-70.
34. Carter DR, Wong M. The role of mechanical loading histories in the development of diarthrodial joints. J. Orthop Res. 1988;6:80416. ]]>
35. Chen D, Norris D, Ventikos Y. The active and passive ciliary motion in the embryo node: A computational fluid dynamics model. Journal of Biomechanics. 2009;42(3): 210-6.
36. Huiskes R, Chao EYS. A survey of finite element analysis in orthopedic biomechanics: The first decade. Journal of Biomechanics.1983;16(6):385-409.
37. Abdul-Kadir M, Hansen U, Klabunde R, Lucas D, Amis A. Finite element modelling of primary hip stem stability: The effect of interference fit. Journal of Biomechanics. 2008;41(3):587-94. ]]>
38. Sfantos GK, Aliabadi MH. Total hip arthroplasty wear simulation using the boundary element method. Journal of Biomechanics. 2007;40(2):378-89.
39. Cowin SC, Van Buskirk WC. Internal bone remodeling induced by a medullary pin. Journal of Biomechanics. 1978;11(5):269-75.
40. Cowin S. Bone Mechanics Handbook. CRC press LLC; 2001.
]]>
41. Weinans H. Huiskes R, Grootenboer HJ. The behavior of adaptive bone-remodeling simulation models. Journal of Biomechanics.1992;25(12):1425-41.
42. Jacobs CR, Simo JC, Beaupre GS, Carter DR. Adaptive bone remodeling incorporating simultaneous density and anisotropy considerations. Journal of Biomechanics.1997;30(6):603-13.
43. Doblaré M, Garcýìa. Anisotropic bone remodelling model based on a continuum damage-repair theory. Journal of Biomechanics. 2002;35(1):1-17.
44. Garzón-Alvarado DA. Análisis del Proceso de Regeneración Ósea por el método de los elementos finitos [tesis de Maestría]. Universidad Nacional de Colombia; 2003.
45. Garzón-Alvarado DA. Roa M, Ramírez A. Predicción del proceso de remodelación ósea para diferentes implantes de cadera utilizando optimización topológica. Rev Cubana Ortop Traumatol. 2009;22(2).
46. van der Meulen MCH, Huiskes R. Why Mechanobiology? Journal of Biomechanics. 2002;35(4):401-14.
47.Huiskes R, Chao EYS. «çA survey of finite element analysis in orthopedic biomechanics: The first decade. Journal of Biomechanics. 1983;16(6):385-409. ]]>
48. Prendergast PJ. Finite element models in tissue mechanics and orthopaedic implant design. Clinical Biomechanics. 1997;12(6):34366.
49. Kelly J. The third culture. Science.1998;279.
50. Martin I, Miota S, Barberoa A, Jakoba M, Wendta D. Osteochondral tissue engineering. Journal of Biomechanics. 2007;40(4).
]]>
51. Hsieh AH, Twomey JD. Cellular mechanobiology of the intervertebral disc: New directions and approaches. Journal of Biomechanics. 2010;43(1):137-45.
52. Knothe ML, Dolejs S, McBride SH, Miller RM, Knothe UR. Multiscale mechanobiology of de novo bone generation, remodeling and adaptation of autograft in a common ovine femur model. Journal of the Mechanical Behavior of Biomedical Materials. 2011;4(6):829-40.
53. Tschumperlin DJ, Boudreault F, Liu F. Recent advances and new opportunities in lung mechanobiology. Journal of Biomechanics. 2010;43(1):99-107.
54. James H, Wang C, Thampatty BP. Chapter 7 Mechanobiology of Adult and Stem Cells. International Review of Cell and Molecular Biology. 2008;271:301-46.
55. Pérez MA, Prendergast PJ. Random-walk models of cell dispersal included in mechanobiological simulations of tissue differentiation. Journal of Biomechanics. 2007;40(10):2244-53.
56. Loboa EG, Fang TD, Warren SM, Lindsey DP, Fong KD, Longaker MT, Carter DR. Mechanobiology of mandibular distraction osteogenesis: experimental analyses with a rat model. Bone. 2004;34(2):336-43.
57. Villemure I, Stokes IAF. Growth plate mechanics and mechanobiology. A survey of present understanding. Journal of Biomechanics. 2009;42(12):1793-1803. ]]>
58. Suresh S. Biomechanics and biophysics of cancer cells. Acta Biomaterialia. 2007; 3(4):413-38.
59. Sauro H, Fell D. SCAMP: a metabolic simulator and control analysis program. Math Comput Model. 1991;15(12):15-28.
60. Mendes P. Gepasi: a software package for modelling the dynamics, steady states and control of biochemical and other systems. Comput Appl Biosci. 1993;9: 563-71.
]]>
61. Mendes P. Biochemistry by numbers: simulation of biochemical pathways with Gepasi. Trends Biochem Sci. 1997;22:361-63.
62. Johnson CG, Goldman JP, Gullick WJ. Simulating complex intracellular processes using object-oriented computational modelling. Progress in Biophysics and Molecular Biology. 2004;86(3):379-406.
63. Bertaud J, Qin Z, Buehler MJ. Intermediate filament-deficient cells are mechanically softer at large deformation: A multi-scale simulation study. Acta Biomaterialia. 2010;6(7):2457-66.
]]>
64. Sen S. Kumar S. Combining mechanical and optical approaches to dissect cellular mechanobiology. Journal of Biomechanics. 2010;43(1):45-54.
65. Sanz-Herrera JA, Moreo P, García-Aznar JM, Doblaré M. On the effect of substrate curvature on cell mechanics. Biomaterials. 2009;30(34):6674-86.
66. Kopacz AM, Liu WK, Liu SQ. Simulation and prediction of endothelial cell adhesion modulated by molecular engineering. Computer Methods in Applied Mechanics and Engineering. 2008;197(25-28):2340-52.
67. Shinbrot T, Chun Y, Caicedo-Carvajal C, Foty R. Cellular Morphogenesis In Silico. Biophysical Journal. 2009;97(4):958-67.
68. Skalak G, Dasgupta M, Moss E, Otten P. Analytical description of growth. Journal of Theoretical Biology. 1982;94.
69. Doblaré M, García-Aznar JM. On the numerical modeling of growth, differentiation and damage in structural living tissues. Arch Comput Meth Engng. 2006;11(4):471-513.
70. Humphrey JD. Mechanics of arterial wall: review and directions. Critic Rev biomed. 1995;23. ]]>
71. Kuhl E, Steinmann P. Theory and numerics of geometrically non-linear open system mechanics. Int J Numer Metho Engng. 2003;58.
72. Kuhl E, Steinmann P.Computational modeling of healing; an application of the material force method. Biomech Model Mechanobiol. 2004;2(4).
73. Garikipati K, Arruda EM, Grosh K, Narayanan H, Calve S. A continuum treatment of growth in biological tissue: the coupling of mass transport and mechanics. Journal of the Mechanics and Physics solids. 2004;52(7).
]]>
74. Turing AM. The chemical basis of morphogenesis. Phil Trans R Soc Lond B. 1952; 327:37-72.
75. Madzvamuse A. A Numerical approach to the study of spatial pattern formation. D. Phil Thesis. UK: Oxford University; 2000.
76. Wolpert L. Cell Behaviour-Cartilage morphogenesis in the limb. Cambridge University; 1982.
]]>
77. Dolnik M, Zhabotinsky A, Rovinsky AB, Epstein IR. Spatio-temporal patterns in a reaction-diffusion system with wave instability. Chemical Engineering Science. 2000; 55:223-31.
78. Dillon R, Gadgil C, Othmer H. Short- and long-range effects of sonic hedgehog in limb development. PNAS.2003;100(18):10152-7.
79. Madzvamuse A, Thomas R, Maini PK, Wathen A. A numerical approach to the study of spatial pattern formation in the ligaments of arcoidbivalves. Bulletin of Mathematical Biology. 2002;64(3):501-30.
80. Oster GF, Murray JD, Harris AK. Mechanical aspects of mesenchymal Morphogenesis. J Embryol Exp Morphol. 1983;78:83-125.
81. Bru A, Herrero MA. From The Physical Laws Of Tumor Growth To Modelling Cancer Processes. Mathematical Models and Methods in Applied Sciences. 2006;16(1).
82. Reis EA, Santos LBL, Pinho STR. A cellular automata model for avascular solid tumor growth under the effect of therapy. Physica A: Statistical Mechanics and its Applications. 2009;388(7):1303-14.
83. Namy P, Ohayon J, Tracqui P. Critical conditions for pattern formation and in vitro tubulogenesis driven by cellular traction fields. Journal of Theoretical Biology. 2004; 227(1):103-20. ]]>
84. Shefelbine SJ. Mechanical Regulation of bone growth fronts and growth plates. PhD Thesis, Stanford University; 2002.
85. Shefelbine SJ, Tardieu C, Carter DR. Development of the femoral bicondylar angle in hominid bipedalism. Bone. 2002;30(5):765-70.
86. Garzón-Alvarado DA, Peinado LM, Cárdenas RP. A mathematical model of epiphyseal development: hypothesis of growth pattern of the secondary ossification centre. Computer Methods in Biomechanics and Biomedical Engineering. 2010;14(1): 1476-8259.
]]>
87. Garzón-Alvarado DA. Peinado LM, Cárdenas RP. A mathematical model of epiphyseal development: hypothesis on the cartilage canals growth. Computer Methods in Biomechanics and Biomedical Engineering. 2010;13(6):1476-8259.
88. Klein-Nulend J, Bacabac RG, Mullender MG. Mechanobiology of bone tissue. Pathologie Biologie. 2005;53(10):576-80.
89. Loret B, Simões FMF. A framework for deformation, generalized diffusion, mass transfer and growth in multi-species multi-phase biological tissues. European Journal of Mechanics - A/Solids. 2005;24(5):757-81.
90. García-Aznar JM, Kuiper JH, Gómez-Benito MJ, Doblaré M, Richardson JB. Computational simulation of fracture healing: Influence of interfragmentary movement on the callus growth. Journal of Biomechanics. 2007;40(7):1467-76.
91. Doblaré M, García JM, Gómez M.J. Modelling bone tissue fracture and healing: a review. Engineering Fracture Mechanics, 2004;71(13-14):1809-40.
92. Gómez-Benito MJ, García-Aznar JM, Kuiper JH, Doblaré M. Influence of fracture gap size on the pattern of long bone healing: a computational study. Journal of Theoretical Biology. 2005;235(1):105-19.
93. Weis JA, Miga MI, Granero-Moltó F, Spagnoli A. A finite element inverse analysis to assess functional improvement during the fracture healing process. Journal of Biomechanics. 2010;43(3):557-62. ]]>
94. Isaksson H, Wilson W, van Donkelaar CC, Huiskes R, Ito K. Comparison of biophysical stimuli for mechano-regulation of tissue differentiation during fracture healing. Journal of Biomechanics. 2006;39(8):1507-16.
95. Meroi EA, Natali AN. A numerical approach to the biomechanical analysis of bone fracture healing. Journal of Biomedical Engineering. 1989;11(5):390-7.
96. Wehner T, Claes L, Niemeyer F, Nolte D, Simon U. Influence of the fixation stability on the healing time A numerical study of a patient-specific fracture healing process. Clinical Biomechanics. 2010;25(6):606-12.
]]>
97. Landinez-Parra NS, Garzón-Alvarado DA, Vanegas-Acosta JC. A phenomenological mathematical model of the articular cartilage damage. Computer Methods and Programs in Biomedicine. In Press, Corrected Proof. Available online 12 March 2011. Disponible en: http://www.sciencedirect.com/science/article/pii/S0169260711000198
98. Wilson W. van Donkelaar CC, van Rietbergen B, Ito K, Huiskes R. Stresses in the local collagen network of articular cartilage: a poroviscoelastic fibril-reinforced finite element study. Journal of Biomechanics, 2004;37(3):357-66.
99. Wilson W, van Donkelaar CC, van Rietbergen R, Huiskes R.The role of computational models in the search for the mechanical behavior and damage mechanisms of articular cartilage. Medical Engineering & Physics. 2005;27(10):810-26.
100. Wilson W, van Rietbergen B, van Donkelaar CC, Huiskes R. Pathways of load-induced cartilage damage causing cartilage degeneration in the knee after meniscectomy. Journal of Biomechanics. 2003;36(6):845-51. ]]>
101. Peña E, Calvo B, Martínez MA, Doblaré M. Computer simulation of damage on distal femoral articular cartilage after meniscectomies. Computers in Biology and Medicine. 2008;38(1):69-81.
102. Vanegas-Acosta JC, Landinez NS, Garzón-Alvarado DA, Casale MC. A finite element method approach for the mechanobiological modeling of the osseointegration of a dental implant. Computer Methods and Programs in Biomedicine. 2011;101(3): 297-314.
103. Moreo P, García-Aznar JM, Doblaré M. Bone ingrowth on the surface of endosseous implants. Part 1: Mathematical model. Journal of Theoretical Biology. 2009;260(1):1-12.
]]>
104. Lin D, Li Q, Li W, Duckmanton N, Swain M.Mandibular bone remodeling induced by dental implant. Journal of Biomechanics. 2010;43(2):287-93.
Recibido: 3 de febrero de 2011. ]]> Aprobado: 20 de marzo de 2011.
Diego A. Garzón-Alvarado. Departamento de Ingeniería Mecánica y Mecatrónica. Facultad de Ingeniería. Universidad Nacional de Colombia. Correo electrónico: dagarzona@bt.unal.edu.co ]]>