Desarrollo de un método para el diagnóstico específico del PepMoV basado en la RT-PCR
Development of a method for the specific diagnosis of PepMoV based on RT -PCR
Franklyn Arana LabradaI,II, Ronald Pacheco SánchezII, Acela Díaz De la OsaIII, Bertha Piñol PérezII, Madelaine Quiñones PantojaII*
IFacultad de Ciencias Agrícolas. Universidad de Las Tunas. Ave. Carlos J Finlay, Reparto Santos, s/n, Las Tunas, Cuba. Correo electrónico: franklynal@ult.edu.cu.
IIDirección de Sanidad Vegetal. Centro Nacional de Sanidad Agropecuaria (CENSA), Carretera de Jamaica y Autopista Nacional, Apartado 10, San José de las Lajas, Mayabeque, Cuba. ]]>
IIIFacultad de Biología, Universidad de La Habana, Cuba.
RESUMEN
El objetivo de este trabajo fue desarrollar un método para el diagnóstico específico del PepMoV basado en laRT-PCR. Se diseñaron cebadores utilizando como referencia la secuencia genómica del aislado de la Florida, para amplificar un fragmento del extremo 5' no traducible y amino terminal de la proteína P1 del genoma. Se utilizó el programa Oligo (versión 7.4) para realizar el análisis in silico y establecer los parámetros iniciales de la reacción. Se evaluaron la temperatura óptima de hibridación de cebadores, la concentración de cebadores, el límite de detección, la repetitividad intraensayo e interensayo y la especificidad analítica. La temperatura óptima de hibridación de los cebadores fue de 59°C; se seleccionó como concentración óptima de los cebadores 0,32 µM. Los aspectos evaluados del ensayo permitieron establecer las condiciones óptimas de la técnica. La RT-PCR se comportó con alta especificidad para el diagnóstico de PepMoV; este mostró un límite de detección de 94 pg.µl-1. La herramienta molecular obtenida permitirá apoyar los programas de mejoramiento genético y de manejo integrado del cultivo en el país.
Palabras clave: RT-PCR, potyvirus, PepMoV, pimiento.
ABSTRACT
The main objective was to develop a method for the specific diagnosis of PepMoV based on RT-PCR. Primers were designed using as reference the genomic sequence of the Florida isolate to amplify a fragment of the 5'untranslatable end and amino-terminus of P1 protein of the genome. The Oligo program (version 7.4) was used to carry out the analysis in silico and establish the initial parameters of the reaction. The optimal temperature of primer hybridization, primer concentration, intra- and inter-assay repeatability, detection limit, and the analytic specificity were evaluated. The optimal temperature of primer hybridization was 59°C, and 0,32 µM was selected as the optimal concentration of the primers. The aspects of the assay evaluated allowed establishing the optimal conditions of the technique. The RT-PCR method behaved with a high specificity for the diagnosis of PepMoV. It showed a detection limit of 94 pg.µl-1. The molecular tool obtained will allow supporting the breeding programs and the integrated pest management of this crop in the country.
Key words: RT-PCR, potyviruses, PepMoV, sweet pepper.
]]>
INTRODUCCIÓN
En Cuba, el pimiento (Capsicum annuum L.) constituye una hortaliza de interés económico por su alta demanda en el mercado; uno de los principales obstáculos para su producción son las enfermedades causadas por virus, entre los que se encuentran los potyvirus (1). Los miembros de este género causan pérdidas significativas en una gran variedad de cultivos. Se transmiten por áfidos de forma no persistente y algunos de ellos son transmitidos por semilla (2).
Informes previos abordaron la presencia de los potyvirus Potato Virus Y (PVY) y Tobacco etch virus (TEV) en pimiento (3). No obstante, en el año 2011, Quiñones et al. (4) informaron la presencia de un aislado de Pepper mottle virus (PepMoV), con 98% de similitud con el aislado de la Florida, en plantas de pimiento provenientes de las principales áreas productoras de las tres regiones del país, lo que evidencia una amplia distribución de este virus.
El PepMoV tiene una vasta gama de hospedantes, entre ellos papa (Solanum tuberosum L.), pimiento (Capsicum annuum L.) y tomate (Solanum lycopersicum L.) (5). Este virus se transmite de manera no persistente por adultos y ninfas de Myzus persicae (Sulzer), especie considerada la más eficiente para la transmisión de este patógeno (6).
El diagnóstico de estas entidades a nivel mundial transitó desde el uso de métodos convencionales, como la expresión de síntomas en plantas indicadoras y el uso de métodos serológicos, hasta el empleo de tecnologías moleculares (7). En nuestro país, Díaz et al. (7) validaron una RT-PCR en un solo paso para el diagnóstico genérico de potyvirus; sin embargo, no se dispone de un método específico para la detección del PepMoV (4).
La presencia de la sintomatología típica de PepMoV en los principales polos productivos de pimiento del país y los bajos rendimientos obtenidos en el cultivo, que pudieran estar asociados a los daños ocasionados por PepMoV, así como el desarrollo de un programa de mejoramiento genético de pimiento encaminado a la obtención de híbridos y cultivares resistentes a potyvirus indicaron la necesidad de disponer de técnicas de alta sensibilidad y fidelidad para el diagnóstico específico de este virus que permita asistir dicho programa y el de manejo integrado de plagas de este cultivo.
Este trabajo tuvo como objetivo desarrollar una RT-PCR para el diagnóstico específico del virus del moteado del pimiento (PepMoV).
MATERIALES Y MÉTODOS ]]>
Análisis in silico de la capacidad de la pareja de cebadores diseñados para la detección específica del PepMoVPara el diseño de los cebadores específicos se tomó como referencia la secuencia nucleotídica del PepMoV aislado en la Florida (AF501519). Se seleccionó, como molde, una región variable en el genoma viral que comprende parte del extremo 5' no traducible y amino terminal de la proteína P1.
El fragmento seleccionado se procesó mediante la herramienta bioinformática Primer-Blast, disponible en el sitio: http://www.ncbi.nlm.nih.gov/Genbank. Este análisis permitió obtener una lista de cebadores que, posteriormente, se analizaron mediante el programa Oligo (versión 7.4). Los mismos se alinearon a la secuencia molde con el programa MEGA (versión 5) para verificar lo obtenido en los análisis bioinformáticos. Se sintetizaron los cebadores por el Centro de Ingeniería Genética y Biotecnología de Cuba (CIGB) (http://www.cigb.edu.cu).
Ensayo de RT-PCR
Se utilizaron hojas de la región apical de 10 plantas de pimiento (cv. Español) inoculadas con el aislado M50 de PepMoV, en las que, previamente, se observaron los síntomas típicos de este virus. También se utilizaron diez plantas sanas, del mismo cultivar, como controles negativos de los ensayos. Se evaluaron las plantas antes y después de ser inoculadas, mediante PCR con cebadores Nib 2F/Nib 3R, según lo descrito por Zheng et al. (8).
Para la extracción de ARN total de las plantas, se partió de 1 g de material vegetal y se procedió según lo descrito por Singh (9). Los productos obtenidos se conservaron a -80ºC y se analizaron mediante electroforesis en gel de agarosa (0,8 %) en tampón TBE 1X y teñido con 1 µg. ml-1de bromuro de etidio.
Los ADNc se obtuvieron a partir de 2µl del ARN total y se incubaron con el cebador oligo-dT a 70°C (5 minutos). A continuación, la mezcla se puso rápidamente en hielo durante 3 minutos. La reacción de transcripción inversa se realizó con la enzima M-MLV (Promega), de acuerdo a las instrucciones de la casa comercial.
A partir del resultado del análisis in silico de los cebadores diseñados, se realizó un ensayo inicial de la PCR, como base para la optimización de la técnica. La mezcla de reacción consistió en: 12,5 µl de Green Master Mix (Promega); 0,4 µM de cada oligonucleótido y 2 µl de ADN complementario [940 pg.µl-1], en un volumen final de 25 µl. La amplificación se desarrolló en un termociclador Biometra T Gradient con el programa de amplificación diseñado (Tabla 1).
Los productos de la PCR (10 µl de cada producto) se analizaron mediante electroforesis en gel de agarosa al 0,8%, en tampón TBE 1X y teñido con 1 µg.ml-1 de bromuro de etidio. Para determinar la talla aproximada de los productos se incluyó un marcador de peso molecular de 1000 pb (Promega).
Se realizaron ensayos de PCR para la evaluación de la temperatura óptima de hibridación de los cebadores al molde, concentración óptima de los cebadores, límite de detección, reproducibilidad intraensayo e interensayo, así como la evaluación de la especificidad de los cebadores. ]]>
Para cada ensayo se utilizaron, como controles positivos, plantas de pimiento infectadas con PepMoV y controles negativos (plantas de pimiento sin inocular) mantenidos en condiciones controladas de casa de cristal, evaluados previamente con cebadores genéricos, según lo descrito por Zheng et al. (8). En cada etapa experimental se varió una condición y las restantes se mantuvieron constantes.Evaluación de la temperatura óptima de hibridación de los cebadores
Para determinar la temperatura óptima de hibridación de los cebadores se realizaron dos ensayos de PCR, uno a 59ºC y el otro a 60ºC. El resto de las condiciones de los ensayos de PCR se realizaron de acuerdo a lo descrito previamente para la PCR preliminar. Para esto se utilizaron diez controles positivos y diez negativos, evaluados previamente y utilizando cebadores genéricos (8).
Evaluación de la concentración óptima de los cebadores
La concentración óptima de los cebadores se determinó mediante la evaluación de tres concentraciones diferentes (0,24 µM; 0,32 µM y 0,40 µM). El ensayo de PCR se evaluó de acuerdo a lo establecido en la PCR preliminar, excepto que se realizó con la temperatura óptima de hibridación de los cebadores, determinada en el ensayo anterior. Se realizaron dos réplicas del experimento y se evaluaron diez plantas positivas y diez negativas como controles del ensayo, previa evaluación con cebadores genéricos (8).
Evaluación del límite de detección o sensibilidad analítica
Se determinó la concentración inicial del ADNc obtenido procedente de cinco muestras de pimiento previamente inoculadas. La lectura de la D.O. se realizó a una longitud de onda de 260 nm en un espectrofotómetro Lassos Spec (Lasso Biotech, LTDA). Una vez calculada la concentración inicial de la muestra (1), se procedió a la realización de diluciones (1:5; 1:10; 1:50) para la obtención de soluciones con concentraciones desde 940 pg.µl-1 hasta 18,8pg.µl-1. Estos ADNc también se evaluaron puros (1 y 2 µl) en el ensayo de RT-PCR. Se realizaron dos repeticiones del experimento.
Evaluación de la repetitividad del ensayo: estimaciones preliminares
De los controles disponibles y evaluados previamente (8), se seleccionaron cuatro controles positivos y uno negativo, se realizaron repeticiones intraensayos e interensayos de la PCR con las condiciones seleccionadas, de acuerdo a los resultados obtenidos en los experimentos anteriores.
Evaluación de la especificidad analítica del ensayo ]]>
Para confirmar la especificidad del ensayo diseñado se evaluaron: una muestra de ADN positivo a begomovirus, procedente del laboratorio de Virología Vegetal del Centro Nacional de Sanidad Agropecuaria (CENSA) (http://www.censa.edu.cu); una muestra de ADN positivo a bacteria (Pseudomonas fluorescens), facilitado por el laboratorio de Bacteriología del CENSA; una muestra de ADN positivo a fitoplasmas y ADNc de planta positiva a PVY, procedente del laboratorio de Virología del CENSA. Como controles positivos se utilizaron los ADNc de dos plantas de pimiento infectadas con PepMoV y, como control negativo, se empleó ADNc de pimiento sano.
RESULTADOS Y DISCUSIÓN
Análisis in silico de la capacidad de una pareja de cebadores para la detección específica del PepMoV
Como resultado de la evaluación in silico se diseñó la pareja de cebadores que se denominaron PepM1/PepM2, como la adecuada para el diagnóstico específico de PepMoV; los mismos posibilitan la amplificación del fragmento de interés. El análisis de los cebadores permitió confirmar la no formación de estructuras secundarias ni de dímeros; además, presentan enlaces fuertes en los extremos 3´. La secuencia de nucleótidos de estos oligonucleótidos, así como las posiciones que ocupan en la secuencia viral se muestran a continuación:
PepM1 (5'GCACTCTACACTCGCAATGGC3') (análogo a las posiciones 153-174 de la cadena viral).
PepM2 (5'AAATCCCCTACTGTGCCGTCC 3') (Complementario a las posiciones 922-944 de esta secuencia).
El análisis realizado con la herramienta Blast, para evaluar la homología de estos cebadores con secuencias depositadas en base de datos, evidenció una identidad del 100% con la secuencia del PepMoV aislado en la Florida (AF501519) y no mostró identidad con el PVY, potyvirus que se describió como el principal problema del cultivo anteriormente (3).
La evaluación in silico de los cebadores diseñados para el diagnóstico específico de PepMoV posibilitó predecir el rango de evaluación de la temperatura óptima de hibridación de los cebadores (57-70ºC), la posición de hibridación de los cebadores al molde, la longitud de la secuencia diana, la temperatura de fusión y el por ciento de guanina-citosina (Tabla 2). También se obtuvo que, para el buen funcionamiento de la enzima, la concentración de Mg2+ libre es de 0,7 nM, dato que resulta de vital importancia, ya que el magnesio es cofactor de la enzima polimerasa (10).
Los datos obtenidos posibilitaron conocer, teóricamente, las condiciones adecuadas para el funcionamiento de la RT-PCR. También fue posible ubicar las posiciones de hibridación de los cebadores. Estos resultados teóricos resultaron de mucho valor para la estandarización de dicha técnica, pues permitieron establecer el punto de partida para la optimización de los parámetros críticos. Todo ello evidenció, desde un punto de vista teórico, que los cebadores fueron capaces de hibridarse a la región de interés, lo que sugiere su utilidad para el diagnóstico específico de PepMoV. ]]>
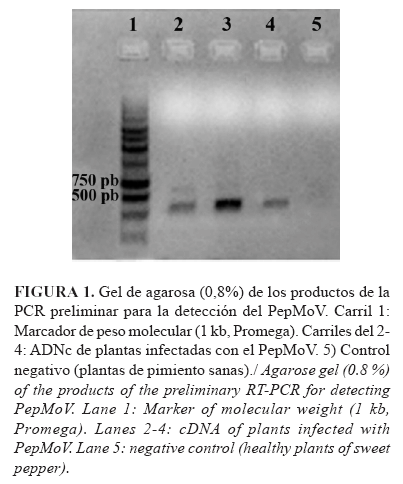
Ensayo de RT-PCREl ensayo preliminar de PCR evaluado mostró una banda, aproximadamente, de 700 pb (Fig. 1) para las réplicas de ADNc evaluadas, aunque también evidenció la presencia de una banda tenue por encima de los 750 pb, en la reacción con las condiciones empleadas. La Figura 1 muestra, de forma representativa, la evaluación con 3 controles positivos.
Este resultado puede deberse a que los cebadores no hibridan en la posición predicha por el análisis in silico y sí en una región cercana, por eso la talla no coincide con lo predicho. Es importante destacar que existe una alta similitud nucleotídica en la región de la proteína de la cápsida (CP), región taxonómica y conservada entre los miembros de esta familia viral (1), pero en este caso la región seleccionada (extremo 5' no traducible y amino terminal de la proteína P1), como molde para el diseño de cebadores específicos, mostró ser altamente variable entre los miembros de este género viral. Otros análisis bioinformáticos de la proteína P1 evidenciaron gran variabilidad en longitud y secuencia de aminoácidos en esta región del genoma (11), lo cual puede influir en la diversidad de especies y con la especialización de su transmisión a diferentes hospedantes. Los cebadores se diseñaron sobre la base de la secuencia del aislado de PepMoV de la Florida, con el cual el aislado cubano comparte el 98 % de identidad de secuencias en la región que codifica para la CP; esto probablemente explicaría también que la diferencia puede deberse a variabilidad en el genoma del aislado cubano, aspecto característico en este género viral.
Evaluación de la temperatura óptima de hibridación de los cebadores
Los ensayos correspondientes a las PCR realizadas a 59ºC y 60ºC de hibridación de los cebadores, respectivamente, amplificaron un fragmento de igual talla (aproximadamente 700pb) (Fig. 2A y B). El análisis electroforético de los productos de amplificación de ambos ensayos mostró mayor intensidad de las bandas para el ensayo a 59ºC.
En este ensayo aparecen, de forma repetida, tres de las réplicas de ADNc utilizadas; no se observaron diferencias entre sí, con respecto a la intensidad de las bandas visualizadas (Fig. 2B). En ambos ensayos el control negativo no mostró producto amplificado. Teniendo en cuenta estos resultados se seleccionó la temperatura de 59ºC como la óptima para el ensayo específico.
A baja temperatura de hibridación, el apareamiento de los cebadores con la región diana y con regiones no específicas suele ser similar. Por tanto, un aumento en la temperatura de hibridación favorece el apareamiento con la secuencia específica, debido a la mayor estabilidad del apareamiento específico (12). Sin embargo, a 60ºC, aunque desaparecieron las bandas inespecíficas, la amplificación de la región de interés fue menos nítida que en el ensayo a 59ºC. Por esta razón se determinó 59ºC como la temperatura óptima de hibridación de los cebadores.
Evaluación de la concentración óptima de los cebadores
El ensayo para determinar la concentración óptima de los cebadores amplificó un fragmento de igual talla (700 pb aproximadamente) para todas las réplicas de ADNc, en cada concentración evaluada (Fig. 3). El análisis electroforético mostró que, a medida que aumentó la concentración de los cebadores, desde 0,24 µM a 0,4 µM aumentó ligeramente la intensidad de las bandas. Se seleccionó 0,32 µM como la concentración óptima de los cebadores, pues se amplificó un producto de fácil visualización y nitidez mediante electroforesis y resultó más económico que la máxima concentración evaluada. ]]>

Este es un paso importante, debido a que al ajustar la concentración de los cebadores se puede optimizar la temperatura de fusión y, con ello, la temperatura de acoplamiento a la molécula blanco. Ajustando la concentración inicial de ambos cebadores entre 0,1 y 0,5 µM, se puede modular la temperatura de acoplamiento en ±2ºC (13). Gibbs y Mackenzie (14) informaron una concentración de 0,3 µM óptima de un par de cebadores para amplificar una región conservada del genoma de potyvirus. Majumder et al. (15) estandarizaron una RT-PCR para la detección del virus del enanismo amarillo de la cebolla (OYDV) y del virus latente del chalote (SLV). En este trabajo se determinó 0,2 µM como la concentración óptima de los cebadores diseñados para OYDV y 0,4 µM para SLV.
La concentración de los cebadores debe propiciar el desplazamiento de la reacción hacia la formación de los productos. No obstante, una alta concentración podría provocar la formación de estructuras secundarias o las uniones inespecíficas al ADN molde (7). Por estas razones, la concentración de los cebadores constituye un parámetro influyente en el adecuado funcionamiento de una PCR (16).
Para evitar la formación de estructuras secundarias, otras consideraciones pueden ser: utilizar tres partes o 37,5 µM de base análoga de guanina dc7GTP, en conjunto con una parte o 12,5 µM de dcGTP, desestabilizará la formación de estructuras secundarias en el producto. Cuando el ADN molde es desnaturalizado pueden formarse estructuras secundarias y la incorporación de dc7GTP evita la formación de estas estructuras aberrantes. Los detergentes no iónicos funcionan suprimiendo la formación de estructuras secundarias y ayudan a estabilizar la enzima ADN polimerasa. Se utilizan en la reacción los detergentes no iónicos, como son Triton X-100, Tween 20 o NP-40, a razón de 0,1 a 1,0%. Estos pueden neutralizar el efecto inhibitorio del SDS, un contaminante ocasional en los protocolos de extracción (17).
Evaluación del límite de detección o sensibilidad analítica
El ensayo de RT-PCR evaluado mostró un bajo límite de detección del genoma viral en el ADNc obtenido de la planta (94 pg.µl-1) al evaluar la dilución de 1:10 de la muestra pura. El ensayo mostró la capacidad de la técnica de amplificar a esta baja concentración el fragmento de 700 pb, aproximadamente, y se observó que se pierde la señal en la evaluación de la dilución de 1:50 (Fig. 4).
Los ensayos de PCR muestran, por lo general, bajo límite de detección debido al principio de amplificación, ya que no necesitan la completa integridad del agente a detectar. No obstante, los ensayos de este tipo pueden no alcanzar todo el potencial de detección esperado debido a diferentes factores, entre los que se destacan: la presencia de inhibidores de la reacción presentes en la muestra, un inadecuado diseño de cebadores o la no optimización del ensayo (7).
Evaluación de la repetitividad del ensayo: estimaciones preliminares
Las repeticiones efectuadas, intra e interensayo, mostraron 100 % de concordancia (Fig. 5 A y B), por lo que no fue necesario realizar análisis estadísticos que determinaran diferencias entre ellos. ]]>
Evaluación de la especificidad analítica del ensayoLos resultados obtenidos no evidencian señal de amplificación en los ADN infectados con el PVY, begomovirus, bacterias y fitoplasmas; mientras que sí se obtuvo una banda de la talla esperada en los controles infectados con PepMoV (Fig. 6).
La especificidad analítica es uno de los parámetros más referidos en la estandarización de técnicas de diagnóstico (18). En este trabajo no se evidenció señal de amplificación en los ADN infectados con begomovirus, bacterias, fitoplasmas y PVY. En los controles infectados con PepMoV se obtuvo una banda de la talla esperada, lo cual sugiere la gran especificidad de los cebadores diseñados y las condiciones de amplificación seleccionadas para la detección confiable y específica del virus del moteado del pimiento en Cuba.
A partir de los resultados obtenidos se fijaron las siguientes condiciones como óptimas para el establecimiento del método específico: 12,5 µl de Green master Mix (Promega), cebadores PepM1/PepM2 [0,32 µM] y 2 µl de ADNc en un volumen final de 25 µl y un programa de amplificación (Tabla 3) que puede ser utilizado en Cuba para la detección específica del aislado cubano de PepMoV.
Los resultados obtenidos resultan de gran importancia, ya que en la actualidad los síntomas asociados a este virus están ampliamente distribuidos en el cultivo en el país (3) y ha desplazado a otros potyvirus, como son el virus Y de la papa (PVY) que anteriormente estaban presentes en campo; sin embargo, no se disponía de un método molecular específico para la detección del mismo.
La herramienta molecular obtenida permitirá apoyar los programas de mejoramiento genético y de manejo integrado del cultivo en el país, pues esta RT-PCR estandarizada es confiable, factible y altamente específica para el diagnóstico del PepMoV en Cuba con un bajo límite de detección.
AGRADECIMIENTOS
Los autores del presente trabajo desean agradecer a International Foundation for Science (IFS) por el financiamiento de esta investigación. ]]>
REFERENCIAS
1. Quiñones ML, Martínez Y, Arana F, Martínez MA, Zamora L, Miranda I, Zerbini FM. Coexistencia de potyvirus y begomovirus en el cultivo del pimiento (Capsicum annuum L.) en Cuba. Rev Protección Veg. 2013;28(1):36-44.
2. Revers F, García JA. Molecular biology of potyviruses. Adv Virus Res. 2015;92:101-99. doi: 10.1016/bs.aivir.2014.11.006.
3. González G, Font C, Valdés S. Diagnóstico de virus vegetales a nivel de grupo en el cultivo del pimiento (Capsicum annuum L.) mediante la técnica de microscopía óptica. Fitosanidad. 2002;6(3):3-7.
4. Quiñones ML, Arana F, Alfenas-Zerbini P, Soto M, Ribeiro D, Díaz A, et al. First report of Pepper mottle virus in sweet pepper in Cuba. New Disease Reports. 2011;24:16. doi:10.5197/j.2044-0588.2011.024.016. ]]>
5. Ivanov KI, Eskelin K, Lõhmus A, Mäkinen K. Molecular and cellular mechanisms underlying potyvirus infection. J Gen Virol. 2014;95:1415-1429. doi: 10.1099 /vir.0.064220-0.
6. Robles HL, González FAC, Gill LEM, Pérez ML, López DJC. Virus fitopatógenos que afectan al cultivo de chile en México y análisis de las técnicas de detección. Tecnociencia Chihuahua. 2010;IV:72-86.
7. Díaz A, Quiñones ML, Arana F, Soto M, Hernández A. Potyvirus: características generales, situación de su diagnóstico y determinación de su presencia en cultivo de pimiento en Cuba. Rev Protección Veg. 2010;25(2):69-79.
8. Zheng L, Rodoni BC, Gibbs MJ, Gibbs AJ. A novel pair of universal primers for the detection of potyviruses. Plant Pathology. 2010;59:211-220. doi: 10.1111/j.1365-3059.2009.02201.x.
9. Singh RP, Nie X, Singh M, Coffin R, Duplessis P. Sodium sulphite inhibition of potato and cherry polyphenolics in nucleic acid extraction for virus detection by RT-PCR. J Virol Methods. 2002;99:123-131. ]]>
10.De Dios TL, Ibarra C, Velasquillo C. Fundamentos de la reacción en cadena de la polimerasa (PCR) y de la PCR en tiempo real. Investigaciones en discapacidad. 2013;2(2):70-78.
11.Pasin F, Simón-Mateo C, García JA. The Hypervariable amino-terminus of P1 protease modulates potyviral replication and host defense responses. PLoSPathog. 2014;10(3):e1003985. doi:10.1371/journal.ppat.1003985.
12.Ishii K, Fukui M. Optimization of annealing temperature to reduce Bias caused by a Primer mismatch in Multitemplate PCR. Appl Environ Microbiol. 2001;67(8): 3753-3755. doi: 10.1128/AEM.67.8.3753-3755.2001.
13.Applied Biosystems. Applied biosystems user's manual PCR basics©. The Perkin-Elmer Corporation. 1998: 1-8.
14.Gibbs A, Mackenzie A. A primer pair for amplifying part of the genome of all potyvirids by RT-PC. J Virol Methos. 1997;63:9-16. ]]>
15.Majumder S, Baranwal VK, Joshi S. Simultaneous detection of Onion yellow dwarf virus and Shallot latent virus in infected leaves and cloves of garlic by duplex RT-PCR. J Plant Pathol. 2008;90(2):371-374.
16.Hecker KH, Roux KH. High and low annealing temperatures increase both specificity and yield in touchdown and step down PCR. Biotechniques. 1996;20:478-485.
17.Lorenz TC. Polymerase Chain Reaction: Basic protocol plus troubleshooting and optimization strategies. J Vis Exp. 2012;63:e3998. doi:10.3791/3998.
18.Crowther JR. nELISA. Theory and Practice. Humana Press, Totowa, New Jersey. 1995. 223pp.
]]>
Recibido: 6 octubre 2015.
* Autor para correspondencia: Madelaine QuiñonesPantoja. Correo electrónico: madeqp@censa.edu.cu. ]]>