Incidencia y caracterización molecular del Potato Leafroll Virus (PLRV) en las principales regiones productoras de papa de Colombia
Incidence and Molecular Characterization of Potato Leafroll Virus (PLRV) in Colombian most Important Potato Crops Regions
José F. Gil Ramírez,1 José M. Cotes Torres2 y Mauricio Marín Montoya1
1Laboratorio de Biología Celular y Molecular, Facultad de Ciencias, Universidad Nacional de Colombia, Sede Medellín, josefergil@gmail.com; mamarinm@unal.edu.co.
2Departamento de Ciencias Agronómicas, Facultad de Ciencias Agropecuarias, Universidad Nacional de Colombia, Sede Medellín, jmcotes@unal.edu.co.
RESUMEN ]]>
El cultivo de la papa representa uno de los renglones agrícolas de mayor importancia en Colombia. Alcanza cerca de 162 000 ha y una producción que supera los 2 721 396 t. Este cultivo es afectado por diversas plagas y enfermedades, entre las que se destacan las polillas de los tubérculos, el tizón tardío y los problemas virales. Los virus reducen los rendimientos y la calidad del tubérculo en cultivos de papa de todo el mundo, y el PLRV es uno de los más limitantes en diferentes latitudes, incluida la región andina. Esta investigación se planteó con el fin de evaluar la incidencia y características genotípicas del PLRV en los cultivos de papa de los departamentos colombianos de Antioquia, Boyacá, Cundinamarca y Nariño. Los resultados indicaron la ocurrencia de PLRV en los cuatro departamentos evaluados, con una incidencia promedio del 20%. Los análisis moleculares generados a partir de secuencias del gen de la cápside viral (CP) indicaron muy bajo nivel de variación entre los aislamientos colombianos de este virus, y entre estos y las secuencias de cepas de referencia de otros lugares del mundo obtenidas de las bases de datos moleculares. Estos resultados enfatizan en la necesidad de reforzar las medidas fitosanitarias en los cultivos de papa del país.Palabras claves: ELISA, luteovirus del enrollado de patata, secuencia nucleotídica, Solanum tuberosum.
ABSTRACT
Potato is one of the most important crops in Colombia, reaching about 162.000 ha and a production of more than 2.721.396 t. This crop is affected by various pests and diseases, including the tuber moths, late blight and different viruses. Virus diseases reduce yields and tuber quality of potato worldwide. PLRV is one of the most limiting viruses of potato in different latitudes, including the Andean region. This research evaluated the incidence and genotypic characteristics of PLRV in potato crops from the Colombian provinces of Antioquia, Boyacá, Cundinamarca and Nariño. Results indicated the occurrence of PLRV in the four provinces studied, with an average incidence of 20%. Molecular analysis of sequences generated from the viral capsid gene (CP) indicated a very low level of variation among isolates of this virus, and between them and the sequences of PLRV strains from different countries obtained from molecular databases. These results emphasize the need to strengthen phytosanitary measures in potato crops of Colombia.
Key words: ELISA, nucleotide sequence, Potato leaf roll luteovirus, Solanum tuberosum.
INTRODUCCIÓN
El cultivo de la papa (Solanum tuberosum L.) en Colombia genera una producción de 2 721 396 t en aproximadamente 162 000 ha cosechadas. El rendimiento promedio del cultivo es de 16,8 t/ha, valor similar al promedio de rendimiento mundial. La producción nacional está distribuida en su orden en los departamentos de Cundinamarca, Boyacá, Nariño y Antioquia con 398 926, 297 492, 266 112 y 119 854 t, respectivamente [Ministerio de Agricultura y Desarrollo Rural, 2006].
Uno de los principales limitantes de la producción de este cultivo en Colombia son los problemas virales. En el mundo se reportan al menos 25 virus y viroides [Salazar, 1995, 2006], entre los que se destacan por su importancia económica PVX (Potato virus X, Potexvirus), PVY ( Potato virus Y, Potyvirus), PVS (Potato virus S, Carlavirus), PLRV (Potato leafroll virus, Polerovirus) y el viroide PSTVd (Potato spindle tuber viroid, Pospiviroid). Adicionalmente, en Colombia es muy limitante el PYVV(Potato yellow vein virus, Crinivirus) [Guzmán et al., 2004]. ]]>
Los problemas virales en el cultivo de la papa afectan la producción de tubérculos al reducir el área fotosintética, la movilización de nutrientes y por tanto la acumulación de carbohidratos para la formación adecuada de los tubérculos, lo cual está asociado directamente a reducciones del rendimiento, y además imposibilita al agricultor para obtener tubérculo semilla a partir de su propio cultivo [Salazar, 1995]. En sistemas agrícolas tradicionales, como los que predominan en las zonas alto-andinas de Suramérica, esta situación es frecuente y conduce a la pérdida de vigor de la semilla, y a un efecto acumulativo de diferentes virus que termina por reducir dramáticamente los rendimientos al cabo de varios ciclos de siembra-cosecha.El PLRV es uno de los virus que generan mayores pérdidas en el rendimiento de los cultivos de papa a nivel mundial, con reportes que varían del 20 al 90% [Rahman y Akanda, 2010], y es aún más limitante cuando su infección ocurre en forma simultánea con otros virus; así, por ejemplo, en evaluaciones en Colombia sobre la variedad ICA-Puracé se encontró que el efecto individual del PLRV ocasionó pérdidas del 47% con respecto al testigo libre de virus, mientras que su asociación con PVY redujo la producción en un 55% [Guerrero y Martínez, 1980]. Es la especie tipo del género Polerovirus (Luteoviridae). Se caracteriza por presentar una cápside desnuda con simetría icosahédrica con diámetro de 24 nm y un genoma de ARN de cadena sencilla positiva de alrededor de 5900 nt, cuyo extremo 5' se encuentra asociado a VPg [Taliansky et al., 2003].
Tiene dividido su genoma en ocho marcos de lectura abiertos (ORF) densamente empaquetados, con el ORF 1 que solapa el ORF 0 y el ORF 3 traslapado con el ORF 4 [Pooramini et al., 2010]. El virus emplea diferentes estrategias para la modulación de su ARN; así, los tres ORF proximales al 5' (0 al 2) se expresan a partir del ARNg, y los ORF cercanos al extremo 3' (3 al 7), se expresan a partir de ARNsg [Taliansky et al., 2003]. El ORF 0 está involucrado en el desarrollo de la sintomatología, y se cree que es un supresor del silenciamiento de genes en sus hospedantes. P1 tiene funciones de proteinasas y contiene la secuencia que codifica para VPg y posiblemente para una helicasa. El ORF 2 codifica para RdRP, mientras que el ORF 3 lo hace para la CP de 23 kDa. El ORF 4 codifica para una proteína de movimiento, y la fusión de los ORF 3 y 5 genera una proteína estructural menor de 80 kDa, que se cree participa en la transmisión del virus por áfidos. Los ORF 6 y 7 han sido descritos recientemente, y aunque sus funciones no se conocen, se especula que P7 tiene propiedades de unión a ácidos nucleicos [Taliansky et al., 2003; Pooramini et al., 2010].
Los áfidos transmiten el PLRV de manera persistente no propagativa, que se multiplica en el floema del huésped. Los insectos más eficientes para su transmisión son Myzus persicae y Macrosiphum euphorbiae. Los síntomas principales que ocasiona este virus en papa corresponden a enanismos y enrollamiento de hojas, acompañados de una grave reducción en el rendimiento. En plantas indicadoras como Datura stramonium se pueden observar amarillamientos sistémicos entre venas, y en Physalis floridiana se presenta clorosis sistémica entre venas y enrollamiento de hojas [Büchen-Osmond, 2010].
A pesar de la importancia económica que representan los virus en los cultivos de papa de Colombia, las investigaciones sobre sus niveles de incidencia y niveles de variación genética son muy pocos [Guerrero y Martínez, 1980; Sánchez de Luque et al., 1991; Guzmán et al., 2004]. Ya que en la actualidad se desconocen los niveles de incidencia de los principales virus en los cultivos de papa de Colombia, esta investigación se planteó con el objetivo de evaluar la presencia del PLRV, uno de los más limitantes en el país, en cuatro de los principales departamentos cultivadores de este tubérculo, mediante la utilización de pruebas de ELISA. Adicionalmente se realizó una caracterización molecular de aislamientos de las diferentes regiones a partir de la secuenciación del gen de la cápside viral (CP), y se realizaron comparaciones con cepas de diferentes países, cuyas secuencias se encuentran reportadas en las bases de datos moleculares.
MATERIALES Y MÉTODOS
Para la determinación de los niveles de incidencia de PLRV en cultivos de papa de Colombia se realizaron muestreos aleatorios en ocho cultivos de diferentes variedades ubicados en tres zonas productoras del departamento de Antioquia (zona 1: Oriente [La Unión, Sonsón]; zona 2: Oriente cercano [Santuario, Marinilla, Carmen de Víboral]; zona 3: norte Antioqueño [Santa Rosa de Osos, Don Matías]); tres zonas en Cundinamarca (zona 4: Zipaquirá; zona 5: Villa Pinzón; zona 6: Occidente [Madrid, Cota]); dos zonas en Boyacá (zona 7: Turmeque, Ventaquemada; zona 8: Tunja, Siachoque) y dos zonas en Nariño (zona 9: Pasto, zona 10: Ipiales).
En cada cultivo se realizó una colección aleatoria de cuatro muestras conformadas por dos foliolos jóvenes para generar una muestra compuesta (bulk). Una vez en el laboratorio, las 320 muestras (cuatro muestras por ocho cultivos por diez zonas) se evaluaron para la detección de PLRV mediante pruebas de DAS-ELISA con anticuerpos policlonales. Los resultados colorimétricos fueron cuantificados en un equipo de espectrofotometría, y se incluyó en cada prueba un control positivo (suministrado en forma liofilizada) y uno negativo. Los pozos fueron considerados con reacción positiva cuando la lectura de absorbancia a 405 nm presentó un valor mínimo del doble de la lectura obtenida en el control negativo, según el criterio de Matthews (1993).
Los resultados de niveles de incidencia se analizaron a través de un modelo lineal generalizado aleatorio donde se consideró una distribución binomial para la variable incidencia, y se utilizó una función de ligamiento logit. Los efectos aleatorios fueron departamentos, zonas y cultivos dentro de zonas. Para el análisis estadístico se utilizó el procedimiento GLIMMIX del programa estadístico SAS versión 9.1.3. ]]>
Para el análisis de variabilidad genética de aislamientos colombianos de PLRV se utilizaron secuencias parciales de la región del genoma que codifica para CP. El ARN molde se obtuvo mediante extracciones de ARN total con un kit para tejido de plantas, a partir de al menos una muestra de cada región bajo estudio que resultara positiva para PLRV en las pruebas de ELISA. Las reacciones de RT-PCR se realizaron en dos pasos, con los cebadores PLRV-F (5' CGC GCT AAC AGA GTT CAG CC 3') y PLRV-R (5' GCA ATG GGG GTC CAA CTC CAA CTC AT 3') [Singh et al., 1995], en un volumen de 20 ìL, incluidos 1,9 ìL de agua, 4 ìL de buffer RT 5X, 4 ìL de MgCl2 25 mM, 2 ìL de dNTPs 10 mM, 1 ìL de cebador reverso (PLRV-R) 10 ìM, 0,1 ìL de inhibidor de RNasa (40U/ìL), 2 ìL de enzima M-MuLV Transcriptasa Reversa (20 U/ìL) y 5 ìL de ARN. El programa consistió de 37°C por 60 min y 75°C por 15 min. Las reacciones de PCR se realizaron en un volumen de 25 ìL con 16,2 ìL de agua, 2,5 de buffer de enzima 10X, 1,8 ìL de MgCl2 (25 mM), 0,5 ìL de dNTPs (10 mM), 0,5 ìL de cada cebador (10 ìM), 0,2 ì: de Taq ADN polimerasa (5 U/ìL) y 2,5 ìL de ADNc, aunque en algunas ocasiones fue necesario preparar diluciones de 1:5 y 1:10 de ADNc. El programa de PCR consistió de 95°C por 30 s, seguido de 40 ciclos de 95°C por 30 s, 52°C por 45 s, 72°C por 1 min y una extensión final a 72°C por 5 min.Los productos amplificados se separaron por electroforesis en gel de agarosa al 1,5% suplementado con 4 ìL de bromuro de etidio (10 mg/mL), visualizados con un transiluminador UV y su tamaño verificado por comparación con el marcador de peso molecular Generuler 100 pb DNA. Los amplicones del tamaño esperado se purificaron directamente del gel mediante un kit de separación de agarosa para proceder a su secuenciación en ambos sentidos.
Las secuencias obtenidas con cada cebador fueron editadas mediante los programas BioEdit 6.0.6 y Chromas 1.45. Se construyeron secuencias consenso y se confirmó su identidad mediante el programa BLASTn. Las secuencias generadas se compararon con aquellas de referencia obtenidas del banco de genes, se alinearon mediante el programa Clustal W y la matriz de similitud generada fue utilizada para obtener un árbol filogenético basado en máxima parsimonia con la utilización del programa PAUP 4.0b [Swofford, 1998]. El soporte de la topología interna de los dendrogramas fue determinado por análisis de bootstrap con 1000 remuestreos [Felsenstein, 1985].
RESULTADOS Y DISCUSIÓN
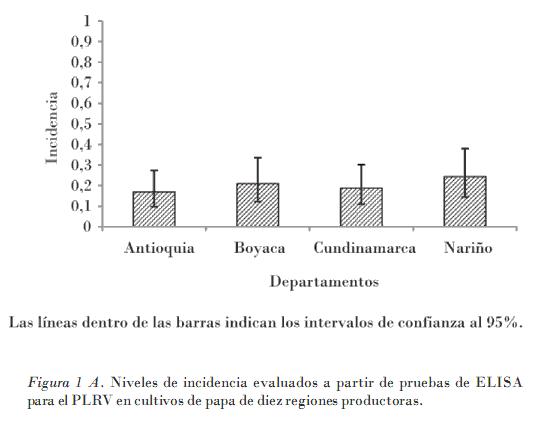
Los resultados de la detección serológica del PLRV indican su presencia generalizada en las zonas productoras de papa de Colombia, con un promedio de incidencia del 20% (Fig. 1A). No se encontraron diferencias significativas para la incidencia entre departamentos, ni entre las regiones evaluadas dentro de cada departamento, aunque zonas como Zipaquirá, Tunja y el Oriente Antioqueño presentaron niveles inferiores al 17% de incidencia, mientras que en los cultivos de Turmeque- Ventaquemada y Villapinzón la incidencia superó el 25% (Fig. 1B).
En Colombia son muy pocos los trabajos que han evaluado la incidencia de virus en cultivos de papa. Uno de ellos fue el realizado por Guzmán et al. (2004), donde se estimó la incidencia de virus mediante inmuno-impresión en 800 muestras de Solanum phureja de municipios de Nariño y Cundinamarca, y encontraron valores de incidencia del 86, 72, 39 y 91% para los virus PVS, PVY, PVX y PLRV, respectivamente. Esta misma evaluación se realizó al material del banco de germoplasma de la Colección Central Colombiana (CCC) de S. phureja, y en este caso los valores de incidencia fueron del 20, 19, 5,7 y 6,6%, para esos mismos virus [Guzmán et al., 2004]. Más recientemente, Guzmán et al. (2010), al evaluar la CCC de papa en campo en un grupo de 581 accesiones de Solanum sect. Petota mediante pruebas de ELISA, encontraron que el 98,8% de todas las muestras analizadas arrojó resultados positivos para al menos uno de los cuatro virus evaluados (PVS, PVY, PVX y PLRV), y se detectó el PVS en el 85% de las accesiones, seguido de PLRV (77,4%), PVY (58,6%) y PVX (13,9%). Estos resultados enfatizan en la importancia de reforzar los programas de manejo integrado de enfermedades virales en Colombia, más aún cuando el programa de certificación de semilla de papa en este país permite solo hasta el 5% de presencia de virus (PLRV, PVY, PVX, PVS) en semilla certificada, el 2% para registrada y el 1% para semilla básica [Zapata, 2004].
De esta forma resulta evidente que los programas de manejo integrado de enfermedades virales de papa en Colombia requieren ser reforzados con un control más estricto del tubérculo semilla desde la propia categoría de élite y de semilla básica, la implementación de prácticas culturales que eviten la presencia de hospedantes alternos y disminuyan la dispersión del virus dentro de lotes de siembra y entre fincas, y para el caso particular del PLRV que garanticen el mantenimiento por debajo de los umbrales de daño de las poblaciones de áfidos vectores del virus, tales como M. persicae y M. euphorbiae. Lógicamente estas medidas requieren de programas agresivos de extensión rural, del fortalecimiento técnico de las organizaciones gremiales de cultivadores de papa y de la implementación de nuevas herramientas de diagnóstico y seguimiento de la sanidad de lotes de semilla y cultivos en campo por parte de los organismos de sanidad vegetal estatales.
Por otra parte, las pruebas de RT-PCR con los cebadores PLRV-F y PLRV-R generaron los amplicones del tamaño esperado de ~330 pb (Fig. 2). El análisis de 18 secuencias de este virus y 14 secuencias de referencia obtenidas del banco de genes de cepas de PLRV de diferentes orígenes geográficos indicó niveles de identidad para la región estudiada superiores al 97%. Estos valores se presentaron tanto entre cepas obtenidas de cultivos de papa de los cuatro departamentos colombianos evaluados como con respecto a las cepas de referencia utilizadas. El Cereal yelow dwarf virus (CYDV), un polerovirus utilizado como grupo externo en el análisis, presentó niveles de identidad cercanos al 77% con respecto a las cepas de PLRV incluidas en el estudio.El análisis filogenético utilizó 328 posiciones, 241 de las cuales resultaron constantes, 72 variables pero no informativas y 15 informativas para el método de máxima parsimonia. El dendrograma presentó un índice de consistencia (CI) de 0,87, índice de retención (RI) de 0,83 y un índice de homoplasia (HI) de 0,12, y agrupó en un solo clado (100% bootstrap) todas las cepas de PLRV, incluidas las obtenidas en este estudio y aquellas de referencia, sin que se presentara ningún subgrupo interno soportado con altos valores de bootstrap (Fig. 3). Las secuencias de los aislamientos colombianos de PLRV fueron depositadas en el banco de genes bajo los números de accesión HQ396176 a HQ396193.
El PLRV ha sido uno de los virus más estudiados y prevalentes en el cultivo de la papa a nivel mundial, así como uno de los que probablemente causan mayores daños en el cultivo [Taliansky et al., 2003; Plchova et al., 2009]; sin embargo, reiteradamente no se ha encontrado una notable diferencia entre las secuencias de sus aislamientos alrededor del mundo [Plchova et al., 2009], hecho que se repitió en este trabajo al analizar las secuencias obtenidas de la región que codifica para CP. El análisis filogenético mostró diferencias máximas del 3% con respecto a las secuencias de referencia, y agrupó a todas las cepas en un solo clado. Aunque estos bajos niveles de variación entre aislamientos de PLRV se han encontrado en diversos trabajos, tal información no podría ser asumida a priori para la región andina de Colombia, por cuanto esta zona hace parte del centro de origen de la papa, lo cual supondría una mayor probabilidad de que se presenten mayores niveles de variación en los hospedantes y sus virus fitopatógenos como resultado de su coevolución por largos períodos [Salazar, 1995, 2006].
Se ha planteado que los bajos niveles de variación encontrados en este virus son posiblemente resultado de su reciente divergencia a partir de otro virus que se especializó en su infección a papa, o a las fuertes presiones de selección que ejerce la estrecha base genética de las variedades de S. tuberosum cultivadas en el mundo [Guyader y Ducray, 2002].
Trabajos recientes indican que los mayores niveles de variación en el PLRV se encuentran principalmente en la región codificante para P0. Esa región permite la discriminación entre diferentes aislamientos del virus y la distinción en tres grupos de aislamientos, con valores de identidad que fluctúan entre el 94,7 y el 98,5% [Plchova et al., 2009]. Es por esto que, con el fin de complementar este estudio, será necesario analizar las secuencias del ORF P0 en las cepas colombianas, de manera que sea posible confirmar o no la alta uniformidad genética encontrada en esta investigación. Se espera que los resultados de esta investigación sean utilizados para el diseño de herramientas de diagnóstico viral ajustadas a las realidades genotípicas del PLRV en los cultivos de papa del país, metodologías necesarias para el apoyo de los programas de certificación de tubérculo semilla y para la formulación de programas de manejo integrado de las enfermedades virales.
CONCLUSIONES
• Se determinó una incidencia promedio del 20% del PLRV en los cultivos de cuatro de los principales departamentos productores de papa de Colombia.
• Los análisis de secuencias de la región de la cápside del PLRV permitieron inferir muy bajos niveles de variación entre las cepas colombianas de este virus y aquellas reportadas de diferentes países del mundo. ]]>
AGRADECIMIENTOS
Se agradece el soporte económico del Ministerio de Agricultura y Desarrollo Rural de Colombia (proyecto 090- 2007S4527-87-08) de la Universidad Nacional de Colombia, Sede Medellín, Fedepapa y Fritolay para la realización de esta investigación, así como el apoyo en la colección de muestras en el departamento de Nariño de la profesora Luz Estela Lagos, de la Universidad de Nariño.
REFERENCIAS
Büchen-Osmond, C.: «The Universal Virus Database of the International Committee on Taxonomy of Viruses», www.ictvdb.org (consultado en julio de 2010).
Felsenstein, J.: «Confidence Limits on Phylogenies: An Approach Using the Bootstrap», Evolution 39:783-791, EE. UU., 1985.
Guerrero, O.; G. Martínez: «Evaluación de pérdidas ocasionadas en la variedad de papa Puracé por los virus Potato virus X, Potato virus Y y Potato leafroll virus», Fitopatol. Colomb. 9:3-40, Colombia, 1980.
Guyader, S.; D. G. Ducray: «Sequence Analysis of Potato leafroll virus Isolates Reveals Genetic Stability, Major Evolutionary Events and Differential Selection Pressure Between Overlapping Reading Frame Products», J. of Gen. Virology 83:1799-1807, Inglaterra, 2002.
Guzmán, M.; M. Caro; Y. García: «Validación de la técnica serológica de inmunoimpresión para detección de diferentes virus que afectan el cultivo de papa», I Taller Nacional sobre Patógenos del Suelo, Virus e Insectos Plaga Diferentes a Tecia solanivora, Bogotá, Colombia, 2004, p. 41.
Guzmán, M.; V. Román; L. Franco; P. Rodríguez: «Presencia de cuatro virus en algunas accesiones de la Colección Central Colombiana de papa mantenida en campo», Agron. Col. 28:225-233, Colombia, 2010.
Matthews, R. E. F: Diagnosis of Plant Virus Diseases. CRC Press, Canadá, 1993. Ministerio de Agricultura y Desarrollo Rural: «Observatorio Agrocadenas. Cuarto informe de coyuntura 2006», http://www.agrocadenas.gov.co/documentos/coyuntura/InfCoyunturapapa4.pdf (consultado en: marzo de 2009).
Plchova, H.; N. Cerovska; T. Moravec; P. Dedic: «Molecular Analysis of Potato leafroll virus Isolates from the Czech Republic», Virus Genes 39:153-155, Springer-Verlay; Nueva York; Heidelberg, Berlín, 2009.
Pooramini, N.; J. Heydarnejad; H. Massumi: «Incidence and Molecular Analysis of Potato leafroll virus in Iran», J. Phytopathol. 158:182-185, Alemania, 2010.
Rahman, M. S.; A. M. Akanda: «Effect of PLRV Infected Seed Tuber on Disease Incidence, Plant Growth and Yield Parameters of Potato», Bangladesh J. Agril. Res. 35:359-366, Bangladesh, 2010.
Salazar, L. F.: Los virus de la papa y su control, CIP, Lima, 1995.
Salazar, L. F.: «Emerging and Re-Emerging Potato Diseases in the Andes», Potato Res. 49:43-47, EE. UU., 2006.
Sánchez de Luque, C.; P. Corzo; O. Pérez: «Incidencia de virus en papa y su efecto sobre rendimientos en tres zonas agroecológicas de Colombia», Rev. Lat. Papa 4:36-51, Perú, 1991.
Singh, R. P.; J. Kurz; G. Boiteau; G. Bernard: «Detection of Potato leafroll virus in Single Aphids by the Reverse Transcription Polymerase Chain Reaction and Its Potential Epidemiological Application», J. of Virol. Methods 55:133-143, EE. UU., 1995.
Swofford, D. L.: PAUP: Phylogenetic Analysis Using Parsimony (*and Other Methods), Version: 4, Sinauer Associates, Sunderland, EE. UU., 1998.
Taliansky, M.; M. A. Mayo; H. Barker: «Potato leafroll virus: a Classic Pathogen Shows New Tricks», Mol. Plant Pathol. 4:81-89, Inglaterra, 2003.
Zapata, J. L.: «Algunos aspectos sobre los virus de la papa en Colombia», I Taller Nacional sobre Patógenos del Suelo, Virus e Insectos Plaga Diferentes a Tecia solanivora, Colombia, 2004, pp. 24-40.
Recibido: 10/2/11
Aceptado: 10/3/11
]]>