RESUMEN
Se estudió la respuesta inmune de un grupo de pacientes con neuropatía epidémica y de individuos controles mediante la técnica de inmunoblotting frente a las proteínas del virus Coxsackie y a las proteínas de la cepa de efecto lento aislada en nuestro laboratorio. Se estudiaron 13 sueros de pacientes con neuropatía epidémica y 9 sueros controles. De los 13 sueros estudiados, 8 (61,5 %) reconocieron a la proteína VP1 y 2 sueros (15,3 %) a la proteína VP0 de la cepa 47/93. De los 9 controles estudiados, 4 (44,4 %) reconocieron la proteína VP1 y 3 sueros (33,3 %) la proteína VP0 solamente. Con el antígeno preparado a partir de la cepa de efecto lento, en 5 (38,5 %) sueros de pacientes y 2 sueros (22,5 %) de controles se obtuvo una señal específica. Es de destacar en este último caso que la proteína observada tenía un peso molecular de 41 300 D, era de menor talla que la proteína precursora detectada frente a la cepa 47/93, que fue de 45 000 D.
Descriptores DeCS: WESTERN BLOTTING/métodos; NEURITIS/sangre; BROTES DE ENFERMEDADES; PROTEINAS VIRALES; COXSACKIEVIRUS.
Durante la segunda mitad del año 1991, se reportó en Cuba un número inusual de casos de pacientes con neuritis óptica. Lejos de presentarse ésta como una epidemia clásicamente conocida, hizo su aparición una nueva entidad cuyo modo de propagación, origen y forma de transmisión eran desconocidos.1
La causa de dicha entidad aún no ha sido determinada; sin embargo, existen manifestaciones clínicas, hallazgos a partir de investigaciones de laboratorio y encuestas epidemiológicas que permiten plantear la hipótesis de una causa multifactorial, donde no podemos descartar los agentes biológicos y entre éstos a los virus, así como los déficits nutricionales, los agentes tóxicos o la asociación de varios de ellos.
Después de la inoculación de líquidos cefalorraquídeos de varios pacientes con neuritis en células de riñón de mono verde africano (Vero), se ha podido aislar e identificar, mediante la neutralización con antisueros específicos, un grupo de cepas pertenecientes al grupo Coxsackie.
Sin embargo, en otro grupo de cultivos inoculados se ha producido la aparición de un efecto citopático lento (ECP) de un comportamiento inusual, el cual no progresa hasta afectar todas las células, tal como ocurre con el ECP de los Enterovirus.
El presente trabajo tuvo como objetivo estudiar la especificidad de la respuesta inmune humoral en sueros de pacientes con neuritis epidémica y en sueros controles frente a las proteínas, tanto del virus Coxsackie como de la cepa de crecimiento lento aislada en nuestro laboratorio. Este estudio fue realizado mediante la técnica de inmunoblotting de alta especificidad que nos permite una caracterización parcial de la respuesta inmune humoral.
MÉTODOS
]]> Sueros positivos: Se utilizaron 13 sueros de pacientes con neuropatía epidémica que tenían alto título de anticuerpos neutralizantes (mayores o iguales que 1/10) frente a la cepa 47/93 IPK (virus Coxsakie A9).Sueros controles: Se utilizaron 9 sueros procedentes de banco de sangre, 5 de ellos con títulos de anticuerpos neutralizantes detectables.
Sueros hiperinmunes: Se utilizaron sueros hiperinmunes de conejo contra la cepa 47/93. Coxsackie A9, Coxsackie B1 y B4 producidos por el laboratorio de Enterovirus del Instituto de Medicina Tropical "Pedro Kourí" (IPK).
Cepas virales: Se utilizaron las cepas de los virus Coxsakie B1, B2, B3, B4, B5 y B6, además de las cepas 47/93 y 44/93 mantenidas en el Laboratorio de Enterovirus del IPK.
Células. Para la preparación de los antígenos virales se utilizaron células Vero (procedentes de la ATCC), mantenidas en el Laboratorio de Cultivo Celular.
Preparación de antígenos virales. Se inocularon 0,5 mL de cada uno de los virus empleados a una multiplicidad de 0,5 unidades formadoras de placas (ufp)/mL en frascos de células Vero (75 cm2). Después de 1 h de adsorción a 37 °C se procedió a la adición del medio de mantenimiento constituido por medio de 199 con 5 % de suero de ternera fetal y antibióticos a la dosis adecuada.
Los cultivos fueron mantenidos a 37 °C y observados diariamente hasta la aparición del efecto citopático (ECP) de 100 %, momento en el cual fueron cosechados. Posteriormente fueron congelados y descongelados (-70 y 37 °C) El producto de la última descongelación fue centrifugado a 10 000 rpm y el sobrenadante obtenido se mantuvo a 4 °C, el precipitado fue sonicado 3 veces por 15 s a 15 Herz y centrifugado a 2 500 rpm por 10 min, ambos sobrenadantes se unieron y se centrifugaron a 2 500 rpm por 2 h a 4 °C. Finalmente el precipitado obtenido fue resuspendido en 200 mL de buffer Laemmli2 y guardado a -20 °C hasta la realización de la electroforesis. En iguales condiciones fue preparado el control celular.
En el caso de la cepa 44/93 IPK se procedió a normalizar otro método de extracción del antígeno a partir del cultivo celular.(3) Después de obtenido un ECP completo, las células fueron desprendidas con policía de goma y fueron lavadas 3 veces con solución salina fosfatada (PBS) 1x. Una vez eliminado el PBS del último lavado se añadieron 450 mL de buffer de lisis (PBS con 0,1 % de dodecil sulfato de sodio, 1 % de Nonidet P40 y 0,5 % de tritón X-100) y se sonicó a 15 Herz por 15 s por 3 veces, se centrifugó a 10 000 rpm durante 1 h y el sobrenadante se resuspendió en igual volumen de buffer Laemmli 2x y se guardó a 4 °C hasta la realización de la electroforesis. En iguales condiciones se preparó un control celular.
Electroforesis en gel de pollacrilamida (PAGE). Se siguió el método de Laemmli,2 se utilizó como gel superior una solución de acrilamida al 5 %, y como gel inferior separador una al 12,5 % para los antígenos de los Enterovirus y otra al 10 % para la cepa 44/93. Se aplicaron 15 mL de cada antígeno. La corrida electroforética se realizó a 120 volts durante 1 h, en cada electroforesis se incluyó un patrón de peso molecular (LKB Mw rango 14 300 -71 500 kD).
Inmunoblotting. Después de la separación electroforética de las proteínas, éstas fueron transferidas a una membrana de nitrocelulosa (LKB 0,45 mm) en un equipo de transferencia semiseco (LKB 2117-250 Novablot) a 50 mA durante 16 h.
]]> Una vez transferidas las proteínas se procedió a la coloración de la membrana de nitrocelulosa con una solución de rojo Ponceau durante 15 min para verificar si la transferencia había sido adecuada, posteriormente se decoloraron con agua destilada. Seguidamente se procedió al bloqueo de la membrana con solución de Tris borato salina (TBS)-Tween 20 al 0,1 % y albúmina bovina (BSA) al 4 % durante 1 h a temperatura ambiente con agitación, una vez bloqueadas las membranas fueron guardadas a 4 °C hasta su utilización. Tanto los sueros hiperinmunes como los humanos fueron diluidos 1/20 y se incubaron con las membranas de nitrocelulosa durante 2 h a temperatura ambiente con agitación. Posteriormente se realizaron 3 lavados con TBS de 10 min cada uno a temperatura ambiente con agitación. Se utilizaron conjugados anti-IgG de conejo y antihumano marcados con peroxidasa (Sigma) diluidos 1/500 en TBS-Tween 20 al 0,1 % y se incubaron por 1 h a temperatura ambiente con agitación. El revelado se realizó utilizando una solución de 3-3 diaminobencidina (SIGMA) durante 5 a 10 min, la reacción se detuvo con agua destilada.RESULTADOS
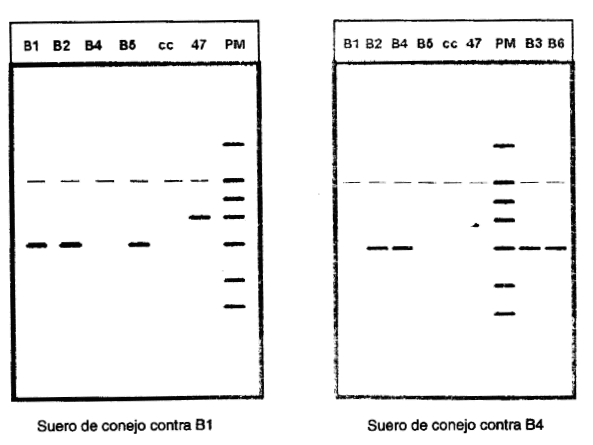
En la figura 1 se presentan los resultados obtenidos en el inmunoblotting con los sueros hiperinmunes de conejo anti-Coxsackie B1 y anti B4. Ambos mostraron reacciones cruzadas frente a varios de los antígenos estudiados, reconocimiento de la proteína VP1 de los Coxsackie B1, B2, B5 y la cepa 47/93 IPK por el antisuero anti-Coxsackie B1, y reconocimiento de la VP1 de los Coxsackie B1, B2, B3, B4, B5 y B6 con el antisuero anti Coxsackie B4. Cada antisuero reaccionó con su virus homólogo.
FIGURA 1. Resultados obtenidos en el inmunoblotting con los sueros hiperinmunes de conejo anti-Coxsackie B1 y B4. En un caso se enfrentó el suero hiperinmune anti-Coxsackie B1 a los antígenos obtenidos a partir del cultivo celular (B1, B2, B4 y B5, y 47/93). En el otro caso se enfrentó el suero hiperinmune anti-B4 a los antígenos B1,B2,B3,B4,B5,B6 y 47/93. Se incluyó como control el antígeno del control celular.
Al analizar la preparación de los antígenos obtenidos a partir de células inoculadas con los diferentes virus, se pudo corroborar que las tallas de las proteínas obtenidas fueron las adecuadas al ser comparadas con el patrón de peso molecular.
En la figura 2 se muestra el resultado de la técnica de inmunoblotting mediante el suero humano 81 frente a las proteínas estructurales de los virus Coxsackie B1, B2, B3, B4, B5 y B6, Coxsackie A9 y las cepas 47/93 IPK y 44/93 IPK. Con dicho suero, se observaron bandas correspondientes a las proteínas VP1 y VP2 frente a los virus Coxsackie B1, B2 y B3 y contra la proteína VP1 del resto de los virus estudiados. Al parecer, las proteínas de la cepa 44/93 no fueron reconocidas. Es de señalar que las proteínas detectadas frente a las cepas de Coxsackie A9 y 47/93 fueron de mayor talla que las de los Coxsackie B.
FIGURA 2. Resultados del inmunoblotting con la utilización del suero humano 81 frente a las proteínas estructurales de los virus Coxsackie B1, B2, B3, B4, B5, B6 y A9 y las cepas 47 y 44 IPK, así como frente al control celular (cc).
En la tabla 1 se presentan los resultados obtenidos al estudiar en un grupo de pacientes y controles la respuesta específica frente a las proteínas de la cepa 47/93 IPK. Como puede observarse, de 13 sueros de pacientes estudiados, 8 (61,5 %) reconocieron a la proteína VP1 y 2 (15,3 %) a la VP0. En 3 casos no se observó reacción. De los controles, 4 (44,4%) reconocieron a la VP1, 3 (33,3 %) la VPO solamente y 2 (22,2 %) fueron negativos. Los sueros de los pacientes reconocen en un mayor porcentaje la VP1 de la cepa 47/93 IPK que los sueros controles.
En la tabla 2 se presentan los resultados del inmunoblotting, se utilizó como antígeno la cepa 44/93 IPK preparada según Gold y otros.3 Con el antígeno preparado de esta forma se obtuvo una señal específica en 5(38,5 %) de los sueros positivos y en 2 (22,5 %) de los controles, es de señalar que la proteína observada tenía un peso molecular de 41 300 D, con menor talla que la proteína precursora detectada frente a la cepa 47/93 IPK, que tenía 45 000 D.
]]> TABLA 1. Resultados del inmunoblotting donde se enfrentaron los sueros de los pacientes y controles a las proteínas de la cepa 47/93 IPK (Coxsackie A9)
| Proteínas | Pacientes | Controles |
| VP1 | 8 | 4 |
| VP2 | ]]> - | - |
| VP0 | 2 | 3 |
| Precursores | 2 | 3 |
TABLA 2. Resultados del inmunoblotting donde se enfrentaron los sueros de los pacientes y controles a las proteínas de la cepa 44/93 IPK (de efecto lento)
]]>| Proteínas | Pacientes | Controles |
| VP1 | - | - |
| VP2 | - | ]]> - |
| VP0 | - | - |
| Precursores | 5 | 2 |
DISCUSIÓN
La neuropatía epidémica ha sido considerada hasta el momento una entidad nueva cuya causa aún no está precisada, aunque se considera que factores nutricionales y tóxicos pudieran estar relacionados con la aparición de dichas manifestaciones clínicas. La causa viral no ha sido descartada, la cual es apoyada por los aislamientos realizados a partir de líquidos cefalorraquídeos de pacientes con neuritis. Asimismo estudios realizados por Balmaseda y otros en población sana, pertenecientes a zonas de alta y baja incidencia de la enfermedad, mostraron mayor número de anticuerpos a la cepa 47/93 IPK, de forma significativa en aquellos pertenecientes a zonas de alta incidencia lo que, demuestra una posible relación entre el virus y la enfermedad.4
Con estos antecedentes nos propusimos estudiar y comparar la respuesta inmune de algunos pacientes con neuropatía epidémica y de un grupo control frente a las proteínas del Coxsackie A9 aislado (47/93 IPK) y del agente productor de ECP lento (44/93 IPK).
]]> Para desarrollar este objetivo se comenzó a trabajar en la normalización de la técnica de Western Blot, se utilizaron cepas de referencia de Enterovirus según el método descrito por Mertens y otros.5 El inmunoblotting se realizó en presencia de sueros hiperinmunes producidos en conejos contra dichas cepas.De acuerdo con la literatura, los antisueros anti-Coxsackie B, muestran reacción cruzada entre los diferentes agentes de este grupo de estudio, los Enterovirus Coxsakie B, y aparentemente en dependencia del antisuero muestran reacción cruzada con otros Enterovirus. Los resultados obtenidos permitieron evaluar que la preparación de los antígenos había sido la adecuada, ya que las proteínas detectadas mostraban un patrón de PM acorde con lo reportado.
Como paso siguiente se valoró la especificidad del método, se enfrentó un grupo de antígenos de Enterovirus con un suero humano con títulos de anticuerpos neutralizantes conocidos contra éstos.
En los resultados obtenidos en los inmunoblotting, tanto con los sueros hiperinmunes de conejos como con el suero humano, se demuestra la reactividad cruzada de los anticuerpos IgG a diferentes Enterovirus. Varios autores 5-7 plantean que esta reacción cruzada no está relacionada directamente con el título de anticuerpos neutralizantes y que dentro de los Enterovirus, algunos grupos, como los Poliovirus, generalmente no presentan reacción cruzada. Por otra parte, no se puede descartar si la extensión de la reacción cruzada depende de la respuesta individual del hospedero inmune (sea un conejo o un humano). Se ha planteado para los sueros humanos que esta extensión de la reactividad cruzada puede ser proporcional al número de infecciones por Picornavirus experimentado en el individuo.
Al estudiar en un grupo de pacientes y controles la respuesta específica frente a las proteínas de la cepa 47/93 IPK, los sueros de los pacientes reconocen en un mayor tanto por ciento a la VP1 de la cepa 47/93 IPK que los sueros controles. Pozzeto y otros6 reportaron un hallazgo similar al demostrar diferencias significativas en sueros de pacientes con infecciones por ECHO 4 cuando se comparan con los controles. Varios autores plantean que los anticuerpos IgG reconocen sólo la VP1 de los Enterovirus y que los anticuerpos IgM reconocen a las proteínas VP1, VP2 y VP3, y que pueden aparecer reacciones cruzadas a VP1 y VP2.6,7
En este trabajo se utilizó un conjugado antiinmunoglobulinas totales que es capaz de reconocer en la reacción tanto IgG como IgM, así que se puede descartar que en el caso en que se detectó la proteína VP0 fueran anticuerpos de tipo IgM los reconocidos. Es preciso destacar que en los sueros estudiados no se observó respuesta específica a la proteína VP1 de la cepa de efecto lento.
Fue llamativo encontrar, tanto en pacientes como en los controles, anticuerpos a proteínas con un mayor peso molecular, las cuales se denominaron precursoras, por no corresponder con la talla de las proteínas estructurales de estos virus ni presentar reacciones cruzadas con las proteínas celulares.
No se puede precisar la importancia de estos resultados. Reigel y otros reportaron reacciones similares por inmunoblotting a proteínas no estructurales con pesos moleculares entre 15 000 y 70 000 D cuando aún utilizaban virus ECHO purificado. La naturaleza de estas proteínas no ha sido precisada pero se consideran precursoras en la replicación del ácido nucléico viral de estos agentes.
Considerando que la mayoría de los aislamientos realizados a partir del líquido cefalorraquídeo de los pacientes fue del tipo lento, era importante estudiar y conocer la especificidad de la respuesta de los anticuerpos a las proteínas de este agente en los sueros de estos pacientes. Por tal motivo escogimos la cepa 44/93 IPK para este estudio. En un principio, el antígeno se preparó en la forma descrita anteriormente por Mertens y otros5 para los Enterovirus. No obstante, en todos los casos en que se realizó el inmunoblotting con sueros de pacientes y controles no se obtuvo señal de reconocimiento. Este resultado y las propias características del virus hizo pensar que se debía cambiar la forma de preparación del antígeno, por lo que se decidió preparar un antígeno celular según el método de Gold y otros para los Herpesvirus. Este método de preparación del antígeno resultó exitoso y se obtuvieron resultados satisfactorios en la técnica de inmunoblotting. Los resultados logrados en el inmunoblotting de la cepa 47/93 IPK demuestran que algunos sueros de pacientes presentan anticuerpos específicos contra dicho agente; no obstante, se pudo correlacionar el título de anticuerpos neutralizantes anticepa 47/93 IPK ni el cuadro clínico de los pacientes con la presencia o ausencia de señal frente a la cepa 44/93 IPK.
El no contar con una batería de anticuerpos monoclonales a los virus estudiados nos permitió conocer la relación antigénica entre las proteínas detectadas en las cepas 47 y 44, aunque el suero hiperinmune preparado contra la cepa 44/93 fue capaz de neutralizar en forma significativa a la cepa 47/93 e indicar una posible relación antigénica entre éstas.
]]> En todos los experimentos realizados se incluyeron controles celulares, no se observaron reacciones de los sueros con las proteínas de las células.SUMMARY
The immune response of a group of patients with epidemical neuropathy and of controls was studied by the immunoblotting technique against proteins of the Coxsackie virus and the proteins of slow effect isolated in our laboratory. 13 sera of patients with epidemical neuropathy and 9 sera of controls were studied. Of the 13 sera studied, 8 (61.5 %) recognized protein VPI and 2 sera (15.3 %) protein VP0 of the strain 47.93. Of the 9 controls studied, 4 (44.4 %) recognized protein VPI and 3 (33.3 %) protein VP0 only. With the antigen prepared from the slow effect strain it was obtained a specific signal in 5 (38.5 %) sera of patients and in 2 sera (22.5 %) of controls. It should be stressed that in this last case the protein observed had a molecular weight of 41 300 D, and that its size was smaller than that of the preceeding protein detected against the strain 47.93 was of 45 000 D.
Subject headings: BLOTTING, WESTERN/methods; NEURITIS/blood; DISEASE OUTBREAKS; VIRAL PROTEINS; COXSACKIE VIRUSES.
REFERENCIAS BIBLIOGRÁFICAS
- Epidemic neuropathy, Cuba. Weekly Epidemiological Records 1993;37:270.
- Laemmli UK. Cleavege of structural proteins during the assembly of the head of bacteriophage T4. Nature 1970;(227):680-5.
- Gold D, Ashley R, Hunter H, Verdon M, Leach L, Mills J, et al. Immunoblot analysis of the humoral immune response in primary Cytomegalovirus infection. J Infect Dis 1988; 152(2):319-26.
- Balmaseda A, Laferté J, Soler M, Vázquez S, Rodríguez L, Otero A, et al. Utilización del ELISA y ultramicro ELISA en la identificación de una cepa de Coxsackie A9 aislada
- durante la epidemia de neuropatía en Cuba. Rev Cubana Med Trop 1995;47(1):44-9.
- Mertenz TH, Pika U, Eggers HG. Cross antigenicity among Enterovirus as reveale by immunoblot technique. Virology 1983;129:431-42.
- Pozzeto B, Gaudin OG, Luncht FR, Hafid J, Ros A. Detection of immunoglobulin G, M, and A, antibodies to Enterovirus structural proteins by immunoblot technique in ]]> Echovirus type 4 infected patients. J Virol Meth 1990; 29:143-56.
- Reigel F, Burkhardt F, Schilt U. Reaction pattern of immunoglobulin M and G antibodies to Echovirus 11 Structural Proteins. J Clin Microbiol 1984;19(6):870-74.
Recibido: 1 de agosto de 1996. Aprobado: 17 de febrero de 1997.
Lic. Mayra Muné. Instituto de Medicina Tropical "Pedro Kourí", Apartado 601, Marianao 13, Ciudad de La Habana, Cuba.
]]>