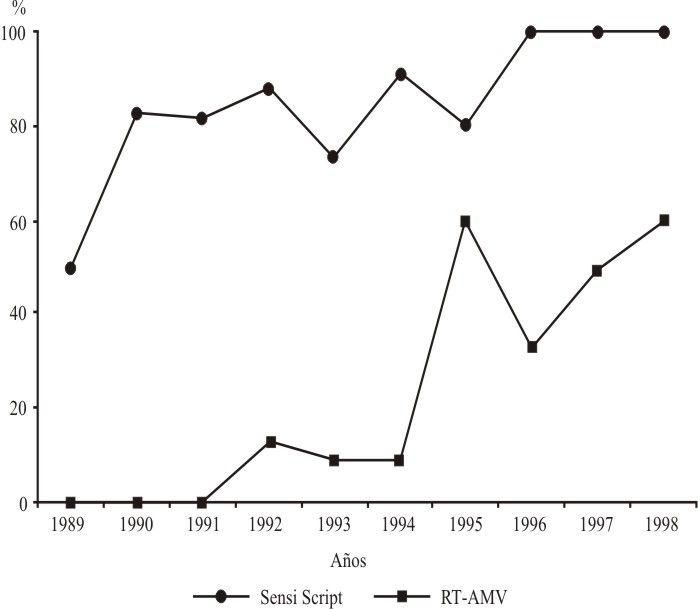
Fig. Porcentaje de recobrado de material genético según el año de toma de muestra y el sistema enzimático empleado.
]]>
Dra. Sonia Resik Aguirre,1 Dra. Li-Hua Ping,2 Dr. Julio A. Barrios Olivera,3 Dra. Vivian Kourí Cardellá4 y Dr. Ronald Swanstrom5
Se demostró la eficacia de la enzima transcriptasa inversa SensiScript para obtener material genético útil en la secuenciación de ácido nucleico de VIH-1, a partir de sueros colectados entre 1989 y 1998 y conservados a temperatura subóptima. Con el empleo de la enzima SensiScript se obtuvo amplificación del ARN del VIH-1 en 86,5 % de las muestras estudiadas, comparado con 20 % al utilizar la enzima AMV-RT. En 13,5 % de las muestras no se obtuvo amplificación con ninguna de las 2 enzimas empleadas.
DeCS: REACCIONES EN CADENA POR POLIMERASA DE TRANSCRIPTASA REVERSA/ métodos; VIH-1; ANALISIS DE SECUENCIA DE ARN; TESTS ENZIMATICOS.
La aplicación de la reacción en cadena de la polimerasa (RCP) en la biología molecular ha tenido un impacto sorprendente. El proceso de RT-RCP (reverso transcripción- reacción en cadena de la polimerasa) es un procedimiento altamente sensible que ha sido utilizado para detectar moléculas de ARN, obtener material útil para secuenciación de ácidos nucleicos y como un paso en el clonaje de copias de ADN complementario (ADNc) a partir de ARN. La amplificación exitosa por RT-RCP requiere de la confluencia de una serie de factores, entre los cuales la calidad de la muestra y el proceso de extracción del ARN desempeñan un papel fundamental.1
]]>
| Cebador | Secuencia (5´-3´) | Posición* |
| g1u | ATGGGTGCGAGAGCGTCAGTATTA | 790-813 |
| ]]>
g1.1u | GGTGCGAGAGCGTCAGTATTA | 793-813 |
| g2.1u | AAAGACACAGCAGGCAGCAG | 1128-1147 |
| g2u | CACCTAGGACTTTGAATGCATG | 1232-1253 |
| g1d | ]]>
TGGGGTGGCTCCTTCTGATAATGC | 1309-1332 |
| g2d | GGCATGCTGTCATCATTTCTTC | 1819-1840 |
| e1u | CAATTCCCATACATTATTGTGC | 6859-6880 |
| e1d | CAATTAAAACTATGTGTTGTAATTTC | ]]>
7332-7357 |
| e2u | GATATGAGGGACAATTGGAGAAGTG | 7644-7668 |
| e2d | GCCTGGAGCTGTTTAATGCCC | 7937-7957 |
* Según cepa HIVHXB2 (F033819)
]]>

Fig. Porcentaje de recobrado de material genético según el año de toma de muestra y el sistema enzimático empleado.
]]>
La enzima SensiScript es una reverso transcriptasa nueva, única, heterodimérica recombinante (expresada en E. coli), diferente de la del virus maloney de la leucemia murina (MMLV) o de la del virus de la mieloblastosis aviar (AMV), y se recomienda para muestras que contengan < 50 ng de ARN. Ha sido utilizada en la técnica de expresión diferencial (differential display) para el estudio de ARN mensajero.9
Al obtenerse solo 20 % de positividad al emplear la enzima AMV y debido a la limitada cantidad de suero con la cual se contaba y la certeza de que las condiciones de almacenamiento no habían sido las idóneas, es que se decide, posteriormente, utilizar la enzima SensiScript; para garantizar un incremento del recobrado de un ARN, que además de degradado en su mayoría, debía estar en muy bajas concentraciones.
Como se ha planteado anteriormente, en este estudio fueron utilizadas muestras de suero para, a partir de estas, extraer material genético. El obtener la secuencia de ácidos nucleicos de las muestras de estos pacientes era de vital importancia y por ser fallecidos no podía contarse con una muestra de plasma fresco y conservado a una temperatura óptima. Un gran número de autores recomienda el uso de plasma libre de células para la obtención de ARN de VIH a utilizar en los estudios moleculares. No obstante, existen reportes que reflejan un coeficiente de variación en la cantidad de copias de ARN/100 uL de muestra de entre 0,09 a 0,8 al comparar el recobrado del plasma con el del suero.7,10 Además, muestras de suero sometidas a ciclos de congelación y descongelación muestran un incremento en el número de copias de ARN (+ 0,073 unidades log).7,11 Por otra parte, la mayoría de las muestras de sangre utilizadas en estudios moleculares de VIH son transportadas en congelación y mantenidas a - 70 °C como plasma libre de células hasta su estudio. Ginocchio7 demostró que la disminución en las cantidades de virus en el plasma al cabo de los meses no fue significativa, pero observó un decrecimiento de 0,3 unidades log al realizar la comparación con el suero.
Con estos resultados se puede concluir que la enzima Sensiscript constituye una herramienta valiosa en el recobrado de ARN de VIH-1, para el análisis genotípico a partir de sueros conservados a temperatura subóptima; esto resulta de vital importancia, no solo para el VIH, sino para otros virus ARN y da la posibilidad de utilizar muestras de suero mantenidas en los laboratorios, bajo estas condiciones de temperatura, hasta por una década.
The efficiency of SensiScript reverse transciptase to obtain useful genetic material in the sequencing of the nucleic acid from HIV-1, starting from sera collected between 1989 and 1998 and kept at suboptimal temperatures, was proved. On using the SensiScript enzyme it was obtained an amplification of the RNA of the HIV-1 in 86.5 % of the studied samples, compared with 20 % on using the AMV-RT enzyme . No amplification was obtained in 13.5 % of the studied samples with any of the 2 enzymes used. ]]>
.
Recibido: 4 de abril de 2003. Aprobado: 8 de mayo de 2003.
Dra. Sonia Resik Aguirre. Instituto de Medicina Tropical "Pedro Kourí". Apartado 601, Marianao 13, Ciudad de La Habana, Cuba. Correo electrónico: sresik@ipk.sld.cu
1 Máster en Virología. Especialista de II Grado en Microbiología. Investigadora Auxiliar. Profesor Instructor. Instituto de Medicina Tropical "Pedro Kourí" (IPK).
2 Investigadora. Center for AIDS Research. Universidad de Chapel Hill, Carolina del Norte, EE. UU. ]]>
3 Especialista de I Grado en Microbiología (IPK).
4 Máster en Virología. Especialista de II Grado en Microbiología. Investigadora Auxiliar, Profesor Instructor (IPK).
5 Director. Center for AIDS Research, Universidad de Chapel Hill, Carolina del Norte, EE. UU.