Instituto Finlay
Lic. Alicia Aguilar Barroso,1 Dr. Nevis Amin Blanco,2 Lic. Luis Morier Díaz3 y Dra. Ela María Pérez Hernández4
Se evaluaron las cepas Hawaii, 3 Perú y Riberao Pretto de Dengue 1 en cuanto a su infectividad viral en las líneas celulares Vero y HepG2, por las técnicas de inmunofluorescencia indirecta. El tropismo celular in vitro de los virus del dengue es diverso, pueden replicarse en una gran variedad de cultivos celulares cuya sensibilidad a la infección viral es variable. El mayor porcentaje de células infectadas en la línea celular HepG2 se obtuvo con las multiplicidades de infección más elevadas (0,04 para las cepas Hawaii y Riberao Pretto y 0,01 para la cepa 3 Perú). El mayor porcentaje de células HepG2 y Vero infectadas para las cepas estudiadas y el mayor título en el sobrenadante viral se obtuvo al quinto día. La línea celular Vero fue la más sensible a la infección viral, pues para los mismos valores de multiplicidad se detectó mayor número de células fluorescentes y mejor título viral en el sobrenadante de esta línea que de la HepG2. La cepa Hawaii permitió obtener mejores resultados al evidenciarse más rápido la infección de las líneas celulares estudiadas.
Palabras clave : Infectividad, dengue, líneas celulares.
El dengue es la enfermedad viral humana transmitida por artrópodos más importante en el mundo. Se estima que anualmente se producen de 50 a 100 000 000 de casos de fiebre dengue (FD) y 250 000 a 500 000 casos de fiebre hemorrágica del dengue (FHD). Esta enfermedad es causada por los 4 serotipos del virus dengue pertenecientes a la Familia Flaviviridae, Género Flavivirus los cuales son mantenidos en la naturaleza mediante un ciclo de transmisión urbano en áreas tropicales y subtropicales donde el Aedes aegypti es el principal vector. La enfermedad se presenta con un espectro clínico que incluye desde un cuadro asintomático hasta las formas hemorrágicas que ocasionan la muerte, si los pacientes no son correctamente tratados.1 Han sido descritos diferentes factores de riesgo para el desarrollo de la FHD y del síndrome de choque por dengue (FHD/SCD), entre los que se encuentran aspectos relacionados con el hospedero y los factores virales.2
El tropismo celular in vitro de los virus del dengue es diverso, pueden replicarse en una gran variedad de cultivos celulares primarios y continuos derivados de tejidos de mamíferos, aves y artrópodos,3 cuya sensibilidad a la infección viral es variable.4 Varios factores pueden estar implicados en esto, la presencia de receptores específicos en las diferentes células, el ambiente en el que ocurre el reconocimiento del receptor, así como la afinidad de la unión del virus a este en la superficie celular.5 Se ha planteado que la proteína E tiene un papel importante en la interacción del virus con la superficie celular6 y además se ha reportado que en presencia de pH ácido se favorece la entrada del virus en el citosol por estimulación de la fusión de membranas.7,8
El análisis del comportamiento biológico entre los virus de los distintos serotipos y entre cepas de un mismo serotipo ha sido ampliamente usado para obtener información sobre la implicación de estas variaciones en la patogenia de la enfermedad.9 Diferencias genotípicas entre cepas de dengue 2 cuyo comportamiento biológico difiere, han sido reportadas.10 Se ha hallado una asociación entre la FHD/SCD y el mayor número de cambios aminoacídicos y nucleotídicos encontrados en aislamientos de dengue 2 de pacientes,11 en este mismo sentido otros autores han demostrado relación entre las diferencias moleculares y los distintos grados de severidad de la enfermedad al analizar un grupo de asilamientos de dengue 2.12 En este estudio se evaluaron 3 cepas de dengue 1 en cuanto a su infectividad viral en las líneas celulares Vero y HepG2.
La línea celular C6/36 HT, empleada para el cultivo de las cepas virales, fue multiplicada en medio esencial mínimo eagle (MEM), 0,2 mM de aminoácidos no esenciales, glutamina 1 % y 10 % de suero fetal bovino inactivado (SFBI). El medio de mantenimiento utilizado para estas células fue el mismo pero con 2 % de SFBI.
La línea celular BHK 21 clono 15 se multiplicó en medio MEM con aminoácidos no esenciales 1 %, glutamina 1 % y 10 % SFBI.
Ambas líneas celulares fueron suministradas por el laboratorio de Cultivo de Células del Instituto de Medicina Tropical Pedro Kourí (IPK).
La línea celular Vero propagada en medio 199 suplementado con SBFI 10 % fue suministrada por el laboratorio de Cultivo de Células del Instituto Finlay.
La línea celular HepG2 fue multiplicada en medio de crecimiento Dulbecco MEM con 1 % de solución de glutamina 200 mM, aminoácidos no esenciales 1 % y 10 % SFBI (pH 6,8). Esta línea celular fue donada gentilmente por el profesor Jeremy Brook de la Universidad de Glasgow.
Cepas de virus dengue 1
Cepa estándar Hawaii: aislada de un paciente con FD en 1944 con 17 pases en cerebro de ratón lactante (CRL) y un pase en la línea celular C6/36HT.
Cepa 3 Perú: aislada de un paciente con FD en 1990 con 4 pases en la línea celular AP61.
Cepa H830 (Riberao Pretto): aislada en Brasil en 1991 de la sangre de una paciente con diagnóstico de FD con 4 pases en la línea celular C6/36HT.
]]> Titulación viral de las cepas por detección de focos mediante la técnica de inmunofluorescencia:A partir de monocapas confluentes de células BHK 21 clono 15, se preparó una suspensión celular de 5 x 105 células/mL en medio de crecimiento. Se añadieron 50 µL/pozo de dicha suspensión en placa de 96 pozos, las cuales se incubaron durante 24 h a 37 °C y 5 % de CO2. Pasado dicho tiempo se añadieron 50 µL del virus puro y sus diluciones en base 10 desde 10-1 hasta 10-6, se realizaron 3 réplicas por cada dilución viral. Posteriormente se incubaron a 37 ºC y 5 % de CO2 durante 4 h, después de las cuales se añadió el medio que contenía carboximetilcelulosa 1,5 %, SFBI 10 % y glutamina 1 % y se incubó en las condiciones anteriores durante 7 d.
Al cabo de este tiempo se siguió el procedimiento descrito por Igarashi13 modificado, se fijaron las monocapas celulares con metanol frío y se utilizaron la dilución 1/100 de líquido ascítico policlonal contra el virus dengue 1 y 1/1000 de un conjugado anti-IgG de ratón marcado con isotiocianato de fluoresceína. Posteriormente se realizó la observación en el microscopio de fluorescencia, se contó el número de focos fluorescentes por pozo y se calculó el título viral.
Estudio de infectividad viral
Para el estudio de infectividad viral se inocularon 50 μL de las cepas virales en células HepG2 y Vero a diferentes multiplicidades de infección (m.o.i.), en placas de 96 pozos. En la línea celular HepG2 se emplearon m.o.i. de 0,004 y 0,04 para las cepas Hawaii y Riberao Pretto y 0,001 y 0,01 m.o.i. para la cepa 3 Perú, mientras que en la línea celular Vero solo se utilizó 0,004 m.o.i. para las primeras y 0,001 m.o.i. para la segunda.
A los 3 y 5 d posinfección se recogió el sobrenadante de ambas líneas celulares infectadas para determinar presencia de virus, para lo cual se realizó la titulación por la técnica de detección de focos por inmunofluorescencia en células BHK 21 clono 15 descrita anteriormente. De forma paralela se determinó el porcentaje de células infectadas por los virus en las líneas celulares estudiadas. Para esto se fijaron las monocapas celulares infectadas con metanol frío para hacer la detección de antígeno dengue mediante la técnica de inmunofluorescencia indirecta.13 Posteriormente se realizó la observación en el microscopio de fluorescencia, determinándose el porcentaje de células fluorescentes para cada caso.
Los títulos de las cepas empleadas en el estudio, obtenidos por la lectura de los focos fluorescentes fueron los siguientes: 3 Perú, 5,2 x 103 UFF/mL; Hawaii, 2 x 104 UFF/mL y Riberao Pretto, 1,5 x 104 UFF/mL.
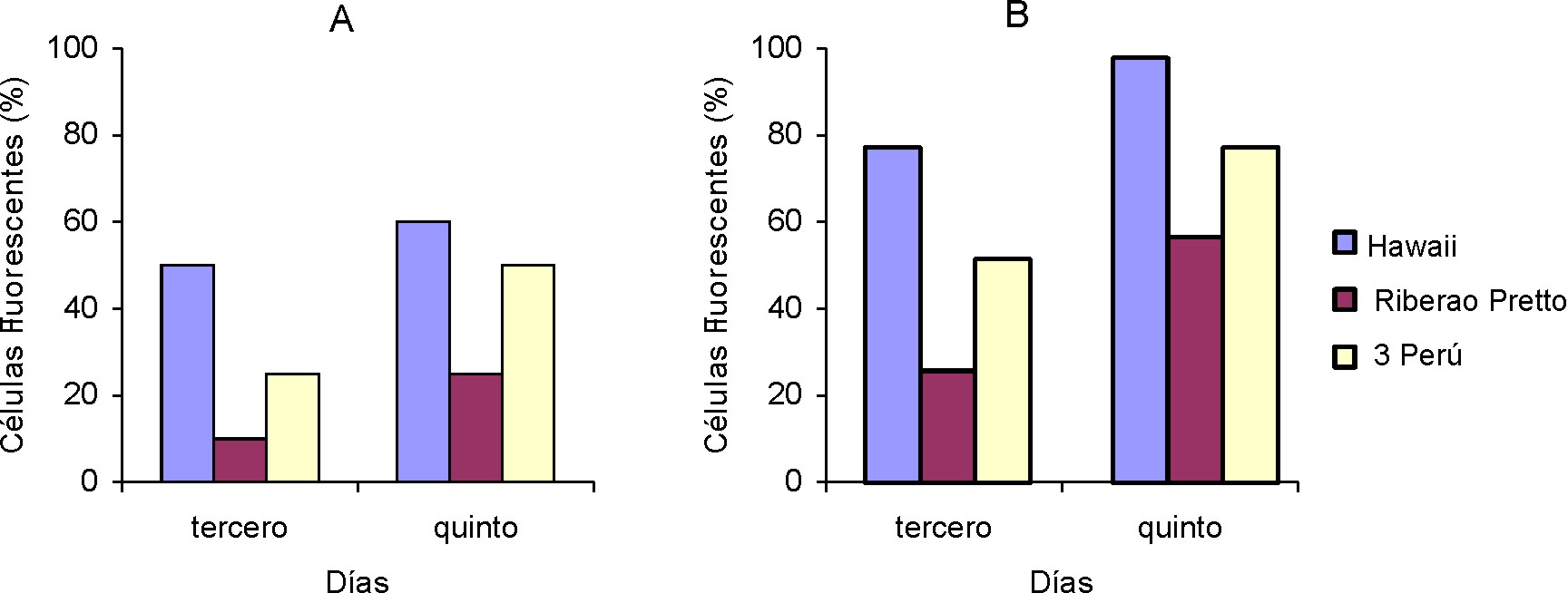
Los porcentajes de células HepG2 infectadas se muestran en la figura 1. El mayor porcentaje de células infectadas en esta línea celular se obtuvo para las m.o.i. más elevadas: 0,01 y 0,04. Los resultados obtenidos con las células Vero se evidencian en la figura 2. El mayor porcentaje de células HepG2 y Vero infectadas para las cepas estudiadas se obtuvo al 5to. día. La cepa Hawaii permitió mejores resultados al ser capaz de infectar más rápido (3 d) un mayor porcentaje de células en cada una de las líneas celulares, que el resto de las cepas empleadas.
Fig. 1. Células HepG2 fluorescentes (%) a los 3 y 5 d posinfección. A: cepas Hawaii y Riberao Pretto (m.o.i. 0,004), 3 Perú (m.o.i. 0,001). B: cepas Hawaii y Riberao Pretto (m.o.i. 0,04), 3 Perú (m.o.i. 0,01).
]]>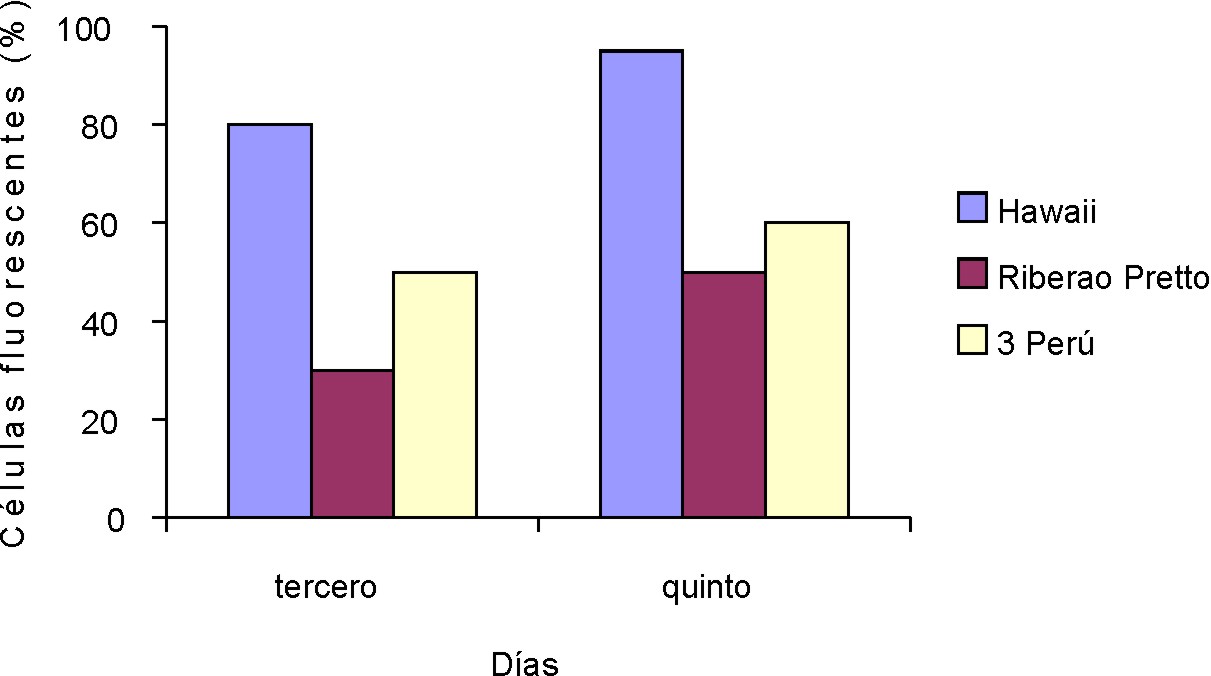
Fig. 2. Células Vero fluorescentes (%) debido a la infección por las cepas Hawaii y Riberao Pretto (m.o.i. 0,004), 3 Perú (m.o.i. 0,001) a los 3 y 5 d posinfección.
Al analizar los sobrenadantes de los cultivos celulares infectados, no se obtuvieron títulos en el sobrenadante de la línea celular HepG2 para las cepas Riberao Pretto y 3 Perú, mientras que en el de las Vero, solo fue posible detectarlos al 5to. día posinfección (Riberao Pretto, 40 uff/mL y 3 Perú 10 uff/mL). Para la cepa Hawaii sí fue posible detectar virus en el sobrenadante de las líneas celulares infectadas para ambos días posinfección, excepto al 3ro. para la m.o.i. 0,004 (tabla). Los títulos virales siempre fueron más altos al 5to. día que al 3ro. para ambas líneas celulares y fueron mucho mejores para la línea celular Vero que para la HepG2, tanto al 3ro. como al 5to. días posinfección. Los mejores títulos en las células HepG2 infectadas con la cepa Hawaii se obtuvieron con la multiplicidad más alta (0,04).
Tabla. Títulos (uff/mL) de la cepa Hawaii en el sobrenadante de células HepG2 y Vero a los 3ro. y 5to. días posinfección
| Días | HepG2 | Vero | ||
| m.o.i. | ]]> Título (uff/mL) | m.o.i. | Título (uff/mL) | |
| 3 | 0,004 | - | 0,04 | 5 x 102 |
| 0,04 | 40 | |||
| ]]> 5 | 0,004 | 10 | 0,04 | 3 x 103 |
| 0,04 | 50 | |||
En este estudio, la susceptibilidad a las 3 cepas de dengue 1, fue mejor para las células Vero que para las HepG2. Al analizar los mismos valores de multiplicidad (0,001 y 0,004) para ambas líneas celulares se detectaron mayores porcentajes de células Vero que HepG2 infectadas, estos porcentajes resultaron similares a los que se obtuvieron con las células HepG2 inoculadas a las multiplicidades más altas (0,01 y 0,04). Estos resultados coinciden con la mayor susceptibilidad de las células Vero comparados con las HepG2 a la cepa Oster de dengue 1.5 Estos resultados son similares a los descritos por Anderson y otros,6 al encontrar esta línea celular más sensible a la infección por dengue 4 y por Diamond y otros,14 quienes observaron una marcada variación en cuanto a la susceptibilidad de diferentes tipos celulares, a la infección por diferentes cepas de dengue 2. En este estudio el grado de infección viral resultó de la interacción entre factores virales y celulares específicos.
Varias explicaciones han sido propuestas para justificar la mayor susceptibilidad de las células Vero. Esto puede deberse a una mejor unión de la proteína E del virus dengue a la superficie celular.6 Marianneau y otros,5 reportaron que aunque aparentemente había una mayor cantidad de sitios de unión en células HepG2 que en Vero, la afinidad de unión de dengue 1 fue mayor para estas últimas; también sus estudios sugieren la presencia de receptores diferentes o presentados en un ambiente diferente en la superficie de ambas líneas celulares. Recién ha sido reportado que el ciclo celular influye en la permisividad de las células HepG2 a la infección por virus dengue 2 y 3 a diferencia de las Vero.15 Este resultado demuestra la influencia de la fisiología de la célula en la permisividad de determinados tipos celulares a la infección viral, evidenciándose una vez más la importancia del factor celular en este proceso.
]]> La unión de un virus a su receptor específico es un factor principal del tropismo celular y un determinante importante en la patogénesis. Recién han sido encontradas proteínas específicas para cada serotipo viral en la superficie de células HepG2, las cuales median la unión a la célula, del serotipo para el cual son específicas, evidenciando que existe un comportamiento serotipo específico que regula la entrada del virus a la célula.16,17Es importante destacar que para ambas líneas celulares los mejores resultados se obtuvieron al 5to. día posinfección, por lo que sería el más recomendado para la obtención de buenos resultados en este tipo de estudios. En los resultados la mejor multiplicidad de infección en el sistema celular HepG2 fue 0,04, esto es consistente con lo reportado por otros autores que en la medida en que aumentaron la m.o.i., aumentaba el porcentaje de células infectadas.5
Se encontraron diferencias en el comportamiento de las 3 cepas empleadas en este estudio. La cepa Hawaii fue capaz de infectar un mayor porcentaje de células HepG2 y fue la única que mostró títulos en el sobrenadante de ambas líneas celulares, exceptuando la m.o.i. más baja (0,004), a los 3 d en HepG2. Con las otras 2 cepas solo se detectó título en el sobrenadante para la línea Vero al 5to. día. Las cepas Hawaii y la Riberao Pretto fueron inoculadas con los mismos valores de m.o.i. obteniéndose con la primera, como ya se mencionó, los mejores resultados. Esto sugiere una más rápida replicación o eficiente maduración y/o liberación de la cepa Hawaii en las líneas celulares estudiadas, especialmente en las Vero. Esta cepa puede ser de gran utilidad en estudios que requieran resultados en corto tiempo empleando bajas multiplicidades de infección. Aunque la cepa Perú fue inoculada con una m.o.i. más baja debido a los bajos títulos del virus de partida, fue la Riberao Pretto la que mostró los porcentajes más bajos de células infectadas, lo cual sugiere el papel del factor viral en la infectividad.
Esta variación entre cepas de un mismo serotipo de virus dengue ha sido encontrada por otros autores. La cantidad de antígeno viral y el número de viriones infecciosos producidos en la línea celular HepG2 mostró diferencias significativas entre cepas de dengue 2.14 Las cepas A15, Jamaica y Nueva Guinea C de dengue 2 difieren en cuanto a su comportamiento biológico.10,18 Estudios moleculares realizados arrojan diferencias genotípicas entre estas cepas.19
Los estudios de caracterización molecular de cepas de dengue de los distintos serotipos han demostrado la correlación entre las diferencias genéticas y las formas clínicas de presentación de esta enfermedad.9 Esta correlación había sido reportada, pero con respecto a la estructura antigénica entre cepas de dengue 2.20 Una correlación entre el patrón de infección in vitro, el genotipo viral y el fenotipo in vivo también ha sido hallada; las células primarias de fibroblastos de dermis humana HFF (human foreskin fibroblasts, siglas en inglés), solo fueron infectadas productivamente por cepas aisladas a partir de pacientes con FHD, pertenecientes al genotipo del sudeste asiático y no por las pertenecientes al genotipo Jamaica, provenientes de casos de FD.14
El conocimiento de la diana celular humana de la infección por dengue y las consecuencias que ocasiona esta infección en los niveles celular y molecular, la identificación de los receptores para el virus y la caracterización de los factores de virulencia de las cepas, están entre las prioridades de investigación por su vital importancia en el establecimiento de una estrategia efectiva contra esta enfermedad. Los resultados obtenidos en este estudio apoyan la importancia del factor viral en la patogénesis de esta enfermedad.
2. Kourí GP, Guzmán MG, Bravo JR, Triana C. Dengue hemorrhagic fever/ dengue shock syndrome: lessons from the cuban epidemic, 1981. Bull WHO 1989; 67:375-80.
4. Guzmán MG, Kourí G. Advances in dengue diagnosis. Clin Diagnostic Lab Immunol 1996;3(6):621-7.
]]> 5. Marianneau P, Megret F, Olivier R, Morens D, Deubel V. Dengue1 virus binding to human hepatoma HepG2 and simian Vero cell surface differs. J.Gen Virol 1996;77:2547-54.6. Anderson R, King AD, Innis BL. Correlation of E protein binding with cel susceptibility to dengue 4 virus infection. J Gen Virol 1992;73:2155-9-
7. Després P, Frenkiel MP, Deubel V. Differences between cell membrane fusion activities of two dengue type 1 isolates reflect modifications of viral structure. Virology 1993;196:209-19.
8. Guirakhoo F, Heinz FX, Mandl CW, Holzman H, Kunz C. Fusion activity of flavivirus: Comparison of mature and immature (prM- containing) tick borne encephalitis virions. J Gen Virol 1991;72:1323-9.
9. Rico Hesse R. Molecular evolution and distribution of dengue viruses type 1 and 2 in nature. Virology 1996;174:479-93.
10. Camacho DE, Guzmán MG, Morier L, Álvarez M, Rodríguez R, Comach G. Estudio de algunas propiedades biológicas de 3 cepas de dengue 2 con diferencias en sus secuencias nucleotídicas. Rev Cubana Med Trop 1999;51(3):177-80.
11. Thant KZ, Morita K, Igarashi A. Sequences of E/NS1 gene junction fomr four dengue 2 viruses of Northeastern Thailand and their evolutionary relationships with other dengue 2 viruses. Microbiol Immunol 1995;39(8):581-90.
12. Leitmeyer KC, Vaughn DW, Watts DM, Salas R, Villalobos I, Ramos C. Dengue virus structural differences that correlate with pathogenesis. J Virol 1999;73(6):4738-47.
13. Igarashi A, Mantani M. Rapid titration of dengue virus type 4 infectivity by counting fluorescent foci. Biken Journal 1974;17:87-93.
]]> 14. Diamond MS, Edgil D, Roberts TG, Lu B, Harris E. Infection of human cells by dengue virus is modulated by different cell types and viral strains. J Virol 2000;74(17):7814-23.15. Phoolcharoen W, Smith DR. Internalization of the dengue virus is cell cycle modulated in HepG2, but not Vero cells. J Med Virol 2004;74(3):434-41.
16. Thepparit Ch, Smith DR. Serotype-specific entry of dengue virus into liver cells:identification of the 37-kilodalton high-affinity laminin receptor as a dengue virus serotype 1 receptor. J Virol 2004;78(22):12647-56.
17. Jindadamronwech S, Smith DR. Virus overlay protein binding assay (VOPBA) reveals serotype specific heterogeneity of dengue virus binding proteins on HepG2 human liver cells. Intervirology.2004;47(6):370-3.
18. Morier L, Camacho DE, Guzmán MG, Álvarez M, Rodríguez R, Comach G. Comportamiento biológico de 3 cepas del virus dengue 2 en 2 líneas celulares de mosquitos. Rev Cubana Med Trop 2000;52(3):215-9.
19. Guzmán MG, Deubel V, Pelegrino JL, Rosario D, Marrero M, Sariol C. Partial nucleotide and aminoacid sequences of the envelope and the envelope/non structural protein-1 gene junction of four dengue-2 virus strains isolated during the 1981 cuban epidemic. Am J Trop Med Hyg 1995;52(3):241-6.
20. Morens DM, Halstead SB. Disease severity- related antigenic differences in dengue 2 strains detected by dengue 4 monoclonal antibodies. J Med Virol 1987; 22:169-74.
Recibido: 15 de febrero de 2004. Aprobado: 15 de marzo de 2005.
Lic. Alicia Aguilar Barroso. Instituto Finlay. Ave. 27 No. 19805, municipio La Lisa, Ciudad de La Habana. Teléf 271 6911. Correo electrónico: aaguilar@finlay.edu.cu