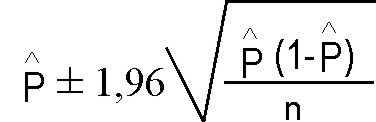
Centro Nacional de Biopreparados
Lic. Anna Tsoraeva1 y Dr. Jorge Luis Muñoz del Campo2
Se evaluó una prueba rápida, en el diagnóstico de Escherichia coli, en diferentes tipos de muestras infecciosas, así como su comparación con los métodos bioquímicos de identificación tradicionales. Se ha reportado que la enzima glutamato descarboxilasa (GAD) es muy específica (97-99 %) para la identificación de Escherichia coli, sin embargo su empleo en la actualidad es muy limitado. Se analizaron 461 muestras clínicas de diferente origen en un hospital pediátrico. En general, con mayor frecuencia Escherichia coli fue aislada en muestras de urocultivo, coprocultivo, vaginales y uretrales. La sensibilidad diagnóstica del método fue de 100 %. Todas las cepas enterotoxigénicas y enterohemorrágicas de Escherichia coli aisladas en muestras de heces fecales también dieron los resultados positivos a la prueba rápida. La especificidad diagnóstica resultó ser de 82,8 %, debido a los resultados falsos positivos proporcionados por 34 cepas de Shigella del grupo D aisladas en coprocultivos. Las ventajas de la aplicación de esta prueba, comparadas con otras pruebas convencionales y comerciales, están dadas por su bajo costo, su rapidez y su alta sensibilidad, especificidad y exactitud diagnósticas, lo que permite ahorro de personal, de materiales y del tiempo empleado en la identificación.
Palabras clave: GAD, prueba rápida, Escherichia coli, identificación.
Escherichia coli es un microorganismo patógeno que se aísla con frecuencia en el diagnóstico clínico a partir de diferentes tipos de muestras infecciosas. Es el patógeno urinario más frecuente y ocupa de 60 a 80 % de todos los aislamientos.1-3 Por otra parte, se conocen al menos 6 categorías enterovirulentas de E. coli causantes de enfermedades gastrointestinales.4
En los últimos años se han desarrollado métodos rápidos, sensibles y específicos para el diagnóstico de este microorganismo, en su mayoría son costosos, es por ello que se hace necesario encontrar nuevas técnicas que además de poseer una alta sensibilidad, especificidad y rapidez, sean lo suficientemente económicas y sencillas para que puedan ser incorporadas al diagnóstico clínico de rutina.
La enzima descarboxilasa de glutamato (GAD), que cataliza la a descarboxilación de ácido glutámico produciendo ácido g-aminobutírico y dióxido de carbono, ha sido reportada anteriormente en Escherichia coli,5,6 presentando rangos de especificidad que varían de 97 a 99 %.7-10
Fiedler y Reiske en 199011 describen un método rápido para la detección de esta enzima. En este método la solución hipertónica de cloruro de sodio y Tritón X se emplean como agentes líticos para la liberación de la enzima, esto posibilita que la reacción ocurra en un período no mayor de 4 h. Aunque las ventajas de empleo de esta prueba han sido reportadas por varios autores, su uso en el diagnóstico de rutina en los laboratorios de microbiología diagnóstica tanto en Cuba como en otros países de América Latina es muy limitado. Un estudio preliminar de aplicación de este método para la identificación de E. coli en muestras de orina en el Hospital Pediátrico Juan Manuel Márquez arrojó resultados muy satisfactorios (97,14 % de sensibilidad y 100 % de especificidad diagnóstica).12
]]> El objetivo de este trabajo consistió en evaluar la prueba rápida en el diagnóstico de E. coli en diferentes tipos de muestras infecciosas, así como, su comparación con los métodos bioquímicos de identificación tradicionales.El trabajo fue realizado en un período desde diciembre de 2002 hasta abril de 2003 en el Hospital Pediátrico Leonor Pérez (Ciudad de La Habana, Boyeros) analizando 163 muestras de orina, 202 muestras de heces fecales, 37 muestras óticas, 44 muestras vaginales y 14 muestras uretrales.
A todos los microorganismos aislados (n = 461) se les aplicó la prueba rápida del GAD y el procedimiento tradicional de identificación por pruebas bioquímicas.13
Las cepas de enterobacterias fueron identificadas empleando las pruebas de fermentación de glucosa, lactosa, dulcitol, sorbitol y sorbosa, producción del gas sulfhídrico, producción del indol, motilidad, utilización del citrato de sodio, descarboxilación de lisina y ornitina, desaminación de fenilalanina, hidrólisis de urea y prueba de oxidasa. Para la identificación de las cepas del género Aeromonas se emplearon las pruebas de oxidasa y catalasa, descarboxilación de lisina y ornitina, hidrólisis de arginina, fermentación de manitol e inositol y prueba de la cuerda.
El reactivo de GAD consistió en 0,1 g del ácido l-glutámico (ICN FLOW, ICN Biochemicals Inc., Ohio), 0,005 g de verde de bromocresol (Merck, Darmstadt), 9 g de Na Cl (Quelab, Canadá), y 0,3 mL de Tritón X-100 (BDH, Inglaterra) por 100 mL de agua destilada (pH 3,4).11 Una vez disueltos todos los componentes, la solución se esterilizó por filtración utilizando una membrana estéril (Sartorius, Alemania) con tamaño de poros de 0,22 µm. El reactivo preparado se almacenó en un frasco ámbar estéril en refrigeración durante un período no mayor de 2 meses.
El procedimiento de la prueba consistió en: adicionar 1 asada del microorganismo aislado a 0,5 mL de la solución salina (0,85 %) estéril, para lograr una suspensión microbiana equivalente al tubo 0,5 de la escala de MacFarland y añadir 0,2 mL del reactivo de GAD estéril, incubar a 35 ± 2 °C durante 4 h, observando los resultados cada 1 h. Respuesta positiva es cualquier cambio del color del tubo de amarillo a verde o azul. Respuesta negativa es color amarillo (sin cambio).
Los estimados de sensibilidad, especificidad y exactitud diagnósticas se calcularon por las ecuaciones siguientes:
P (S) = VP / (VP + FN); P (E) = VN / (VN + FP) y P (Ex) = VP + VN / (VP + VN + FP + FN), donde
VP y VN son los números de verdaderos positivos y negativos y
FP y FN son los números de falsos positivos y negativos.14
En la tabla 1 se presentan los resultados de detección de la presencia de la enzima glutamato descarboxilasa en un total de 461 cepas aisladas, comprendiendo 15 especies pertenecientes a 8 géneros. De las 263 cepas de E. coli ensayadas, todas (100 %) dieron respuestas positivas a la prueba rápida, mientras que 34 (55,74 %) de 61 cepas de Shigella, todas pertenecientes al serogrupo D, también mostraron resultados positivos. En ningún otro microorganismo aislado fue detectada la actividad de esta enzima.
Tabla 1. Resultados de la prueba del GAD para diferentes microorganismos
| Microorganismo (No. de cepas) | No. (%) de cepas positivas |
| Aeromonas sp. (5) | 0 (0) |
| Citrobacter freundii (2) | ]]> 0 (0) |
| ECEHa (29) | 29 (100) |
| ECETb (94) | 94 (100) |
| Enterobacter aerogenes (18) | 0 (0) |
| Enterobacter cloacae (12) | 0 (0) |
| Escherichia coli (140) | ]]> 140 (100) |
| Klebsiella pneumoniae (6) | 0 (0) |
| Proteus mirabilis (50) | 0 (0) |
| Proteus morganii (6) | 0 (0) |
| Proteus rettgeri (12) | 0 (0) |
| Proteus vulgaris (19) | ]]> 0 (0) |
| Salmonella grupo B (2) | 0 (0) |
| Salmonella grupo D (11) | 0 (0) |
| Shigella grupo B (26) | 0 (0) |
| Shigella grupo C1 (1) | 0 (0) |
| Shigella grupo D (34) | ]]> 34 (100) |
a ECEH: Escherichia coli enterohemorrágica, b ECET: Escherichia coli enterotoxigénica
La sensibilidad diagnóstica para la identificación rápida de E. coli fue de 100 % (tabla 2) para todos los tipos de muestras analizados. Aunque la especificidad diagnóstica resultó ser menor que 90 % debido a la interferencia de cepas de Shigella en análisis de coprocultivos, la exactitud diagnóstica del método fue suficientemente alta (92,62 ± 2,97 %).
Tabla 2. Comparación de la cantidad de las respuestas positivas a la prueba del GAD con la cantidad de las cepas confirmadas como E. coli
| Tipo de muestra | No. de reacciones positivas a GAD | No. (%) de cultivos confirmados como E. coli | Parámetros diagnósticosa | ||
| S, % | ]]> Eb, % | Exb, % | |||
| Urocultivo | 93 | 93 | 100 | 100 | 100 |
| Coprocultivo | 157 | ]]> 123 | 100 | 56,96 ± 7,74 | 83,17 ± 5,8 |
| Exudado ótico | 5 | 5 | 100 | 100 | 100 |
| ]]> Exudado vaginal | 30 | 30 | 100 | 100 | 100 |
| Exudado uretral | 12 | 12 | 100 | ]]> 100 | 100 |
| Total | 297 | 263 | 100 | 82,82 ± 4,29 | 92,62 ± 2,97 |
a S: sensibilidad diagnóstica, E: especificidad diagnóstica, Ex: exactitud diagnóstica, b resultados están presentados como el intervalo de 95 % de confianza del valor estimado
En general, con mayor frecuencia E. coli fue aislada en muestras de urocultivo, coprocultivo, vaginales y uretrales (figs. 1 - 5).
]]>
Fig. 1. Distribución de cepas aisladas en muestras de orina.
ECEH: Escherichia coli enterohemorrágica, ECET: Escherichia coli enterotoxigénica
Fig. 2. Distribución de cepas aisladas en muestras de heces fecales.
Fig. 3. Distribución de cepas aisladas en muestras óticas.
Fig. 4. Distribución de cepas aisladas en muestras vaginales.
]]> Fig. 5. Distribución de cepas aisladas en muestras uretrales.Los resultados obtenidos concuerdan con los datos reportados por Rice9 y McDaniels11 en que entre las bacterias gramnegativas Shigella es el único otro género que ha producido reacciones GAD-positivas en alrededor de 61 % de casos.
Todas las cepas enterotoxigénicas (94) y enterohemorrágicas (29) de E. coli aisladas en muestras de coprocultivo también fueron GAD-positivas, esto confirma los resultados obtenidos por Grant y otros,6 que demostraron en un estudio realizado con 173 cepas patógenas de esta especie, incluidas diferentes categorías enterovirulentas, que una alta proporción (100 %) de estas cepas presentan la actividad de la enzima glutamato descarboxilasa. Por otra parte, McDaniels11 también reporta una sensibilidad de 96,87 % para la prueba fenotípica del GAD en una evaluación con 64 cepas de E. coli: enteropatogénicas, entrotoxigénicas y enterohemorragicas, entre ellas.
Teniendo en cuenta la elevada frecuencia de aislamiento de E. coli en muestras de orina, exudados uretrales y vaginales, se recomienda la aplicación de la prueba rápida de GAD para la identificación de este microorganismo, teniendo en cuenta los altos valores de la exactitud diagnóstica obtenidos en este procedimiento. En el caso del análisis de coprocultivos es recomendable tener en cuenta las características culturales de las colonias aisladas en los medios de cultivo de aislamiento primario, porque las colonias de Shigella tienen coloración distinta de la de E. coli en el agar de MacConkey y en el agar SS pero similar a la de las cepas de E. coli enterohemorrágica en el agar de MacConkey con sorbitol.
Otro importante beneficio de la prueba es el considerable ahorro de tiempo y reactivos, debido a que mientras el procedimiento de identificación tradicional necesita de al menos 72 h para el diagnóstico, las respuestas positivas de la reacción de GAD fueron obtenidas en menos de 2 h de incubación, y dentro de ellos 95 % en menos de 1 h.
Por último, la factibilidad económica de la prueba permite su aplicación en cualquier laboratorio de microbiología por muy sencillo que sea.
En resumen, las ventajas de la aplicación de esta prueba, comparadas con otras pruebas convencionales y comerciales, están dadas por su bajo costo, factibilidad de realizar en el laboratorio para la identificación de E. coli, su rapidez y su alta sensibilidad, especificidad y exactitud diagnósticas.
A rapid test was evaluated in the diagnosis of Escherichia coli in different types of infectious samples, and a comparison with the biomedical methods of traditional identification was made. It has been reported that glutamate decarboxylase (GAD) is very specific (97-99 %) for the identification of Escherichia coli; however, its use is very limited nowadays. 461 clinical samples of different origin were analyzed in a childrens hospital. In general, Escherichia coli, was more frequently isolated from urine, fecal, vaginal and urethral specimens. The diagnostic sensitivity of the method was 100 %. All the enterotoxigenic and enterohemorrhagical strains of Escherichia coli isolated from feces samples were also positive to the rapid test. The diagnostic specificity was 82.8 %, due to the false positive results yielded by 34 strains of Shigella of the group D isolated from feces. The advantages of the application of this test compared with other conventional and commercial tests are its low cost, its celerity and its high diagnostic sensitivity, specificity and accuracy, which allow to save personnel, materials and the time used in the identification.
Key words: GAD, rapid test, Escherichia coli, identification.
2. Naylor GR. A 16-month analysis of urinary tract infections in Children. J Med Microbiol 1984;17:31-6.
3. Alos JI, Chacón J. Bacteriología de las infecciones urinarias extrahospitalarias. Med Clin 1988;90:395-8.
4. Grant MA, Weagant SD, Feng P. Glutamate decarboxylase genes as a prescreening marker for detection of pathogenic Escherichia coli groups. Appl Environ Microbiol 2001;67:3110-4.
5. Wauters G, Cornelius G. Methode simple pour la recherche de la decarboxylation de lacide glutamique chez les bacterias a gram negatif. Ann Microbiol 1974;125:183-92.
6. Freier PA, Graves MH, Kocka FE. A rapid glutamic decarboxylase test for identification of bacteria. Ann Clin Lab Sci 1976;6:537-9.
7. Rice EW, Johnson CH, Dunnigan ME, Reasoner DJ. Rapid Glutamate Decarboxylase Assay for Detection of Escherichia coli. Appl Environ Microbiol 1993;59:4347-9.
8. Rice EW, Johnson CH, Reasoner DJ. Detection of Escherichia coli O157:H7 in water from coliform enrichment cultures. Lett Appl Microbiol 1996;23:179-82.
9. McDaniels AE, Rice EW, Reyes AL, Johnson CH, Haugland RA, Stelma GN. Confirmational identification of Escherichia coli, a comparison of genotypic and phenotypic assays for glutamate decarboxylase and beta-D-glucuronidase. Appl Environ Microbiol 1996;62: 3350-4.
10. Schubert R, Esanu JG, Schafer V. The glutamic acid decarboxylase disc test: an approach to a faster and more simple detection of E. coli. Zentralbl Bacteriol Hyg 1988;B 187:107-11.
11. Fiedler J, Reiske J. Glutaminesaueredecarboxylase-Schnelltest zur Identifikation von Escherichia coli. Z Gesamtee Hyg Grenzgeb 1990;36:620-2.
12. Tsoraeva A., Quesada Muñiz VJ, Duran Vila A., Hernández Robledo E., García Suárez V. Identifizierung von Escherichia coli. LVT Lebensmittel Industrie 2003;9/10:46-7.
13. Farmer JJ. New groups of Enterobacteriaceae. J Clin Microbiol1985;21:46-76.
14. Havelaar AH, Heisterkamp SH, Hoekstra JA, Mooijman KA. Performance characteristics of methods for the bacteriological examination of water. Wat Sci Tech 1993;27: 3.
15. Ilstrup DM. Statistical Methods in Microbiology. Clin Microbiol Rev 1990;V 3,N 3: 219-26.
Recibido: 5 de marzo de 2005. Aprobado: 10 de septiembre de 2005.
Lic. Anna Tsoraeva. Centro Nacional de Biopreparados, Apartado 6048. Habana 6. Cuba. Fax 338439. Correo electrónico: atsoraeva@biocen
1 Máster en Microbiología General. Investigadora Auxiliar. Centro Nacional de Biopreparados (BIOCEN). ]]> 2 Especialista de I Grado en Microbiología. Hospital Pediátrico Leonor Pérez. Ciudad de La Habana.