
Detección del volumen del líquido Cefalorraquídeo a través de imágenes de Resonancia Magnética
Cerebrospinal fluid volume detection through Magnetic Resonance Imaging
Enrique González Martín1*,Marcelino Rodríguez Cancio2, Laura Pérez Triana1, Elvis González Cabrera4
1Universidad Central de Las Villas. Martí #12 e/ Luaces y Calixto García, San Juan de Los Yeras, Ranchuelo, Villa Clara. {egmartin, ltriana}@uclv.cu
2Vanderbilt University, Inria. Francia ]]>
*Autor para la correspondencia: egmartin@uclv.cu
RESUMEN
Para los anestesistas se hace necesario calcular la cantidad de anestesia espinal a utilizar en cada paciente, debido al riesgo que corren estos, si se le aplica la dosis equivocada. Esta dosis depende en gran medida del volumen de líquido cefalorraquídeo que posea el paciente, sin embargo, no existe un equipo capaz de calcular este volumen. En este artículo se presenta un algoritmo de segmentación heurístico para la detección y posterior segmentación del líquido cefalorraquídeo. El algoritmo fue diseñado a partir del conocimiento de expertos en el campo de la medicina del hospital Arnaldo Milián Castro de Santa Clara, Villa Clara, e utiliza imágenes de resonancia magnética. También se realiza una comparación entre los valores de volúmenes alcanzado por el algoritmo y los calculados por técnicos especializados en este campo, tal y como se realiza hoy en día.
Palabras clave: líquido cefalorraquídeo, imágenes de resonancia magnética, registro de imágenes, componente conexa
ABSTRACT
In this work we introduce a heuristic segmentation algorithm for the detection and subsequent segmentation of the volume of cerebrospinal fluid (CSF) that allows from MRI to calculate the CSF due to the importance of this represents to calculate the amount of anesthesia to be used in patients. The algorithm was designed from medical knowledge from Arnaldo Milián Castro hospital from Santa Clara, Villa Clara. Also is made a comparison between the algorithm volume values and the volume gathered from technician (this is the way to get the volume today).
]]> Key words: Cerebrospinal Fluid (CSF), Magnetic Resonance Imaging, Image Registration, region-growing.
INTRODUCCIÓN
Estudios recientes aseveran que la cantidad de anestesia a utilizar depende de muchos factores, entre los que destacan(Marsch and Staender, 1999, Higuchi et al., 2005) la potencia relativa del anestésico local a emplear, el número de nodos o raíces nerviosas espinales a bloquear y la concentración mínima efectiva del anestesio local (CMEA).
En este artículo se abordará la forma de determinar la concentración mínima del anestésico local, el cual depende directamente del volumen del líquido cefalorraquídeo (LCR). Este volumen se puede determinar de una forma relativamente precisa a través de imágenes de resonancia magnética (MRI) utilizando técnicas de procesamiento de imágenes como el registro de imágenes y “región growing”.
El LCR recubre la medula espinal y el cerebro; es un ultrafiltrado de plasma, incoloro, contiene glucosa, electrolitos, aminoácidos y otras pequeñas moléculas encontradas en el plasma, tiene muy pocas proteínas y pocas células. El LCR protege el sistema nervioso central de daños por colisión con la estructura ósea circundante(McPherson and Pincus, 2011, Kee, 2004) .
Se hace necesario conocer el volumen del LCR antes de suministrar anestesia local a un paciente debido a que la concentración mínima efectiva del anestésico local depende del volumen de LCR donde será depositado el mismo; si se aplica una misma dosis, en igualdad de volumen y concentración de anestésico local, a dos pacientes con distintos volúmenes de LCR, en aquel que el volumen resulta menor, la concentración del anestésico local será superior y por lo tanto la difusión rostral del fármaco será mayor, alcanzando un nivel de bloqueo más alto en relación al que tiene un volumen superior de LCR (Longnecker et al., 2008, Ronald D. Miller, 2005) .
La resonancia magnética es una técnica en la que se coloca al paciente en un campo magnético muy fuerte y se pasa ondas de radiofrecuencia a través del cuerpo del paciente en cortos pulsos. Cada pulso causa un pulso de respuesta de ondas de radiofrecuencia que son emitidos por los tejidos del paciente. El lugar del cual se originan esas señales y su fuerza es determinado por una computadora, la cual produce una imagen bidimensional de una sección del paciente. Las MRI se pueden producir en cualquier plano y se producen en forma de corte, que no es más que una porción de la zona de la cual se está tomando la imagen. (González and Woods, 2001, Pratt, 2001) Figura 1
]]> Aplicando diferentes gradientes en la altura, ancho o profundidad en diferentes momentos se puede determinar un mapa tridimensional completo de la región de interés, además, estas imágenes brindan la posibilidad de obtener información de intensidad, forma e incluso volumen de una región determinada, lo que las hacen una buena opción para realizar el cálculo del volumen del LCR.(Allison, 2006)Para poder calcular el volumen del LCR es necesario obtener de la mejor forma posible, la porción de la imagen con que se desea trabajar, en este caso la región del LCR, este proceso se denomina segmentación, que no es más que el proceso de dividir una imagen digital en múltiples segmentos (conjuntos de píxeles, también conocidos como súper píxeles). El objetivo de la segmentación es simplificar y/o cambiar una representación de una imagen en algo que tiene mejor significado y es más fácil de analizar. La segmentación de imágenes es usada típicamente para localizar objetos y vecindades (líneas, curvas, etc.) en imágenes.
Es el proceso de asignar una etiqueta a cada píxel en una imagen tal que los pixeles con la misma etiqueta compartan ciertas características visuales.
Tipos de imágenes MRI usadas
Los tipos de imágenes MRI usadas son de pesado T1 (T1-weighted MRI) y de pesado T2 (T2-weighted MRI)
Las imágenes de pesado T1 se refieren a un conjunto de estándares de escaneo que bosquejan diferencias entre varios tejidos dentro del cuerpo. En el cuerpo los escáneres con pesado T1 trabajan bien para diferenciar la grasa del agua, la grasa apareciendo más clara y el agua más oscura. (Belkic, 2004) Figura 2
En las imágenes de pesado T2 como en los escáneres de pesado T1, la grasa es diferenciada del agua, pero en este caso la grasa aparece más oscura y el agua más clara. En el caso del estudio del LCR, será más claro en las imágenes de pesado T2. Estos escáneres son particularmente buenos para mostrar edemas.(Belkic, 2004)
Registro de imágenes
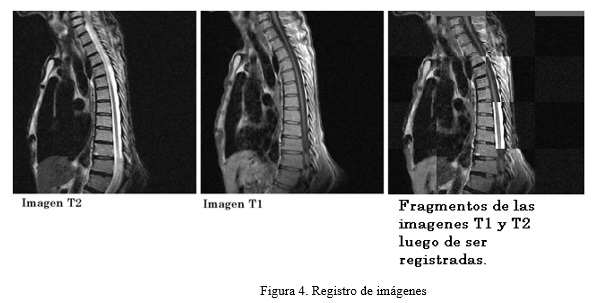
En muchas aplicaciones de procesamiento de imágenes es necesario formar una comparación píxel a píxel de dos imágenes del mismo campo obtenidas por sensores diferentes, o de dos imágenes del mismo campo obtenidas por el mismo sensor en diferentes momentos. Para esto es necesario registrar espacialmente las imágenes y corregir los cambios de traslación, las diferencias de rotación, diferencias de escala e incluso las diferencias de perspectiva de las imágenes.(Pratt, 2001) “El registro de imágenes es el proceso de alinear o desarrollar correspondencia entre la información de varias imágenes.”(Ibáñez et al., 2005) Figura 4
]]>
Componente conexa
Es un espacio que no puede ser dividido en dos conjuntos, porque cada elemento de dicho espacio presenta algún tipo de conexión con sus vecinos; también se puede decir que es un conjunto maximal de nodos tal que existe al menos un camino que conecta ambos nodos. En el caso de las imágenes, una componente conexa se puede considerar como un conjunto maximal de pixeles con características similares (en este caso de intensidad) tal que existe al menos un camino que conecta a ambos pixeles.
MATERIALES Y MÉTODOS
Con el objetivo de segmentar el LCR, la técnica presentada en este artículo toma como entrada dos series de imágenes MRI, las imágenes de tipo T1 y T2, para producir una imagen 3D con valores escalares asignados a los píxeles que permiten crear una máscara usando técnicas conocidas de procesamiento de imágenes.
Dicho algoritmo utiliza una heurística de reconocimiento de patrones (Pearl, 1983, Gigerenzer et al., 1999) . Se obtuvo gracias al resultado de investigaciones e intercambios con expertos en medicina (Martín, 2012) ,tanto anestesiólogos como radiólogos. EL LCR es un líquido de densidad uniforme que cubre la médula espinal completamente. Esta información reviste gran importancia, ya que de la misma se pueden extraer varias observaciones que se tienen en cuenta durante el desarrollo del algoritmo:
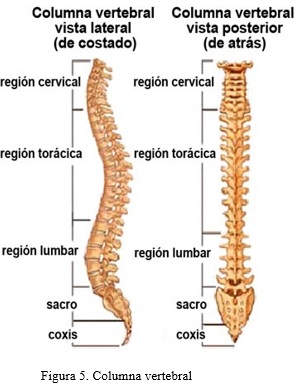
Cubre la médula espinal completa, por lo que en el plano sagital se verá como dos capas finas de una misma intensidad cubriendo una capa de intensidad diferente (Figura 3 ).
Al observarse una imagen MRI desde el plano Transversal, la médula se ve como una zona circular cubierta completamente por una misma capa fina de otra intensidad, esta capa que recubre la médula es el LCR. Por ejemplo, en T1 se debe ver como un punto de claro cubierto por una capa oscura (Figura 6 ), sin embargo en T2 se ve como un punto oscuro cubierto por una capa clara (Figura 7 ).
]]> 4 - En las imágenes donde se muestra la columna, se hace énfasis en la médula, por lo que es de esperar que el LCR sea una componente conexa de longitud considerable.5 - En el pesado T1, los píxeles de LCR son de baja intensidad y la grasa de alta intensidad, mientras que en T2 la grasa y el agua tienen alta intensidad.
Las observaciones realizadas han servido de guía para el algoritmo propuesto, pues la heurística propuesta se basa en estas para determinar la región del LCR.
Algoritmo Heurístico
Para obtener semillas (puntos donde comenzar a buscar), el algoritmo hace un rastreo de línea (“scanline”), ejecutando durante dicho rastreo el autómata de estados finitos A(Xijk). En la Figura 8 sólo se muestran las entradas que hacen cambiar de estado al autómata, el resto se omiten por claridad.
Durante el “scanline” se va alimentando al autómata con una entrada “C” cada vez que se encuentra un píxel considerado “claro” (por encima de cierto umbral, i.e. más del 50% de la intensidad máxima de la imagen) y con entrada “O” si dicho pixel es considerado “oscuro” (lo contrario):
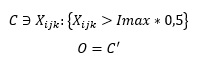
Siendo Xijk es el píxel de posición i, j, k.
Entonces, si se encuentra un segmento de “scanline” y un valor entero n dado, tal que:
]]>O sea, un segmento que cumpla con la Observación 1: un grupo continuo de píxeles oscuros rodeado por dos segmentos continuos de píxeles claros, por tanto se toma como semilla el píxel central del segmento, formalmente:![]()
Este autómata genera múltiples semillas falsas que son descartadas teniendo en cuenta la Observación 3. Para esto se analizan cada uno de los K cortes transversales, generándose dos regiones R1k y R2k con “region-growing”:
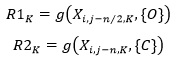
De lo anterior se puede inferir que R1k es la posible región de la médula y R2k la posible zona del LCR en el corte K. Desafortunadamente, este procedimiento aún genera falsos positivos y se deben descartar las regiones R1k que no están completamente contenidas en su correspondiente R2k . En la práctica esto se hace para cada corte K, verificando que las dimensiones mínimas de R1k sean mayores que las R2k y sus dimensiones máximas menores:
![]()
Se define R3 como una región que contiene el LCR en todo el volumen de la imagen. Se puede tomar como semilla para un “region-growing” de R3 cualquier píxel en el conjunto de las R2k . Si R3 contiene más de una componente conexa, se selecciona la de mayor longitud R3'.
Como se dijo anteriormente, todo el proceso se hace en T2 por tanto la grasa y el LCR estarán ligados. Para separarlos, se registra la imagen T1 con T2 y se obtiene el LCR como los píxeles la intersección entre R3' y el conjunto de los píxeles oscuros de la imagen T1 (OT1):
![]()
Complejidad computacional del Algoritmo propuesto
]]> La búsqueda y corrección de la región del LCR tiene un tiempo computacional igual a las dimensiones de la imagen, es decir, si la imagen contiene 512x512x14 pixeles entonces:Sean N, M, O cantidad de pixeles en cada una de las 3 dimensiones X, Y y Z respectivamente, el tiempo computacional de la búsqueda y corrección de la región del LCR será O(N*M*O).
La complejidad del registro de imágenes depende en gran medida de la biblioteca utilizada para realizar este complejo paso.
Pseudocódigo:
Leer Imágenes T1 y T2
Ajustar intensidades
Registrar imagen T1 con T2
Para cada corte sagital en T2 hacer:
Mientras no se alcance el final del corte hacer:
Buscar la posible zona del LCR en el plano sagital (Observación 1) ]]>
Si la zona encontrada está totalmente rodeada (Observación 3)
Hallar Componente conexa
Rectificar la zona del LCR de la imagen T1 con T2
Devolver la mayor componente conexa
Calcular el volumen de la componente.
EVALUCIÓN DE RESULTADOS
Para evaluar el algoritmo de segmentación de la médula se intenta confirmar que el algoritmo se comporta como un operador humano. A continuación, se muestran en la Tabla 1 los valores de similitud de Dice obtenidos para los casos evaluados.
Se evalúan las similitudes usando la prueba de Friedman. Los resultados de esta prueba se muestran en la Figura 9.
]]>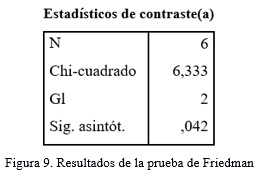
Con una significación asintótica entre 0,05 y menor que 0,1 la prueba arroja que no hay diferencias significativas.
Finalmente, se comparan los volúmenes de LCR obtenidos mediante la segmentación, como se muestra en la Tabla 2 .
En este acápite solo se reportan los resultados, ya que no fue posible hallar otro algoritmo de segmentación del LCR con el cual comparar la eficiencia del mismo.
CONCLUSIONES
Se implementó un algoritmo que permite calcular el volumen de líquido cefalorraquídeo a partir de imágenes de resonancia magnética aplicando técnicas heurísticas. Pese a no encontrarse múltiples casos de prueba, ni otro algoritmo similar con el cual comparar el algoritmo implementado, ha sido posible realizar una comparación entre los resultados del algoritmo y las respuestas de un ser humano especializado en el tema, utilizando los pocos casos de prueba encontrados. La comparación demostró que no existen diferencias significativas entre el algoritmo y un ser humano. Se puede considerar el algoritmo como un primer paso para poder determinar el volumen de líquido cefalorraquídeo de forma eficiente y semiautomática e incluso automática.
REFERENCIAS BIBLIOGRÁFICAS ]]>
ALLISON, W. 2006. Fundamental Physics for Probing and Imaging. Oxford University Press.
BELKIC, K. 2004. Molecular Imaging through Magnetic Resonance for Clinical Oncology. In: PUBLISHING, C. I. S., 6AZ, C. C. & BRITAIN, G. (eds. ).
GONZÁLEZ, R. C. & WOODS, R. E. 2001. Digital Image Processing. In: HALL, P. (ed. ).
HIGUCHI, H., ADACHI, Y. & KAZAMA, T. 2005. The influence of lumbosacral cerebrospinal fluid volume on extent and duration of hyperbaric bupivacaine spinal anesthesia: a comparison between seated and lateral decubitus injection positions. Anesth Analg, 101, 555-60, table of contents.
IBÁÑEZ, L., SCHROEDER, W., NG, L., CATES, J. & CONSORTIUM, I. S. 2005. The ITK Software Guide - Second Edition - Updated for ITK version 2.4.
]]>KEE, J. L. 2004. Handbook of Laboratory and Diagnostic Tests with Nursing Implications.
LONGNECKER, D. E., BROWN, D. L., NEWMAN, M. F. & ZAPOL, W. M. 2008. Anestesiology. In: COMPANIES, N. Y. M. G. H. (ed. ).
MCPHERSON, R. A. & PINCUS, M. R. 2011. Clinical Diagnosis and Management By Laboratory Methods.
PRATT, W. K. 2001. Digital Image Processing Third Edition. In: JHON WILEY AND SONS, I. (ed. ).
]]>RONALD D. MILLER, M. D. 2005. Miller's Anesthesia. Sexta Edición. In: RONALD D. MILLER, M. D. (ed. ).
Recibido: 15/07/2016
Aceptado: 23/09/2016