My SciELO
Services on Demand
Article
Indicators
-
 Cited by SciELO
Cited by SciELO
Related links
-
 Similars in
SciELO
Similars in
SciELO
Share
Vaccimonitor
On-line version ISSN 1025-0298
Vaccimonitor vol.16 no.2 Ciudad de la Habana May-Aug. 2007
de M. tuberculosis en Saccharomyces cerevisiae
María de los Angeles García1, María Elena Sarmiento1, Roberto Coria2, Laura Kawasaky2, Laura Ongay2,
Juan Francisco de la Rosa3, Armando Acosta1.
1. Instituto Finlay. Centro de Investigación-Producción de Vacunas. Ave. 27 No. 19805 e/ 198 y 202.
La Lisa, Ciudad de La Habana. Cuba.
Correo electrónico: mangeles@finlay.edu.cu
2.Instituto de Fisiología Celular, UNAM, D.F. México.
3.Grupo Empresarial LABIOFAM. Ave. Independencia Km 16½. Boyeros. Ciudad de La Habana. Cuba.
Saccharomyces cerevisiae ha sido ampliamente utilizada como sistema de expresión de proteínas heterólogas. El presente trabajo se encaminó hacia la expresión en Saccharomyces cerevisiae de un péptido de epitopes múltiples de M. tuberculosis. Con dicho propósito el péptido quimérico denominado B2 fue clonado en dos vectores de expresión de esta levadura con promotores regulables por galactosa y sulfato cúprico, respectivamente. Luego de los experimentos de inducción, la expresión del péptido B2 fue analizada mediante SDS/PAGE y Western blot. El análisis por Western blot confirmó la expresión del péptido B2, al hacerse la inducción con 100 mM de CuSO4 durante toda la noche. No ocurrió así en los experimentos donde se utilizó la galactosa como inductor con todas las condiciones ensayadas. Estos resultados muestran que la levadura Saccharomyces cerevisiae pudiera ser un buen hospedero alternativo para la expresión de péptidos multiepitópicos de M. tuberculosis.
Palabras clave: Saccharomyces cerevisiae, tuberculosis, vacuna, expresión, antígeno.
Introducción
La tuberculosis continúa siendo una de las enfermedades infecto-contagiosas que mayor número de muertes causa en el mundo. Según la Organización Mundial de la Salud, en el año 2005 se estimó una incidencia global de más de 8,8 millones de nuevos casos con tuberculosis (1), se calcula que la infección por M. tuberculosis origina alrededor de 2 millones de muertes por año, por lo que es considerada la primera causa de mortalidad provocada por un agente infeccioso (2).
Varios factores agravan esta situación, entre las cuales podemos citar: la aparición de cepas multidrogas resistentes, la infección concomitante de M. tuberculosis con HIV, así como el deterioro de las condiciones socioeconómicas en muchas regiones del mundo.
Hasta la actualidad, la única vacuna disponible contra la tuberculosis y aprobada para uso en humanos, es la ya conocida BCG, una cepa atenuada de M. bovis, desarrollada entre los años 1905-1921 por Calmette y Guerin (3). Esta vacuna ha sido efectiva en prevenir la tuberculosis diseminada en niños, sin embargo en muchos países ha fallado en la población adulta, sobre todo contra la tuberculosis pulmonar. Estudios epidemiológicos de programas de vacunación con BCG han revelado una inconsistencia en sus efectos, con unos rangos de eficacia que van desde el 0% al 80% (4). Por todo esto se hace imperativa la necesidad de obtener una vacuna mejorada o superior. Para ello se han abordado diversas estrategias, entre las que se encuentran el uso de cepas inactivadas, cepas vivas atenuadas genéticamente, vectores vivos que expresan antígenos de M. tuberculosis, vacunas recombinantes de subunidades, vacunas conjugadas y vacunas de ADN, entre otras (5).
La obtención por la vía recombinante de antígenos heterólogos continúa siendo un área de creciente interés en el campo de la vacunología. La levadura Saccharomyces cerevisiae es uno de los hospederos que más ampliamente se ha utilizado con estos fines. Este sistema es utilizado no sólo en la obtención de productos para la industria sino también en la obtención de moléculas de importancia biomédica. De hecho fue a partir de este hospedero que se obtuvo la primera vacuna de subunidades por vía recombinante, que es la vacuna contra la hepatitis B (6); también han sido expresados en este sistema otros antígenos de importancia vacunal (7).
Varios aspectos condujeron a la selección de este hospedero como sistema de expresión de antígenos vacunales. Primeramente, se han señalado las propiedades adyuvantes que tienen muchos componentes de la pared celular de esta levadura, lo que pudiera repercutir en la respuesta inmune generada contra el antígeno obtenido a partir de este microorganismo, el cual es muy utilizado en la industria alimenticia y que consumimos normalmente; los índices de endotoxinas que produce son prácticamente indetectables, tiene un alto perfil de inocuidad, por lo que es clasificado como microorganismo GRAS (Generally Regarded as Safe) (8). Todo esto justifica el uso potencial de esta levadura para la obtención de productos destinados a ser administrados por la vía oral, así como también como vector vivo no-patogénico.
En esta primera fase de nuestro estudio, se realizó el clonaje y expresión de un péptido multiepitópico sintético de células B de M. tuberculosis en Saccharomyces cerevisiae. Con la expresión de péptidos con epitopes inductores de células de clase B pretendemos estimular la respuesta inmune humoral e inducir una respuesta inmune protectogénica contra M. tuberculosis. Esto constituiría un reto, pues el pensamiento tradicional es que sólo la inmunidad mediada por células ofrece protección contra la tuberculosis. Sin embargo varios trabajos actuales defienden la hipótesis del papel de los anticuerpos para prevenir o modificar el curso de la infección por M. tuberculosis (9, 10).
Materiales y Métodos
Cepas, plásmidos y medios de cultivo: La cepa de E. coli utilizada fue DH5a (Stratagene) y la cepa de Saccharomyces cerevisiae fue W303-1A (MAT a, ade2-1 trp1-1 ura3-1 leu2-3, 112 his3-11, 15 can1-1000). E. coli creció en medio LB suplementado con ampicillina (100 µg/mL) a 37 oC y agitación vigorosa a 250 rpm. La cepa de Saccharomyce cerevisiae sin transformar se cultivó en medio YPD líquido (1% de extracto de levadura, 1% Bacto-Peptona, 3% de glucosa) e incubadas en incubadora rotatoria a 200 rpm y 30 oC. Las cepas de Saccharomyces cerevisiae transformadas con los respectivos plásmidos recombinantes crecieron en SD-Leu y SD-Ura (medios mínimos sintéticos deficientes respectivamente de leucina y uracilo, suplementado con 2% de glucosa y 2% de agar), las cuales fueron incubadas durante 2 a 3 días en incubadora a una temperatura de 30 oC. Los vectores de expresión en levadura utilizados fueron los plásmidos pYES2 (inducible por galactosa) y pSAL2 (inducible por sulfato cúprico).
Los productos de las reacciones de ligazón con o sin inserto fueron primeramente introducidos en E. coli por transformación mediante la técnica de shock térmico (11) y luego las construcciones recombinantes fueron transferidas a Saccharomyces cerevisiae, utilizando la técnica de transformación por acetato de litio (12).
En el diseño del péptido B2 se emplearon técnicas computacionales de predicción de epitopes de células B. Para ello se partió de antígenos inmunodominantes de M. tuberculosis como: mce1, L7/L12, 85B, HBBA y 16 kDa. Finalmente en el diseño del péptido se incorporó una cola de ocho residuos de histidina en su extremo carboxilo terminal para facilitar su posterior purificación y caracterización.
Amplificación del péptido B2 mediante la reacción en cadena de la polimerasa (PCR): El fragmento de ADN del péptido B2 fue amplificado por PCR a partir del plásmido pNMNO12 4.2. Con este objetivo se diseñaron dos oligonucleótidos (5´a 3´) a los cuales se les añadió los sitios de reconocimiento para las enzimas XhoI y SphI, respectivamente:
B2/XhoI:
TACCCGATCACCTCGAGCATGACCACGCC
B2/SphI:
TCACCTGGATGGCATGCATATGTTAGTGGT
El programa del termociclador (oC/min) fue: un ciclo a 94/5, 30 ciclos de 94/1, 55/1, 72/1 y un ciclo final de 72/10. Para la optimización de las reacciones de PCR fueron utilizadas diferentes concentraciones de MgCl2 (0,5 mM-2,5 mM).
El producto de esta reacción se sometió a electroforesis en gel de agarosa a bajo punto de fusión Sea Plaque (0,8%), luego se realizó la extracción y purificación con el estuche Gene Clean II (Promega) y se ligó en el vector comercial pGEM-T Easy (Promega). Los productos de dicha ligazón fueron introducidos por transformación en una cepa de E. coli (DH5a), químicamente competente. Posteriormente, mediante el método de selección de colonias blancas/azules se escogieron los clones recombinantes y el plásmido resultante que contenía el inserto fue nombrado pGEMTEasy-B2. La presencia de la banda B2 y la fidelidad de su amplificación por PCR fueron comprobadas mediante secuenciación automática a partir del plásmido pGEMTEasy-B2.
Construcción de los plásmidos recombinantes para la expresión del péptido B2 en Saccharomyces cerevisiae: El segmento que codifica para el péptido B2 se liberó del plásmido pGEMTEasy-B2 mediante las enzimas de restricción XhoI y SphI, se purificó con el sistema Gene Clean II, siguiendo las instrucciones del productor y se ligó con los vectores de expresión en levadura pYES2 y pSAL2, previamente digeridos con las mismas enzimas. Las construcciones obtenidas (pYES-B2 y pSAL-B2) fueron introducidas en la cepa W303-1A de Saccharomyces cerevisiae.
Análisis de las construcciones recombinantes mediante enzimas de restricción: Para dicho análisis los aislamientos de ADN plasmídicos y las manipulaciones del ADN en general se hicieron de acuerdo con protocolos estándar previamente descritos en la literatura (11). Las enzimas de restricción fueron suministradas por Promega, utilizando EcoRI y XbaI en el análisis de las construcciones pYES-B2 y EcoRI para pSAL-B2.
Inducción de la expresión del péptido B2: La inducción de la expresión del péptido B2 clonado en pYES2 fue realizada mediante la sustitución de glucosa por galactosa al 2% en medio selectivo SD-Ura. Para la inducción con la construcción pSAL-B2 fueron añadidos 100 µm de CuSO4 al medio mínimo sintético SD-Leu. Ambos experimentos de inducción fueron conducidos durante toda la noche.
Extracción de las fracciones solubles intracelulares: Las proteínas expresadas intracelularmente fueron extraídas de la manera siguiente: Se colectaron las células luego de la inducción durante toda la noche; el precipitado celular fue lavado con 1 mL de agua destilada estéril. Posteriormente las células fueron resuspendidas en solución amorti-guadora de lisis (HEPES 50 mM, EDTA 3 mM, DTT 1 mM, Polivinilpirrolidona 0,6%, MgCl2 0.1 mM, pH 7.2) y se adicionaron 3 µL del inhibidor de proteasas fluoruro de fenilmetil sulfonilo (PMSF) a 10 mM. La ruptura de las células se realizó con perlas de vidrio con ciclos de 30 segundos en vortex y 30 segundos de reposo en hielo durante 15 min. Por último se adicionaron otros 200 µL de esta solución de lisis y los lisados fueron centrifugados por 15 min a 4 oC a 20 000 g, recuperando el sobrenadante.
Análisis por Western blot: Los extractos proteicos fueron separados mediante SDS/PAGE al 12%, aplicando 40 mg/carril y siguiendo el procedimiento descrito por Laemmli (13). Las bandas de proteínas fueron electrotransferidas a una membrana PVDF (polivinilideno difluoruro) (Immobilon, Millipore Corp.), la que luego fue bloqueada por 1 h a 37 oC en una solución compuesta por PBS1X, BSA1 % (p/v) y 0,05% (v/v) de Tween 20. La membrana con las proteínas transferidas fue incubada durante 1 h con el anticuerpo de ratón anti-His (contra cola de histidina, Roche) conjugado con peroxidasa de rábano picante, a una dilución de 1:1000. Al final de cada uno de estos pasos de incubación se realizaron tres lavados con una solución compuesta por PBS 1X y 0,01% de Tween 20. Seguidamente se incubó la membrana con un sustrato quimioluminiscente denominado luminol, a partir de un estuche de quimioluminiscencia comercial (SuperSignal West Pico Chemiluminescent Substrate kit, Pierce, USA). Por último se expuso la membrana a una película de rayos X y se procedió al revelado para la visualización de la banda B2.
Resultados y Discusión
Análisis de la amplificación por PCR del fragmento que codifica para el péptido B2: En este experimento se
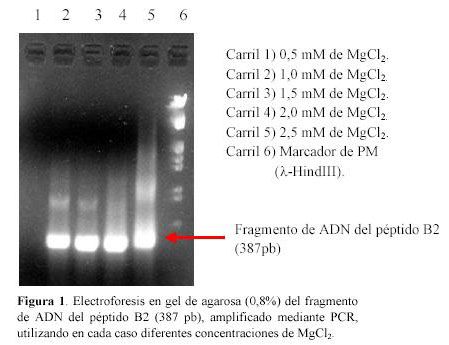
pudo observar la presencia de una banda de 387 pb en todas las condiciones ensayadas que se corresponde con el tamaño esperado del fragmento de ADN de B2. También se observaron bandas inespecíficas, por lo cual se escogieron las condiciones en las que hubo una mayor señal del producto de la amplificación y en las que al mismo tiempo se utilizaron concentraciones menores de MgCl2 (1 mM) (Figura 1).
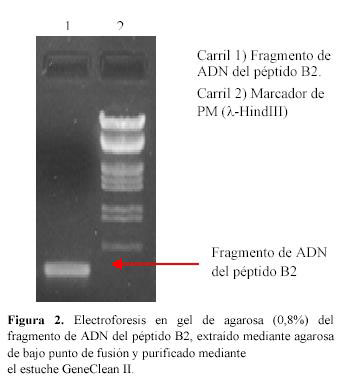
En la Figura 2 se muestra la banda purificada del producto de la amplificación, luego de haber sido separada en agarosa de bajo punto de fusión y purificada por el método comercial Gene Clean II.
Obtención de vectores plasmídicos mediante electroforesis en agarosa de bajo punto de fusión: Los plásmidos de expresión en levadura pYES2 y pSAL2 fueron previamente digeridos con las enzimas de restricción XhoI y SphI y posteriormente extraídos y purificados a partir de geles de agarosa de bajo punto de fusión (dato no mostrado).
Análisis de construcciones recombinantes mediante las enzimas de restricción EcoRI y XbaI: Los clones recombinantes fueron analizados mediante digestión con enzimas de restricción.
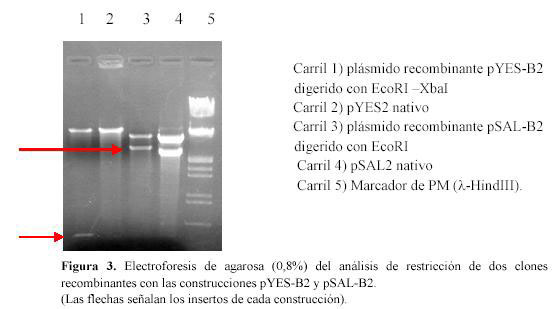
En la Figura 3 se muestra dos de los posibles clones recombinantes después de su purificación por Miniprep y digestión con las respectivas enzimas de restricción. En el caso de la construcción pYES-B2 se observó una banda alrededor de los 387 pb que corresponde al inserto. La presencia del inserto para la construcción pSAL-B2 se pudo comprobar debido al retardo que se produjo en la migración relativa del plásmido recombinante con respecto al plásmido nativo, donde se observó que la banda de talla inferior del plásmido recombinante se encontraba por encima de la banda de talla inferior del plásmido nativo, lo que concuerda con las tallas esperadas para cada caso.
Inmunodetección del péptido B2 recombinante mediante Western blot: La detección de la expresión del péptido B2 fue posible mediante la técnica de Western blot. Sólo se detectó la expresión del mismo cuando se indujo con 100 µM de CuSO4 durante toda la noche, visualizándose una banda a la altura correspondiente al peso molecular calculado para B2 (PM teórico=14.115 kDa) (Figura 4).

En el caso donde se colocaron los extractos proteicos de la cepa control (cepa de Saccharomyces cervisiae con plásmido vacío) no se observó banda alguna. Paralelamente, se realizaron experimentos donde se empleó 1 µM y 10 µM de CuSO4 y 4 h de inducción donde no se detectó señal de expresión. Así mismo, en los experimentos en los que se utilizó la galactosa como inductor tanto a las 4 h como durante toda la noche de inducción tampoco se observó señal alguna de expresión. De ahí que podamos concluir que la construcción pSAL-B2 fue la más eficiente para la expresión del péptido B2 en Saccharomyces cerevisiae al inducir con 100 µM de sulfato de cobre durante toda la noche.
Estos resultados evidencian que es factible la expresión de péptidos sintéticos de M. tuberculosis en la levadura Saccharomyces cerevisiae con el empleo de vectores inducibles con sulfato de cobre. No obstante, se pudieran probar otros vectores y condiciones para optimizar la expresión de este péptido.
Varios elementos fundamentan el uso de esta levadura como sistema alternativo para la expresión de péptidos sintéticos con epitopes de M. tuberculosis. Uno de ellos lo constituye el hecho de que varios autores recurrieran al uso de hospederos tales como baculovirus (14), bacterias filogenéticamente cercanas a las micobacterias como Streptomyces lividans, Corynebacterium spp., y Mycobacterium smegmatis (15), (16), (17) y Pichia pastori (18), entre otros, debido a las dificultades encontradas al tratar de expresar antígenos de M. tuberculosis en E. coli.
Por otro lado, Saccharomyces cerevisiae posee mucha semejanza con los sistemas bacterianos en cuanto a simplicidad en el trabajo de Biología Molecular. Esta levadura aunque es un microorganismo eucariota, se caracteriza por tener pocos requerimientos nutricionales y alta velocidad de crecimiento, por lo que es factible llevarlo a escala industrial con relativo bajo costo de producción. Igualmente, tiene una alta frecuencia de transformación. Sin embargo, a diferencia de muchos sistemas bacterianos como E. coli, esta levadura no forma cuerpos de inclusión y los niveles de endotoxina que produce son prácticamente indetectables, siendo esto último una característica muy importante en el campo de la vacunología (19).
Este trabajo pudiera tener importancia práctica en varios campos de aplicación, así: La obtención de estos péptidos por la vía recombinante pudiera tener potencialmente aplicaciones en el desarrollo de futuros candidatos vacunales, así como en el desarrollo de sistemas de diagnóstico serológicos.
Con la expresión de péptidos de M. tuberculosis en Saccharomyces cerevisiae sería posible explorar el uso de esta levadura como vector vivo no patogénico en vacunas orales contra la tuberculosis. Por otro lado, la obtención de este péptido por vía recombinante permitiría desarrollar diferentes formulaciones vacunales basadas en vacunas de subunidades de naturaleza proteica y además brindaría la posibilidad de abordar diferentes estrategias de inmunización prime-boost heterólogas.
En el campo del diagnóstico se ha reportado en la literatura que las pruebas serológicas de infectados por el bacilo de la tuberculosis en las que se emplea un solo antígeno, no son muy efectivas considerando que la respuesta de anticuerpos es muy heterogénea (20). Por lo cual se ha sugerido para estas pruebas el uso de mezclas de antígenos, acercándose aún más a lo que ocurre naturalmente (21). El péptido B2 al estar constituido por varios epitopes de diferentes antígenos inmunodominantes de M. tuberculosis pudiera ser un buen candidato para resolver estos problemas.
Referencias
1. World Health Organization. Global tuberculosis control: surveillance, planning, financing. Geneva; 2007 (WHO/HTM/TB/2007.376).
2. .Dye C, Scheele S, Dolin P, Pathania V and Raviglione MC. Consensus statement. Global burden of tuberculosis: estimated incidence, prevalence, and mortality by country. WHO Global Surveillance and Monitoring Project. J. Am. Med. Ass.1999; 282:677.
3. .Crispen R. History of BCG and its substrains. Prog. Clin. Biol. Res.1989; 310:35.
4. Orme IM. Beyond BCG: the potential for a more effective TB vaccine. Mol. Med. Today 1999; 5:487.
5. Mohd-Nor N, Sarmiento ME and Acosta. Recent Advances in Tuberculosis Vaccine Development. Current Respiratory Medicine Reviews 2005; 1(2): 109-116.
6. Valenzuela P, Medina A, Rutter WJ, Ammerer G & Hall BD. Synthesis and assembly of hepatitis B virus surface antigen particles in yeast. Nature 1982; 298: 347-350.
7. Razanskien A, Schmidt J, Geldmacher A, Ritzi A, Niedrig M, Lundkvis A et al. High yields of stable and highly pure nucleocapsid proteins of different hantaviruses can be generated in the yeast Saccharomyces cerevisiae. J. Biotechnol. 2004; 111: 319-333.
8. Schreuder MP, Deen C, Boersma WJA, Pouwels PH and Klis FM. Yeast expressing hepattis B virus surface antigen determinants on its surface: implications for a posible oral vaccine. Vaccine. 1996; 14: 383- 388.
9. Olivares N, León A, López Y, Puig A, Cádiz A, Falero G et al. The effect of the administration of human gamma globulins in a model of BCG infection in mice. Tuberculosis. 2006; 86(3- 4): 268-272.
10. Reljic R, Clark SO, Willians A, Falero- Diaz G, Singh M, Challacombe S et al. Intranasal IFN? extends passive IgA antibody protection of mice against Mycobacterium tuberculosis lung infection. Clinical & Experimental Immunology 2006; 143 (3): 467- 473.
11. Sambrook J, Fritsh EF, Maniatis T Molecular Cloning: a Laboratory Manual. In: Ford N, Nolan C, Ferguson M, editors. New York: Cold Spring Harbor Laboratory Press; 1989.
12. Ito H, Fulkuda Y, Murata K, and Kimura A. Transformation of intact yeast cells treated with alkali cations. J. Bacteriol. 1983; 153:163-168.
13. Laemmli UK. Cleavage of structural proteins during the assembly of the head of bacteriophage T4. Nature. 1970 Aug 15;227(5259):680–685.
14. Atkins D, al-Ghusein C, Prehaund C, and Coates AR. Overproduction and purification of Mycobacterium tuberculosis chaperonin 10. Gene 1994; 150: 145-148.
15. Harth G, Lee BY, and Horwitz MA. High-level heterologous expression and secretion in rapidly growing nonpathogenic mycobacteria of four major Mycobacterium tuberculosis extracellular proteins considered to be leading vaccine candidates and drug targets. Infect. Immun. 1997; 65:2321–2328.
16. Menéndez MC, Domenech P, Prieto J, and Garcia MJ. Cloning and expression of the Mycobacterium fortuitum superoxide dismutase gene. FEMS Microbiol. Lett. 1995;134: 273–278.
17. Zhang Y, Lathigra R, GarbeT, Catty D, and Young D. Genetic analysis of superoxide dismutase, the 23 kilodalton antigen of Mycobacterium tuberculosis. Mol. Microbiol. 1991; 5:381–391.
18. Benabdesselem C, Barbouche MR, Jarboui MA, Dellagi K, Ho JL, Fathallah DM. High Level Expression of Recombinant Mycobacterium tuberculosis Culture Filtrate Protein CFP32 in Pichia pastoris. Molecular Biotechnology. January 2007; 35(1): 41-50.
19. Rogan D, Babiuk LA. Novel vaccines from biotechnology. Rev. sci. tech. Off. int. Epiz. 2005; 24 (1): 159-174.
20. Gennaro ML. Immunologic diagnosis of tuberculosis. Clin Infect Dis. 2000; Suppl. 3: S243–S246.
21. Lyashchenko KP, Singh M, Colangeli R, Gennaro ML. A multi-antigen print immunoassay for the development of serological diagnosis of infectious diseases. J Immunol Methods 2000; 28:91–100.
Heterologous expression of a B-cell multiepitopic peptide from M. tuberculosis in Saccharomyces cerevisiae
Abtract
Saccharomyces cerevisiae has been widely used as expression system of heterologous proteins. The aim of the present work was the expression in Saccharomyces cerevisiae of a class B multiepitopic peptide from M. tuberculosis. For this purpose, the chimerical peptide named B2 was cloned in two yeast expression vectors containing galactose and cupric sulphate regulated promoters, respectively. After induction experiments, B2 expression was analyzed by SDS/PAGE and Western Blot. By Western Blot analysis B2 expression was confirmed when induction took place overnight with 100 mM of CuSO4. No expression signal took place when galactose was used as inductor. These results show that Sacchromyces cervisiae could be a good alternative host for the expression of multiepitopic peptides from M. tuberculosis.
Keywords: Saccharomyces cerevisiae, tuberculosis, vaccine, expression, antigen.
Recibido: Junio de 2007 Aprobado: Agosto de 2007